著名医師による解説が無料で読めます
すると翻訳の精度が向上します
動機:RNA二次構造分析では、多くの場合、大きなシーケンスデータで潜在的なヘリックスを検索する必要があります。 結果:RNAベースペアリングルールの下で潜在的ならせん領域を効率的に特定するユーティリティプログラムのGuugleを提示します。正と負のシーケンスのセットを受け入れ、指定された長さを超える正と負のシーケンスの間のRNAルールの下でのすべての正確な一致を決定します。Guaugleアルゴリズムは、正のシーケンスセットの事前計算された接尾辞アレイを使用するように適合させることもできます。このプログラムは、miRNAターゲット予測など、より計算上の高価なタスクに先行するフィルターとして効果的に使用する方法を示します。 可用性:Guugleは、http://bibiserv.techfak.uni-bielefeld.de/guugleのBielefeld Bioinformatics Serverから入手できます。
動機:RNA二次構造分析では、多くの場合、大きなシーケンスデータで潜在的なヘリックスを検索する必要があります。 結果:RNAベースペアリングルールの下で潜在的ならせん領域を効率的に特定するユーティリティプログラムのGuugleを提示します。正と負のシーケンスのセットを受け入れ、指定された長さを超える正と負のシーケンスの間のRNAルールの下でのすべての正確な一致を決定します。Guaugleアルゴリズムは、正のシーケンスセットの事前計算された接尾辞アレイを使用するように適合させることもできます。このプログラムは、miRNAターゲット予測など、より計算上の高価なタスクに先行するフィルターとして効果的に使用する方法を示します。 可用性:Guugleは、http://bibiserv.techfak.uni-bielefeld.de/guugleのBielefeld Bioinformatics Serverから入手できます。
MOTIVATION: RNA secondary structure analysis often requires searching for potential helices in large sequence data. RESULTS: We present a utility program GUUGle that efficiently locates potential helical regions under RNA base pairing rules, which include Watson-Crick as well as G-U pairs. It accepts a positive and a negative set of sequences, and determines all exact matches under RNA rules between positive and negative sequences that exceed a specified length. The GUUGle algorithm can also be adapted to use a precomputed suffix array of the positive sequence set. We show how this program can be effectively used as a filter preceding a more computationally expensive task such as miRNA target prediction. AVAILABILITY: GUUGle is available via the Bielefeld Bioinformatics Server at http://bibiserv.techfak.uni-bielefeld.de/guugle
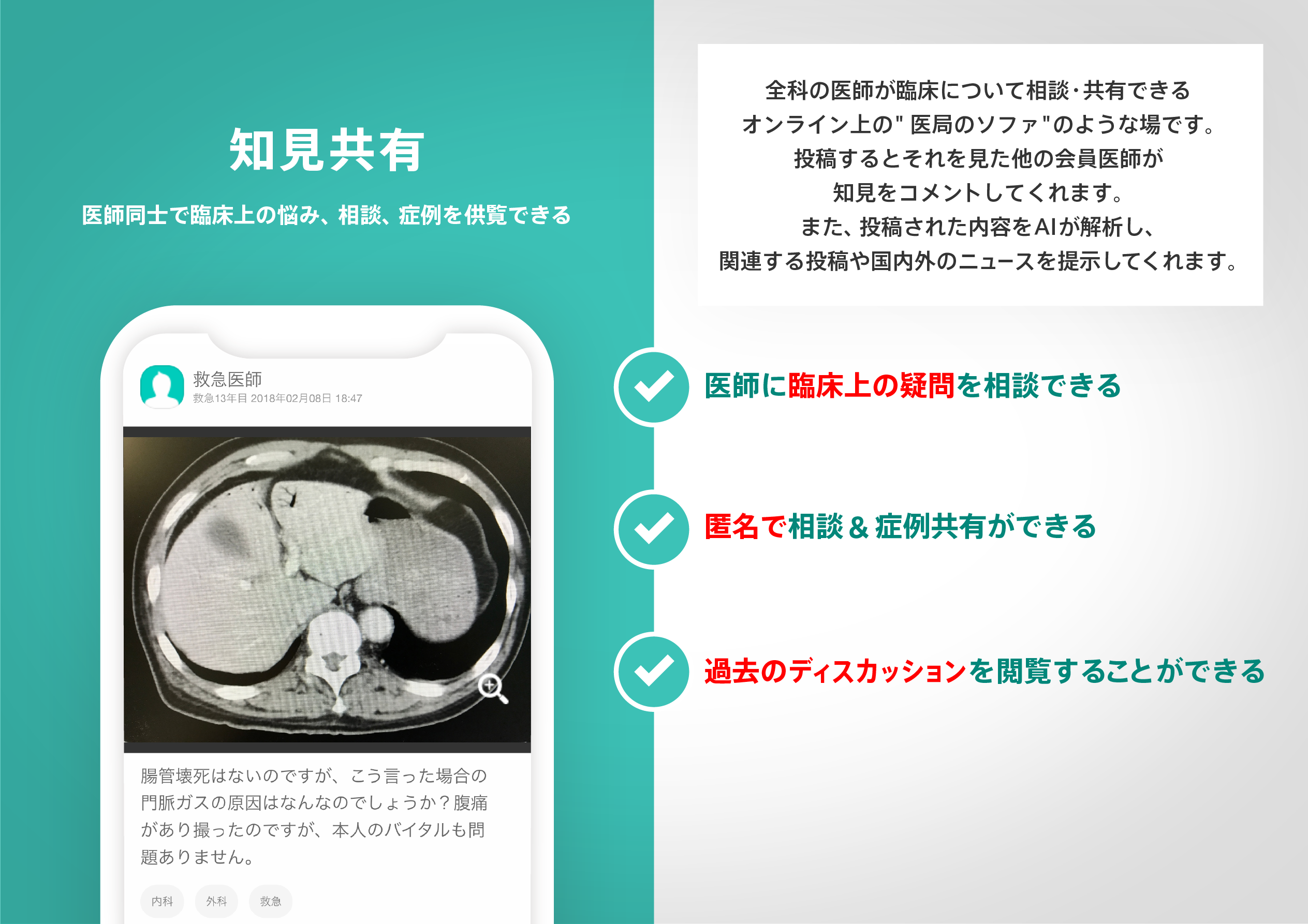
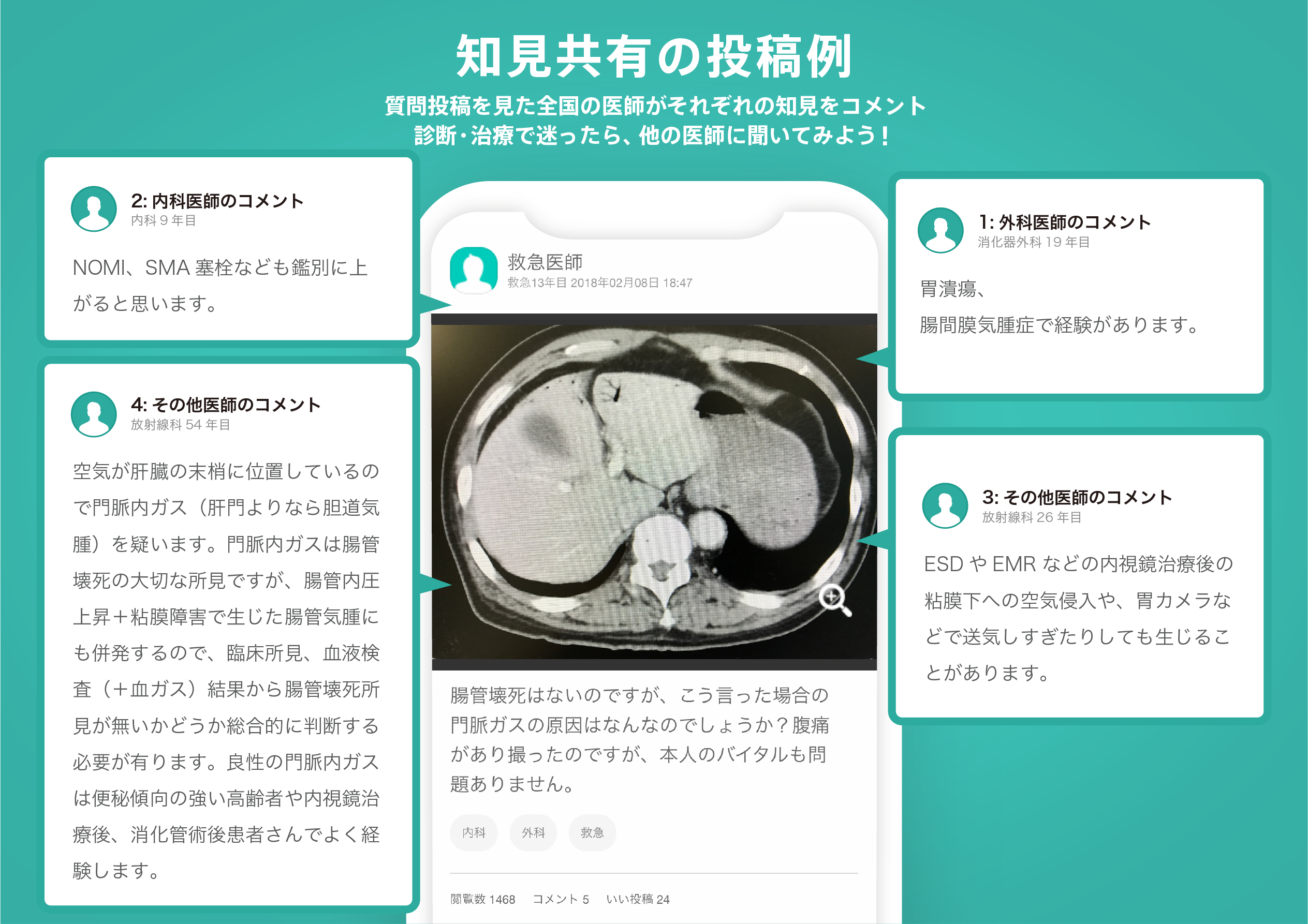
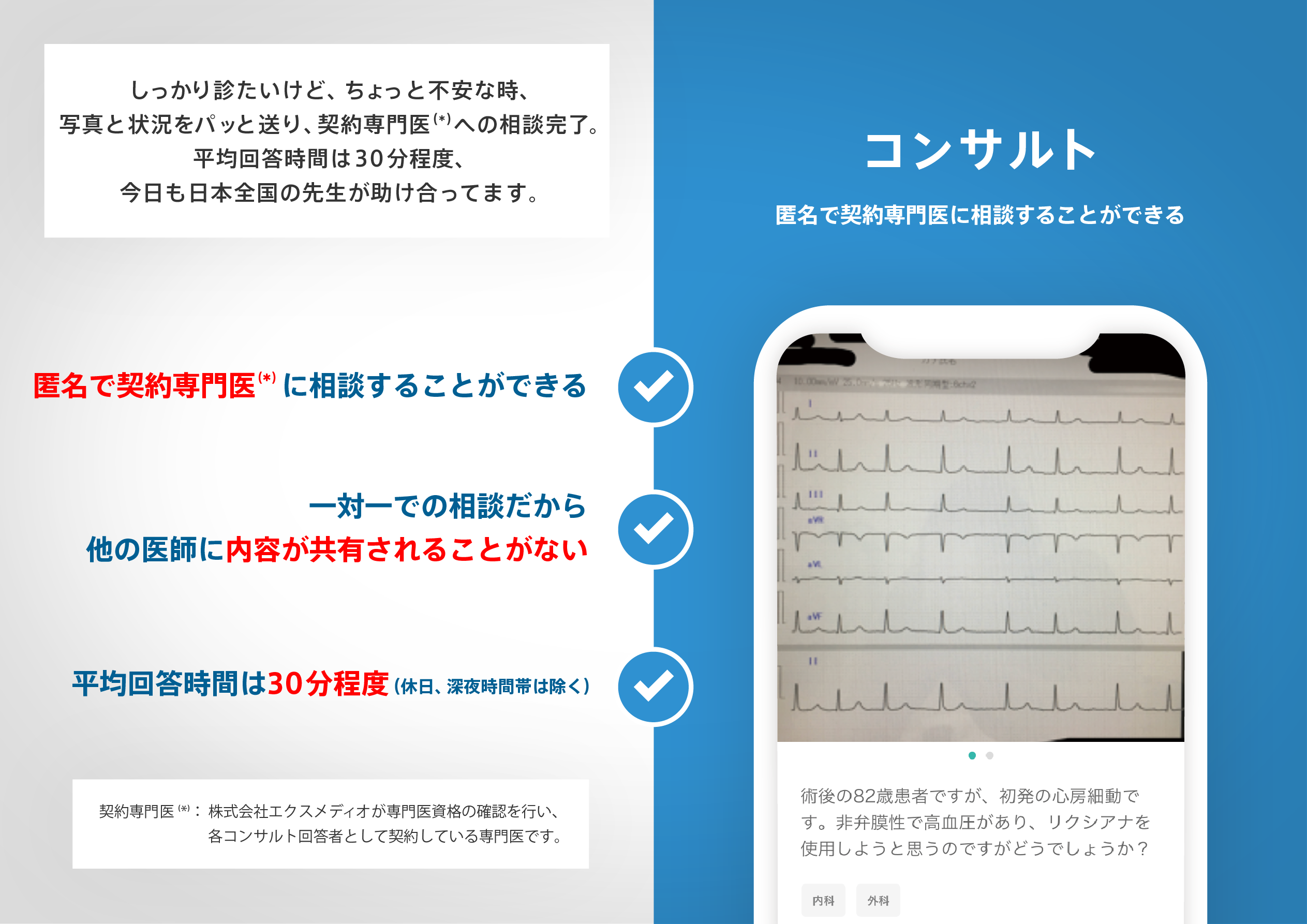
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。