著名医師による解説が無料で読めます
すると翻訳の精度が向上します
DNAはいくつかのタンパク質や薬物の非常に重要な標的であるにもかかわらず、核酸を伴う分子動力学シミュレーションには、選択された力場の信頼性など、多くの課題が依然として含まれています。この論文では、Gromos 53A6とAmber 03 Forceフィールドを比較したDickerson-Drew Dodecamerの分子動力学シミュレーションを実施しました。Amber Forceフィールドは5 'および3'末端ヌクレオチドの特定のトポロジを示しますが、Gromos Forceフィールドはすべてのヌクレオチドを同じ方法で考慮します。末端ヌクレオチド定義の効果を調査するために、両方の力場を修正して、特定の末端ヌクレオチドトポロジーの有無にかかわらず、2つの可能な方法で適用されました。グローバルな安定性(RMSD、塩基対の数、水素結合の数)の分析は、Amberでシミュレートされた両方のシステムが安定していることを示しましたが、元のGromosトポロジーでシミュレートされたシステムは5 ns後に非常に不安定でした。Gromos Forceフィールドに特定の末端トポロジーが含まれている場合、DNAの変性は15 nsまで遅延しましたが、回避されませんでした。アルファ/ガンマの遷移は、力場に強い依存性を示しましたが、末端ヌクレオチド定義にはそうではありませんでした:Amberシミュレーションは主にグローバルな最小値に対応する構成を調査しましたが、Gromosシミュレーションはシミュレーションの非常に早い段階で、ローカルの広範なサンプリングを示しました。A-DNAアイソフォームへの遷移を容易にする可能性のある最小値。Epsilon/Zetaサンプリングは、力場と末端ヌクレオチド定義の両方に依存していました。Mberシミュレーションは明確に定義されたB-I-> B-II遷移を示しましたが、Gromos ForceフィールドはB-I立体構造を明らかに支持しました。また、元のGromosトポロジーでシミュレートされたシステムは、非結合されたエプシロン/ゼータ遷移を表示し、非癌の立体構造につながりましたが、これは新しい末端ヌクレオチドトポロジーが適用されたときに戻りました。最後に、Gromos Forceフィールドは、DNAの強い幾何学的変形(過大評価された溝の幅とロール、および強く過小評価されたねじれとスライド)につながり、これにより、さらなるリパラメーター化が行われない限り、長時間スケールDNAシミュレーションでのGromos Forceフィールドの使用が制限されます。
DNAはいくつかのタンパク質や薬物の非常に重要な標的であるにもかかわらず、核酸を伴う分子動力学シミュレーションには、選択された力場の信頼性など、多くの課題が依然として含まれています。この論文では、Gromos 53A6とAmber 03 Forceフィールドを比較したDickerson-Drew Dodecamerの分子動力学シミュレーションを実施しました。Amber Forceフィールドは5 'および3'末端ヌクレオチドの特定のトポロジを示しますが、Gromos Forceフィールドはすべてのヌクレオチドを同じ方法で考慮します。末端ヌクレオチド定義の効果を調査するために、両方の力場を修正して、特定の末端ヌクレオチドトポロジーの有無にかかわらず、2つの可能な方法で適用されました。グローバルな安定性(RMSD、塩基対の数、水素結合の数)の分析は、Amberでシミュレートされた両方のシステムが安定していることを示しましたが、元のGromosトポロジーでシミュレートされたシステムは5 ns後に非常に不安定でした。Gromos Forceフィールドに特定の末端トポロジーが含まれている場合、DNAの変性は15 nsまで遅延しましたが、回避されませんでした。アルファ/ガンマの遷移は、力場に強い依存性を示しましたが、末端ヌクレオチド定義にはそうではありませんでした:Amberシミュレーションは主にグローバルな最小値に対応する構成を調査しましたが、Gromosシミュレーションはシミュレーションの非常に早い段階で、ローカルの広範なサンプリングを示しました。A-DNAアイソフォームへの遷移を容易にする可能性のある最小値。Epsilon/Zetaサンプリングは、力場と末端ヌクレオチド定義の両方に依存していました。Mberシミュレーションは明確に定義されたB-I-> B-II遷移を示しましたが、Gromos ForceフィールドはB-I立体構造を明らかに支持しました。また、元のGromosトポロジーでシミュレートされたシステムは、非結合されたエプシロン/ゼータ遷移を表示し、非癌の立体構造につながりましたが、これは新しい末端ヌクレオチドトポロジーが適用されたときに戻りました。最後に、Gromos Forceフィールドは、DNAの強い幾何学的変形(過大評価された溝の幅とロール、および強く過小評価されたねじれとスライド)につながり、これにより、さらなるリパラメーター化が行われない限り、長時間スケールDNAシミュレーションでのGromos Forceフィールドの使用が制限されます。
Despite DNA being a very important target for several proteins and drugs, molecular dynamics simulations with nucleic acids still encompass many challenges, such as the reliability of the chosen force field. In this paper, we carried out molecular dynamics simulations of the Dickerson-Drew dodecamer comparing GROMOS 53A6 and AMBER 03 force fields. While the AMBER force field presents specific topologies for the 5' and 3' terminal nucleotides, the GROMOS force field considers all nucleotides in the same way. To investigate the effects of the terminal nucleotide definitions, both force fields were modified to be applied in the two possible ways: with or without specific terminal nucleotide topologies. The analysis of global stability (rmsd, number of base pairs and hydrogen bonds) showed that both systems simulated with AMBER were stable, while the system simulated with the original GROMOS topologies was very unstable after 5 ns. When specific terminal topologies were included for GROMOS force field, DNA denaturation was delayed until 15 ns, but not avoided. The alpha/gamma transitions also displayed a strong dependence on the force field, but not on the terminal nucleotide definitions: AMBER simulations mainly explored configurations corresponding to the global minimum, while GROMOS simulations exhibited, very early in the simulations, an extensive sampling of local minima that may facilitate transitions to A-DNA isoform. The epsilon/zeta sampling was dependent both on the force field and on the terminal nucleotide definitions: while the AMBER simulations displayed well-defined B-I --> B-II transitions, the GROMOS force field clearly favored the B-I conformation. Also, the system simulated with the original GROMOS topologies displayed uncoupled epsilon/zeta transitions, leading to noncanonical conformations, but this was reverted when the new terminal nucleotide topologies were applied. Finally, the GROMOS force field leads to strong geometrical deformations on the DNA (overestimated groove widths and roll and strongly underestimated twist and slide), which restrict the use of GROMOS force field in long time scale DNA simulations unless a further reparametrization is made.
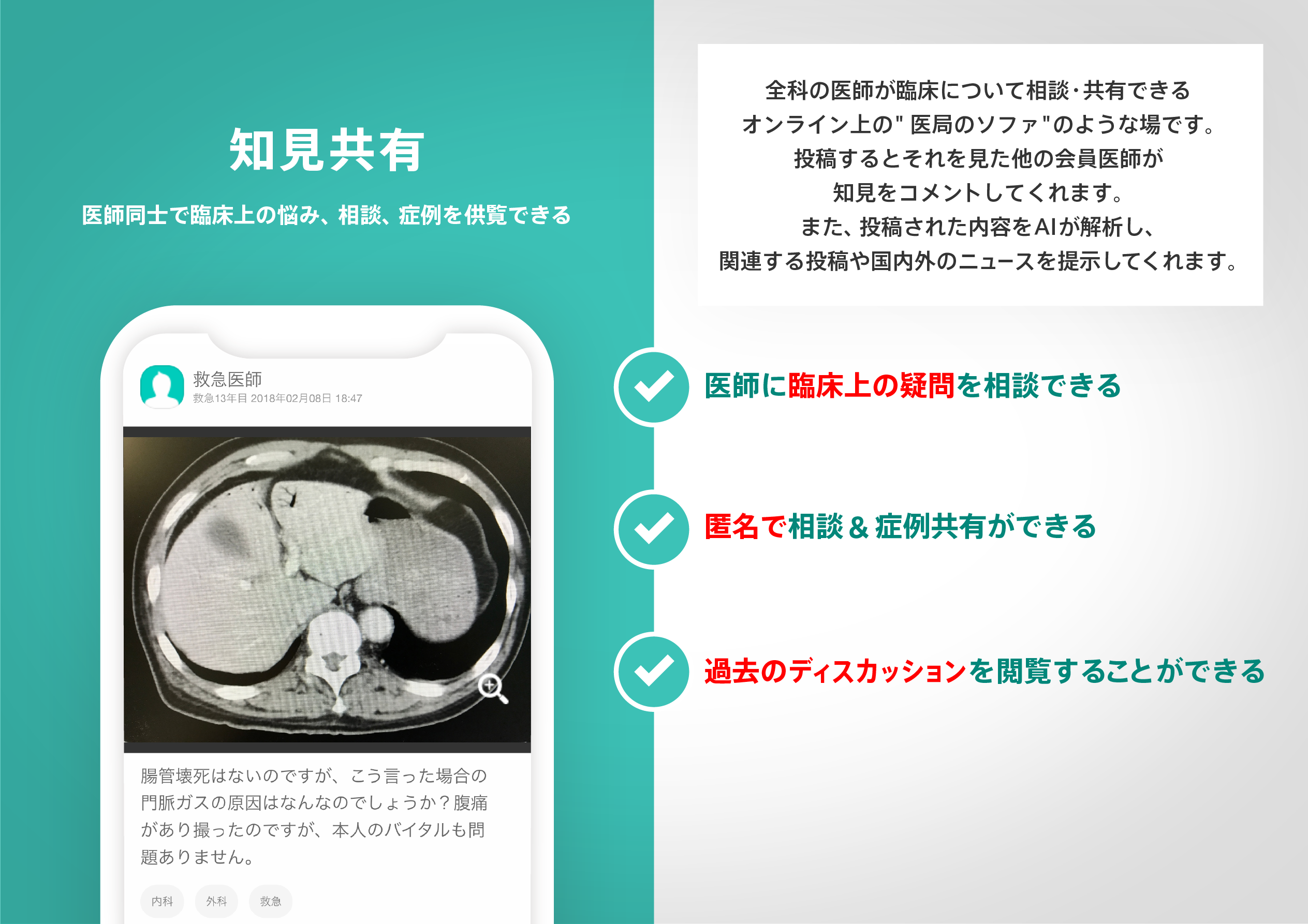
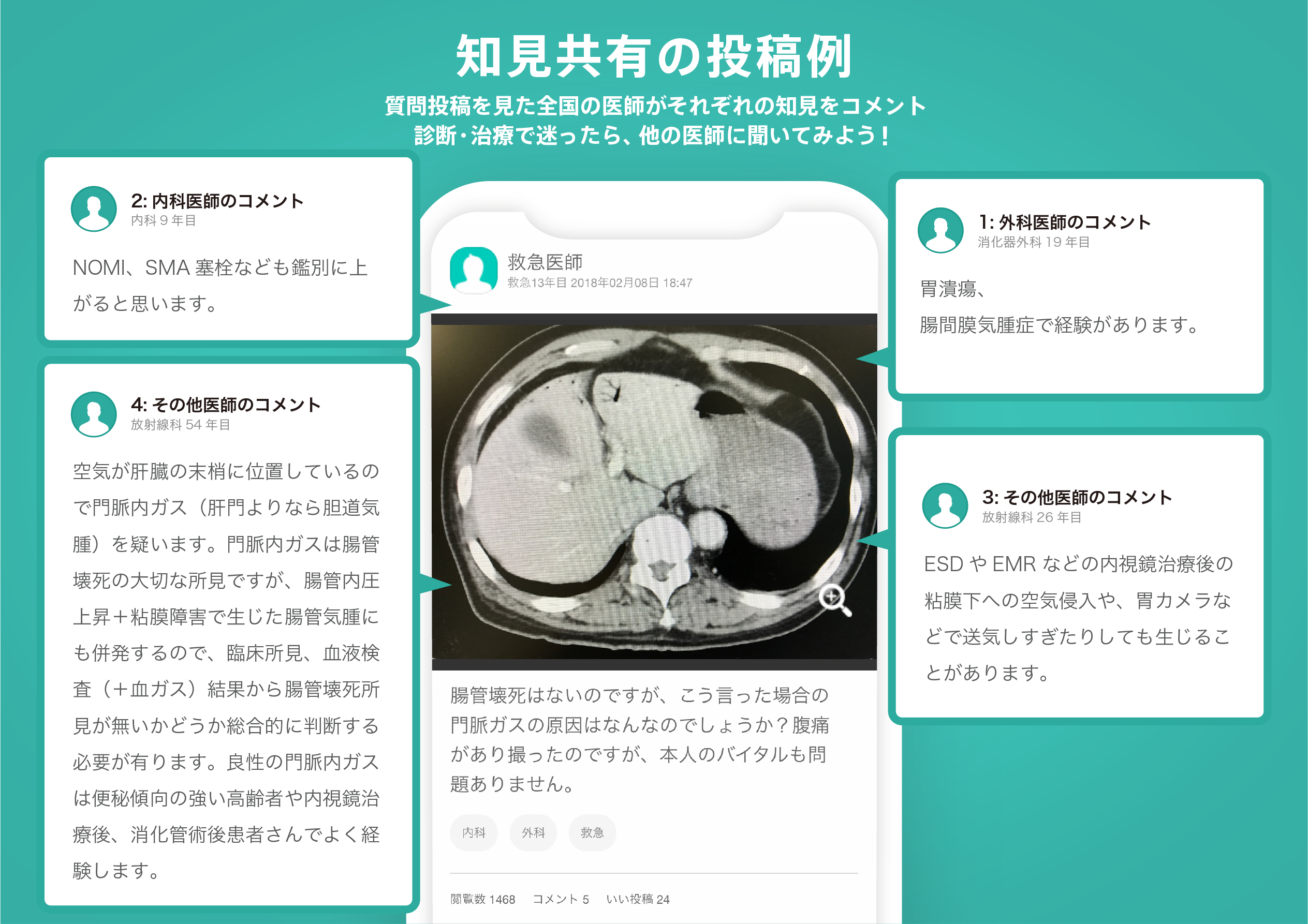
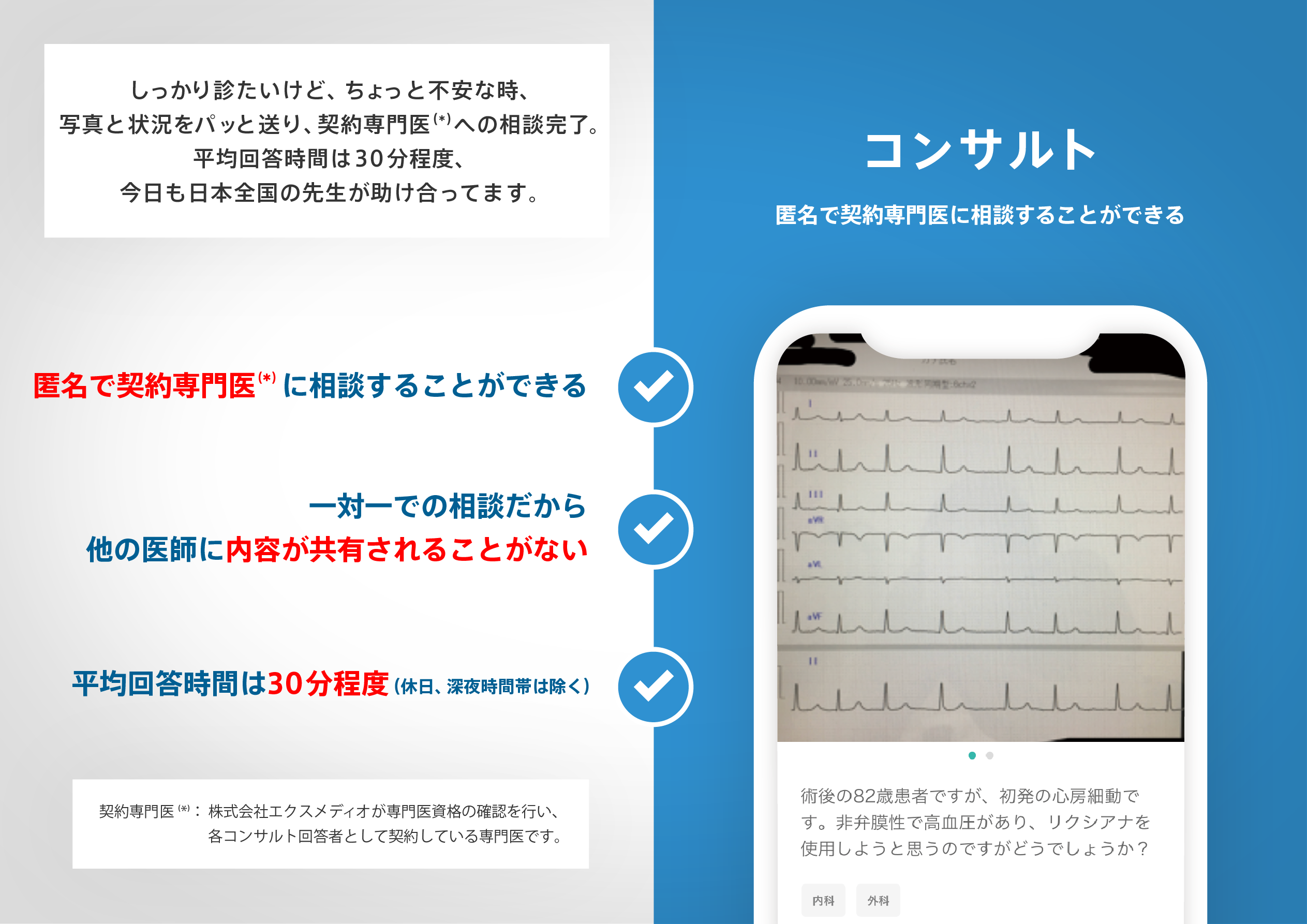
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。