著名医師による解説が無料で読めます
すると翻訳の精度が向上します
背景:ほとんどのゲノムの高い部分を組み合わせたタンデムDNAリピートの機能的および形態学的研究は、これらのゲノム要素の不完全な特性評価により、ほとんど制限されています。ここでは、マウスゲノムアセンブリにある大きなタンデムリピート(TR)のゲノムワイド分析を報告します。 結果:バイオインフォマティクスアプローチを使用して、2つのマウス全ゲノムショットガン(WGS)アセンブリで3 kb以上のアレイサイズの大きなTRを特定しました。大きなTRは、配列の類似性、染色体位置、モノマーの長さ、アレイの変動性、およびGC含有量に基づいて分類されました。4つのスーパーファミリー、8つの家族、および62のサブファミリーを特定しました。1)cantomeric微小衛星のスーパーファミリーは、参照ゲノムの組み立てられていない部分にのみ見られます。2)周腹部の主要な衛星は、最も豊富なスーパーファミリーであり、高次の繰り返し構造を明らかにしています。3)関連するスーパーファミリーに関連する転位要素には、2つの家族が含まれています。4)異種のタンデムリピートのスーパーファミリーには、4つの家族が含まれます。1つのファミリはWGSでのみ見つかりますが、2つのファミリは、単一または多軌道の場所でタンデムリピートを表しています。多軌道の位置にもかかわらず、TRPC-21A-MMは、その豊富な、厳密に侵害中心的な位置、および大きな人間の衛星と類似しているため、分離されたファミリーに配置されます。データを確認するために、次に、異なるファミリからの3つの繰り返しでその場でのハイブリダイゼーションを実行しました。TRPC-21A-MMプローブ染色体3および17にハイブリダイズし、10個の染色体にハイブリダイズされた多軌道TR-22a-MMプローブ、および染色体の端から出現する長いループとハイブリダイズした単一遺伝子座TR-54B-MMプローブ。In in Silicoに加えて、いくつかのエクストラ染色体がTRによる現場分析に対して陽性であると予測し、潜在的に不正確なゲノムアセンブリを異系複合ゲノム領域のアセンブリを示しています。 結論:マウスについては染色体特異的TRが予測されていましたが、以前に信頼できる細胞遺伝学的プローブは入手できませんでした。シリコで特定され、その場3/17染色体特異的プローブTRPC-21-MMを確認した新しい分析を報告します。したがって、新しい分類はゲノム研究の継続に有用なツールであることが証明されていましたが、注釈付きTRは染色体認識のための細胞遺伝学的プローブの貴重なソースになります。
背景:ほとんどのゲノムの高い部分を組み合わせたタンデムDNAリピートの機能的および形態学的研究は、これらのゲノム要素の不完全な特性評価により、ほとんど制限されています。ここでは、マウスゲノムアセンブリにある大きなタンデムリピート(TR)のゲノムワイド分析を報告します。 結果:バイオインフォマティクスアプローチを使用して、2つのマウス全ゲノムショットガン(WGS)アセンブリで3 kb以上のアレイサイズの大きなTRを特定しました。大きなTRは、配列の類似性、染色体位置、モノマーの長さ、アレイの変動性、およびGC含有量に基づいて分類されました。4つのスーパーファミリー、8つの家族、および62のサブファミリーを特定しました。1)cantomeric微小衛星のスーパーファミリーは、参照ゲノムの組み立てられていない部分にのみ見られます。2)周腹部の主要な衛星は、最も豊富なスーパーファミリーであり、高次の繰り返し構造を明らかにしています。3)関連するスーパーファミリーに関連する転位要素には、2つの家族が含まれています。4)異種のタンデムリピートのスーパーファミリーには、4つの家族が含まれます。1つのファミリはWGSでのみ見つかりますが、2つのファミリは、単一または多軌道の場所でタンデムリピートを表しています。多軌道の位置にもかかわらず、TRPC-21A-MMは、その豊富な、厳密に侵害中心的な位置、および大きな人間の衛星と類似しているため、分離されたファミリーに配置されます。データを確認するために、次に、異なるファミリからの3つの繰り返しでその場でのハイブリダイゼーションを実行しました。TRPC-21A-MMプローブ染色体3および17にハイブリダイズし、10個の染色体にハイブリダイズされた多軌道TR-22a-MMプローブ、および染色体の端から出現する長いループとハイブリダイズした単一遺伝子座TR-54B-MMプローブ。In in Silicoに加えて、いくつかのエクストラ染色体がTRによる現場分析に対して陽性であると予測し、潜在的に不正確なゲノムアセンブリを異系複合ゲノム領域のアセンブリを示しています。 結論:マウスについては染色体特異的TRが予測されていましたが、以前に信頼できる細胞遺伝学的プローブは入手できませんでした。シリコで特定され、その場3/17染色体特異的プローブTRPC-21-MMを確認した新しい分析を報告します。したがって、新しい分類はゲノム研究の継続に有用なツールであることが証明されていましたが、注釈付きTRは染色体認識のための細胞遺伝学的プローブの貴重なソースになります。
BACKGROUND: Functional and morphological studies of tandem DNA repeats, that combine high portion of most genomes, are mostly limited due to the incomplete characterization of these genome elements. We report here a genome wide analysis of the large tandem repeats (TR) found in the mouse genome assemblies. RESULTS: Using a bioinformatics approach, we identified large TR with array size more than 3 kb in two mouse whole genome shotgun (WGS) assemblies. Large TR were classified based on sequence similarity, chromosome position, monomer length, array variability, and GC content; we identified four superfamilies, eight families, and 62 subfamilies - including 60 not previously described. 1) The superfamily of centromeric minor satellite is only found in the unassembled part of the reference genome. 2) The pericentromeric major satellite is the most abundant superfamily and reveals high order repeat structure. 3) Transposable elements related superfamily contains two families. 4) The superfamily of heterogeneous tandem repeats includes four families. One family is found only in the WGS, while two families represent tandem repeats with either single or multi locus location. Despite multi locus location, TRPC-21A-MM is placed into a separated family due to its abundance, strictly pericentromeric location, and resemblance to big human satellites. To confirm our data, we next performed in situ hybridization with three repeats from distinct families. TRPC-21A-MM probe hybridized to chromosomes 3 and 17, multi locus TR-22A-MM probe hybridized to ten chromosomes, and single locus TR-54B-MM probe hybridized with the long loops that emerge from chromosome ends. In addition to in silico predicted several extra-chromosomes were positive for TR by in situ analysis, potentially indicating inaccurate genome assembly of the heterochromatic genome regions. CONCLUSIONS: Chromosome-specific TR had been predicted for mouse but no reliable cytogenetic probes were available before. We report new analysis that identified in silico and confirmed in situ 3/17 chromosome-specific probe TRPC-21-MM. Thus, the new classification had proven to be useful tool for continuation of genome study, while annotated TR can be the valuable source of cytogenetic probes for chromosome recognition.
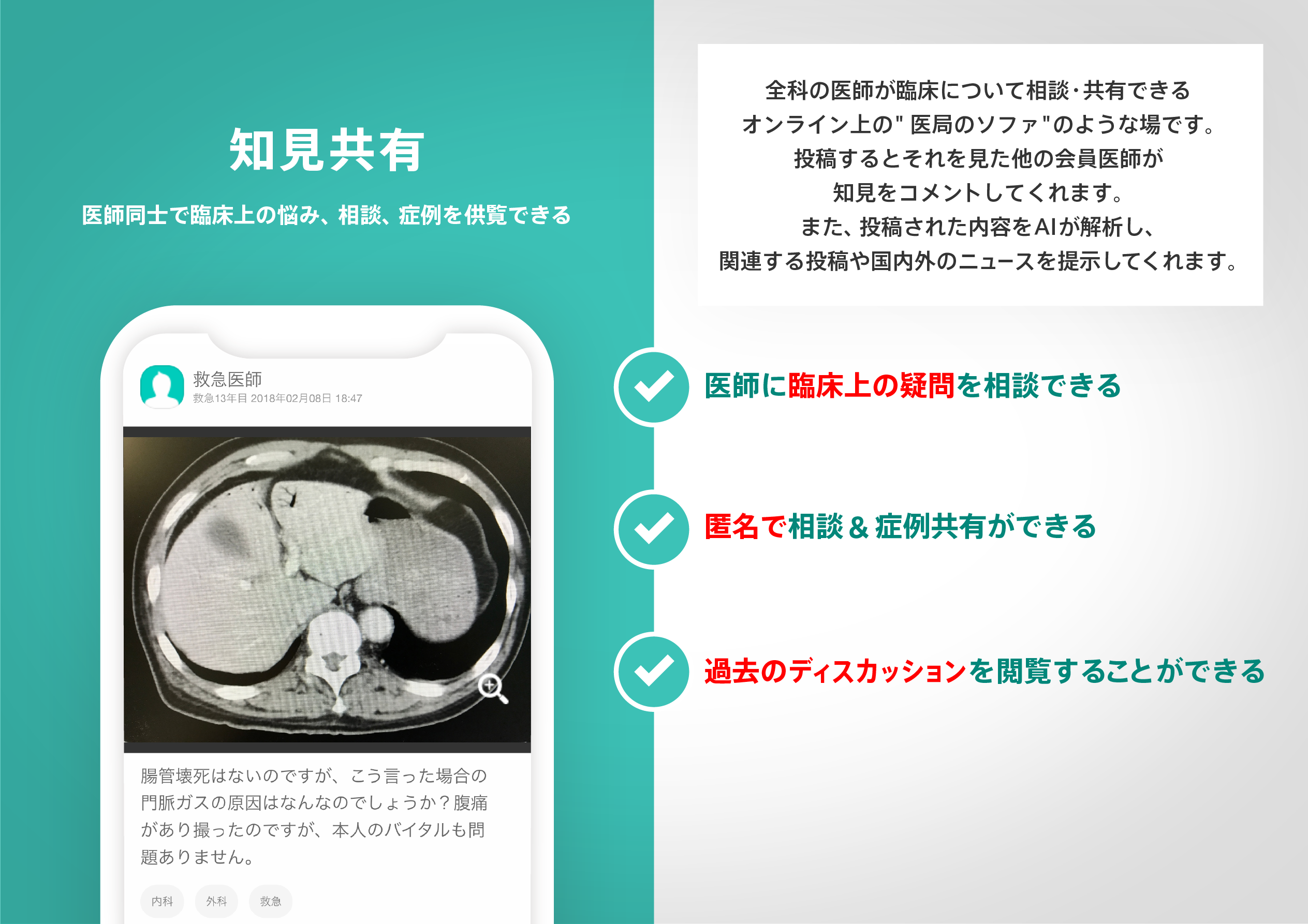
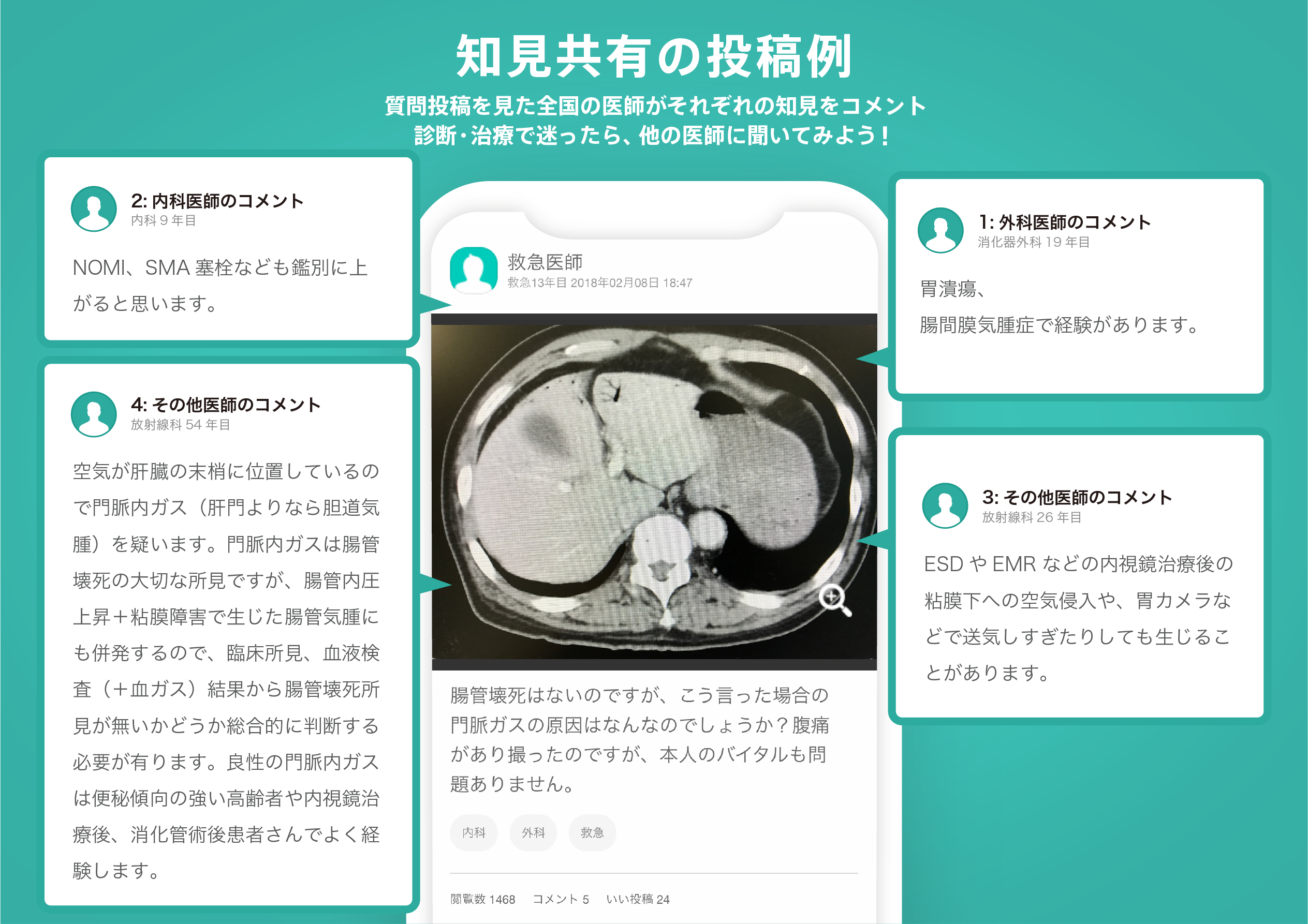
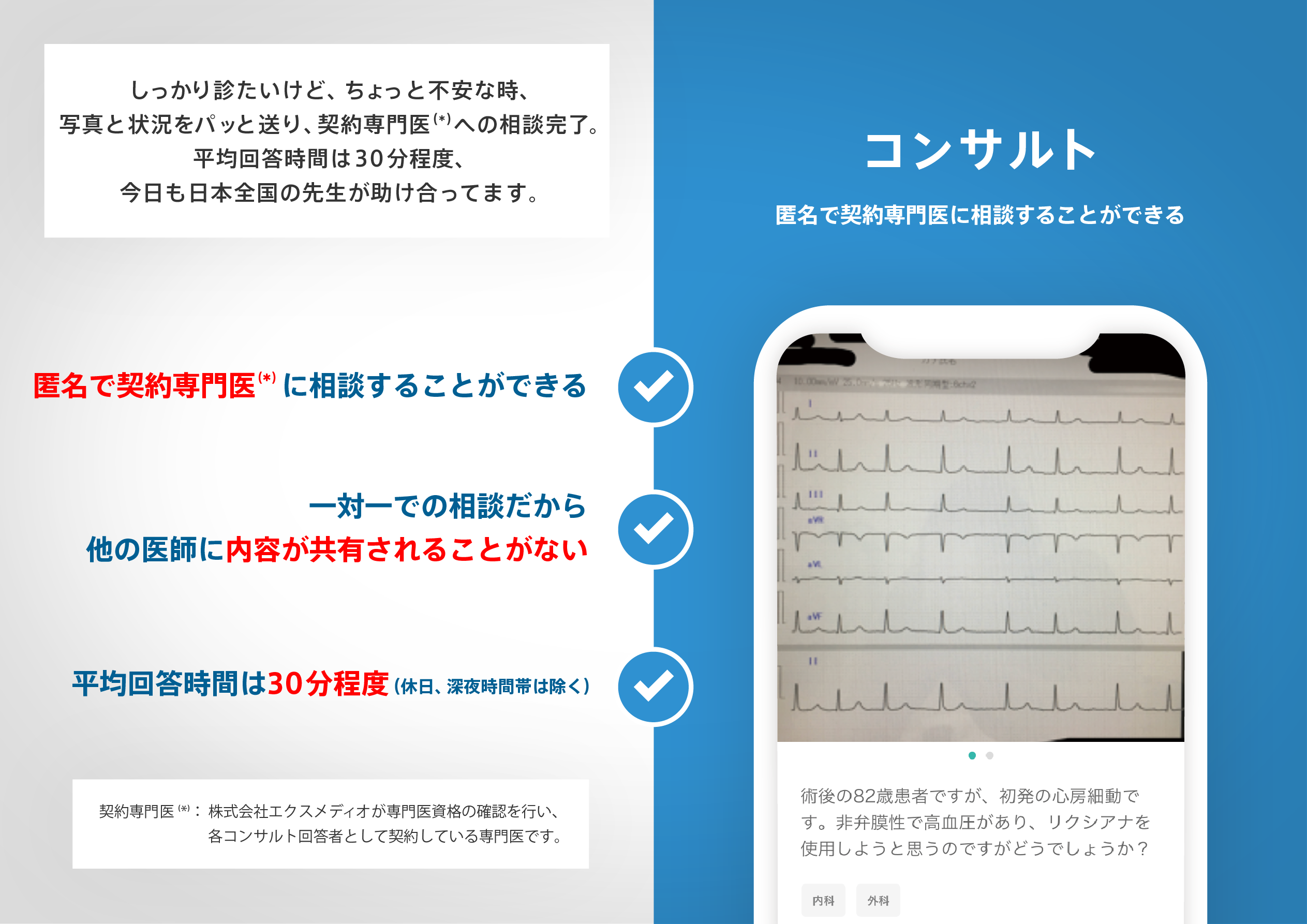
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。