著名医師による解説が無料で読めます
すると翻訳の精度が向上します
脂肪アシルエロンガーゼ5(ELOVL5)は、18炭素脂肪酸からの生理学的に必須の長鎖ポリン飽和脂肪酸(LC-PUFA)、ドコサヘキセン酸(DHA)、エイコサペンテノ酸(EPA)を生成する脊椎動物の生合成経路の重要な酵素です。前駆体。他のほとんどの脊椎動物とは対照的に、アトランティックサーモンは、サルモン系系統の基部で発生した全ゲノム重複(WGD)の結果として、ELOVL5(ELOVL5AおよびELOVL5B)の2つのコピーを所有しています。WGDは、脊椎動物の進化に大きな影響を与え、余分な遺伝物質を提供し、適応と種分化を加速するための新機能化を可能にしました。しかし、そのような複製された家族遺伝子が分岐するメカニズムについてはほとんど知られていない。ここでは、ホメロログの大西洋サーモンELOVL5AおよびELOVL5B遺伝子がトランスポゾン様要素によって非対称的に定着していることを示しています。同一の位置と挿入のアイデンティティは、虹色のトラウトの重複ELOVL5遺伝子にも存在しますが、最も近い現存する代表的な事前に重複する伸縮式ぼうであるノーザンパイクにはありません。ELOVL5サーモンの両方の重複は、SREBP1依存性転写とSREBP2依存性転写を促進する保存された調節要素を所有しており、プロモーター間のSREBP応答の大きさの違いは、ELOVL5BのSREおよびNF-Y補因子結合部位のタンデム重複に起因する可能性があります。さらに、ELOVL5Aのプロモーター領域への挿入は、LXR/RXR転写活性化に対する応答性を付与します。我々の結果は、すべてではない、すべてではないほとんどの場合、ELOVL5遺伝子へのトランスポゾンの動員は、パイクとサーモンの共通の祖先からの分割後に発生したが、より最近のサケ科の具体化の前に発生したこと、およびELOVL5調節領域の発散が発現することにより新生生物化を可能にしたことを示しています。これらの家族の遺伝子。
脂肪アシルエロンガーゼ5(ELOVL5)は、18炭素脂肪酸からの生理学的に必須の長鎖ポリン飽和脂肪酸(LC-PUFA)、ドコサヘキセン酸(DHA)、エイコサペンテノ酸(EPA)を生成する脊椎動物の生合成経路の重要な酵素です。前駆体。他のほとんどの脊椎動物とは対照的に、アトランティックサーモンは、サルモン系系統の基部で発生した全ゲノム重複(WGD)の結果として、ELOVL5(ELOVL5AおよびELOVL5B)の2つのコピーを所有しています。WGDは、脊椎動物の進化に大きな影響を与え、余分な遺伝物質を提供し、適応と種分化を加速するための新機能化を可能にしました。しかし、そのような複製された家族遺伝子が分岐するメカニズムについてはほとんど知られていない。ここでは、ホメロログの大西洋サーモンELOVL5AおよびELOVL5B遺伝子がトランスポゾン様要素によって非対称的に定着していることを示しています。同一の位置と挿入のアイデンティティは、虹色のトラウトの重複ELOVL5遺伝子にも存在しますが、最も近い現存する代表的な事前に重複する伸縮式ぼうであるノーザンパイクにはありません。ELOVL5サーモンの両方の重複は、SREBP1依存性転写とSREBP2依存性転写を促進する保存された調節要素を所有しており、プロモーター間のSREBP応答の大きさの違いは、ELOVL5BのSREおよびNF-Y補因子結合部位のタンデム重複に起因する可能性があります。さらに、ELOVL5Aのプロモーター領域への挿入は、LXR/RXR転写活性化に対する応答性を付与します。我々の結果は、すべてではない、すべてではないほとんどの場合、ELOVL5遺伝子へのトランスポゾンの動員は、パイクとサーモンの共通の祖先からの分割後に発生したが、より最近のサケ科の具体化の前に発生したこと、およびELOVL5調節領域の発散が発現することにより新生生物化を可能にしたことを示しています。これらの家族の遺伝子。
Fatty acyl elongase 5 (elovl5) is a critical enzyme in the vertebrate biosynthetic pathway which produces the physiologically essential long-chain polyunsaturated fatty acids (LC-PUFA), docosahexenoic acid (DHA), and eicosapentenoic acid (EPA) from 18 carbon fatty acids precursors. In contrast to most other vertebrates, Atlantic salmon possess two copies of elovl5 (elovl5a and elovl5b) as a result of a whole-genome duplication (WGD) which occurred at the base of the salmonid lineage. WGDs have had a major influence on vertebrate evolution, providing extra genetic material, enabling neofunctionalization to accelerate adaptation and speciation. However, little is known about the mechanisms by which such duplicated homeologous genes diverge. Here we show that homeologous Atlantic salmon elovl5a and elovl5b genes have been asymmetrically colonised by transposon-like elements. Identical locations and identities of insertions are also present in the rainbow trout duplicate elovl5 genes, but not in the nearest extant representative preduplicated teleost, the northern pike. Both elovl5 salmon duplicates possessed conserved regulatory elements that promoted Srebp1- and Srebp2-dependent transcription, and differences in the magnitude of Srebp response between promoters could be attributed to a tandem duplication of SRE and NF-Y cofactor binding sites in elovl5b. Furthermore, an insertion in the promoter region of elovl5a confers responsiveness to Lxr/Rxr transcriptional activation. Our results indicate that most, but not all, transposon mobilisation into elovl5 genes occurred after the split from the common ancestor of pike and salmon, but before more recent salmonid speciations, and that divergence of elovl5 regulatory regions have enabled neofuntionalization by promoting differential expression of these homeologous genes.
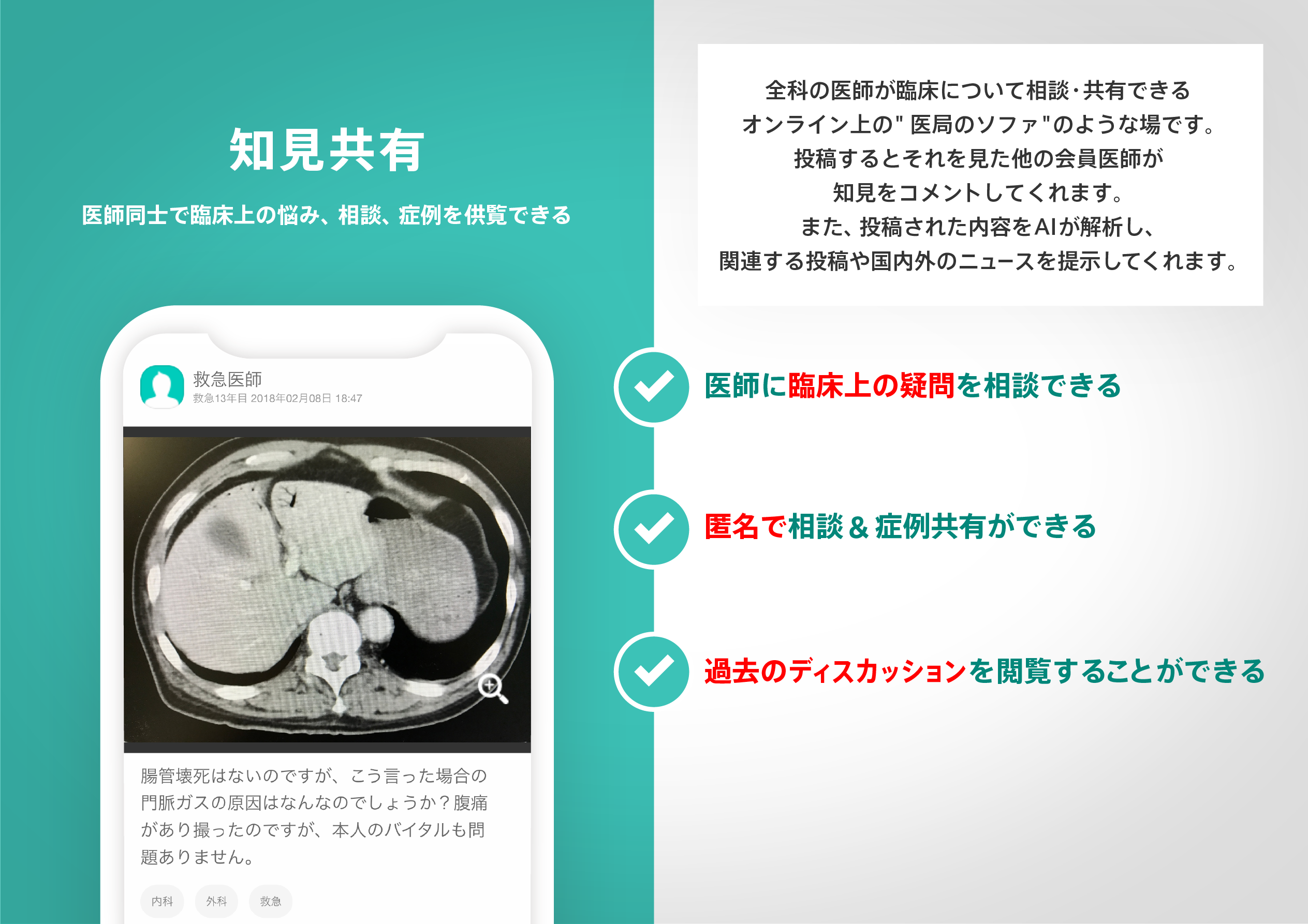
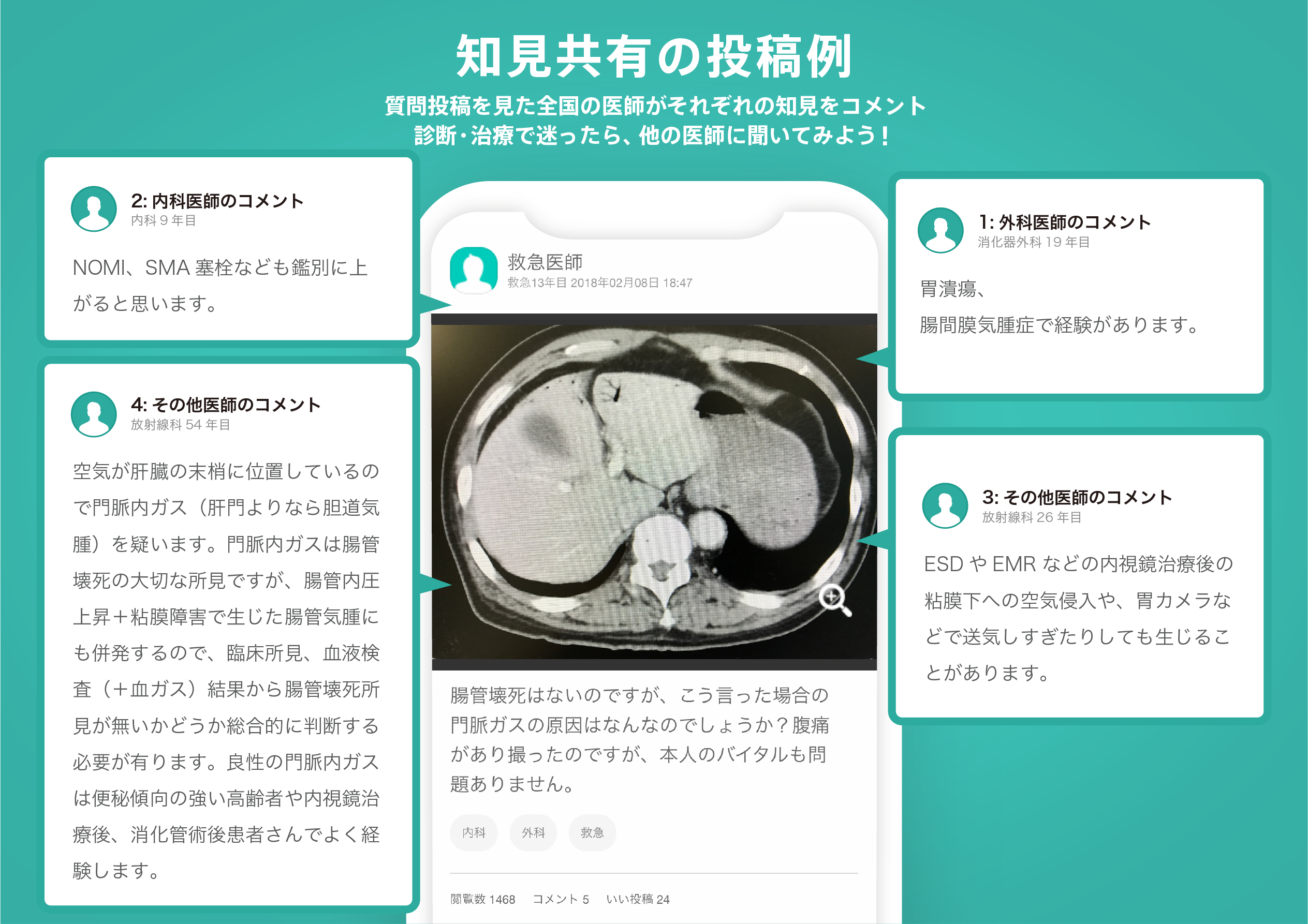
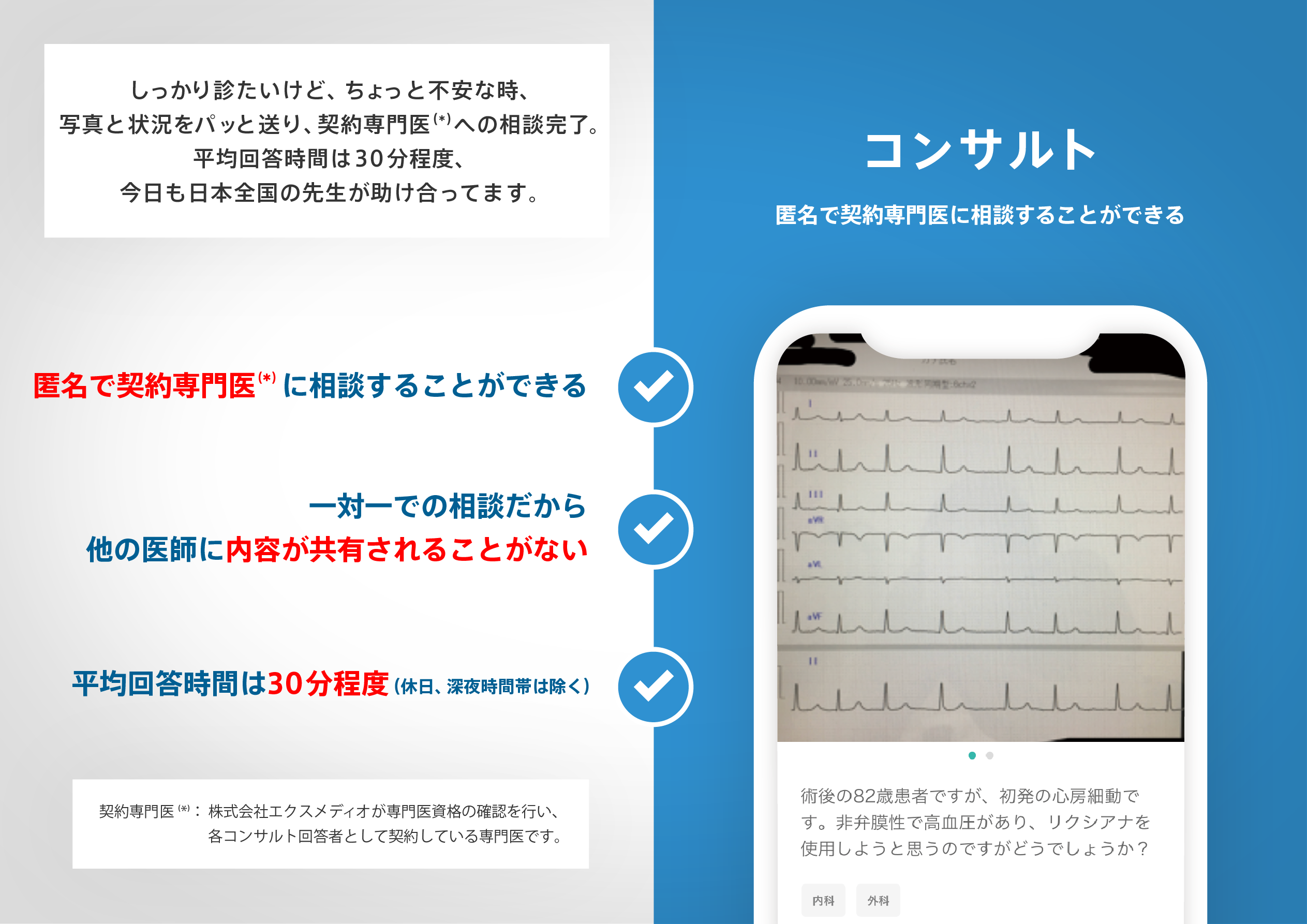
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。