著名医師による解説が無料で読めます
すると翻訳の精度が向上します
ヒト肝フラビンを含むモノオキシゲナーゼ3(HFMO3)は、炭素結合反応性ヘテロ原子のモノオキシゲン化を触媒し、薬物と生体異物の代謝に重要な役割を果たします。多数のHFMO3対立遺伝子バリアントが患者で特定されていますが、in vitroで十分に特徴付けられた生化学的特性は、機能喪失変異の根底にある分子メカニズムは、HFMO3の詳細な構造情報の欠如のためにまだ解明されていません。したがって、この作業では、HFMO3の3D構造モデルが相同性モデリングによって生成され、さまざまなバイオインフォマティクスツールによって評価され、分子動力学シミュレーションによって改良され、in vitro生化学データに基づいてさらに評価されました。Molecular Dynamicsシミュレーション結果は、タンパク質の4つの柔軟な領域を強調し、そのうちのいくつかはTrypsin Digestのデータと重複しています。これに続いて、12の重要な多型変異体の構造マッピングと、HFMO3の5つの異なる既知の基質/薬物、すなわち、ベンジダミン、硫化硫化硫化物、トザサル酸、メチマゾール、トリメチルアミンの5つの異なる基質/薬物を使用した分子ドッキング実験が続きました。HFMO3モデルへのこれらの変異の局在化は、観察された生物学的効果とHFMO3-drug錯体のドッキングされたモデルの構造的説明を提供しました。窒素と硫黄含有基質がPi-Comation comation comation comation comation comation ringとイソロキサジン環と相互作用することを実証する結合メカニズムへの洞察を与えました。それぞれPi硫黄相互作用。最後に、提示されたデータは、HFMO3の薬物結合メカニズムに関する洞察を与えます。これは、新しい化学物質のスクリーニングだけでなく、この重要なフェーズI薬物代謝酵素の新規阻害剤の設計にもっと重要になる可能性があります。
ヒト肝フラビンを含むモノオキシゲナーゼ3(HFMO3)は、炭素結合反応性ヘテロ原子のモノオキシゲン化を触媒し、薬物と生体異物の代謝に重要な役割を果たします。多数のHFMO3対立遺伝子バリアントが患者で特定されていますが、in vitroで十分に特徴付けられた生化学的特性は、機能喪失変異の根底にある分子メカニズムは、HFMO3の詳細な構造情報の欠如のためにまだ解明されていません。したがって、この作業では、HFMO3の3D構造モデルが相同性モデリングによって生成され、さまざまなバイオインフォマティクスツールによって評価され、分子動力学シミュレーションによって改良され、in vitro生化学データに基づいてさらに評価されました。Molecular Dynamicsシミュレーション結果は、タンパク質の4つの柔軟な領域を強調し、そのうちのいくつかはTrypsin Digestのデータと重複しています。これに続いて、12の重要な多型変異体の構造マッピングと、HFMO3の5つの異なる既知の基質/薬物、すなわち、ベンジダミン、硫化硫化硫化物、トザサル酸、メチマゾール、トリメチルアミンの5つの異なる基質/薬物を使用した分子ドッキング実験が続きました。HFMO3モデルへのこれらの変異の局在化は、観察された生物学的効果とHFMO3-drug錯体のドッキングされたモデルの構造的説明を提供しました。窒素と硫黄含有基質がPi-Comation comation comation comation comation comation ringとイソロキサジン環と相互作用することを実証する結合メカニズムへの洞察を与えました。それぞれPi硫黄相互作用。最後に、提示されたデータは、HFMO3の薬物結合メカニズムに関する洞察を与えます。これは、新しい化学物質のスクリーニングだけでなく、この重要なフェーズI薬物代謝酵素の新規阻害剤の設計にもっと重要になる可能性があります。
Human hepatic flavin-containing monooxygenase 3 (hFMO3) catalyses the monooxygenation of carbon-bound reactive heteroatoms and plays an important role in the metabolism of drugs and xenobiotics. Although numerous hFMO3 allelic variants have been identified in patients and their biochemical properties well-characterised in vitro, the molecular mechanisms underlying loss-of-function mutations have still not been elucidated due to lack of detailed structural information of hFMO3. Therefore, in this work a 3D structural model of hFMO3 was generated by homology modeling, evaluated by a variety of different bioinformatics tools, refined by molecular dynamics simulations and further assessed based on in vitro biochemical data. The molecular dynamics simulation results highlighted 4 flexible regions of the protein with some of them overlapping the data from trypsin digest. This was followed by structural mapping of 12 critical polymorphic variants and molecular docking experiments with five different known substrates/drugs of hFMO3 namely, benzydamine, sulindac sulfide, tozasertib, methimazole and trimethylamine. Localisation of these mutations on the hFMO3 model provided a structural explanation for their observed biological effects and docked models of hFMO3-drug complexes gave insights into their binding mechanism demonstrating that nitrogen- and sulfur-containing substrates interact with the isoalloxazine ring through Pi-Cation interaction and Pi-Sulfur interactions, respectively. Finally, the data presented give insights into the drug binding mechanism of hFMO3 which could be valuable not only for screening of new chemical entities but more significantly for designing of novel inhibitors of this important Phase I drug metabolising enzyme.
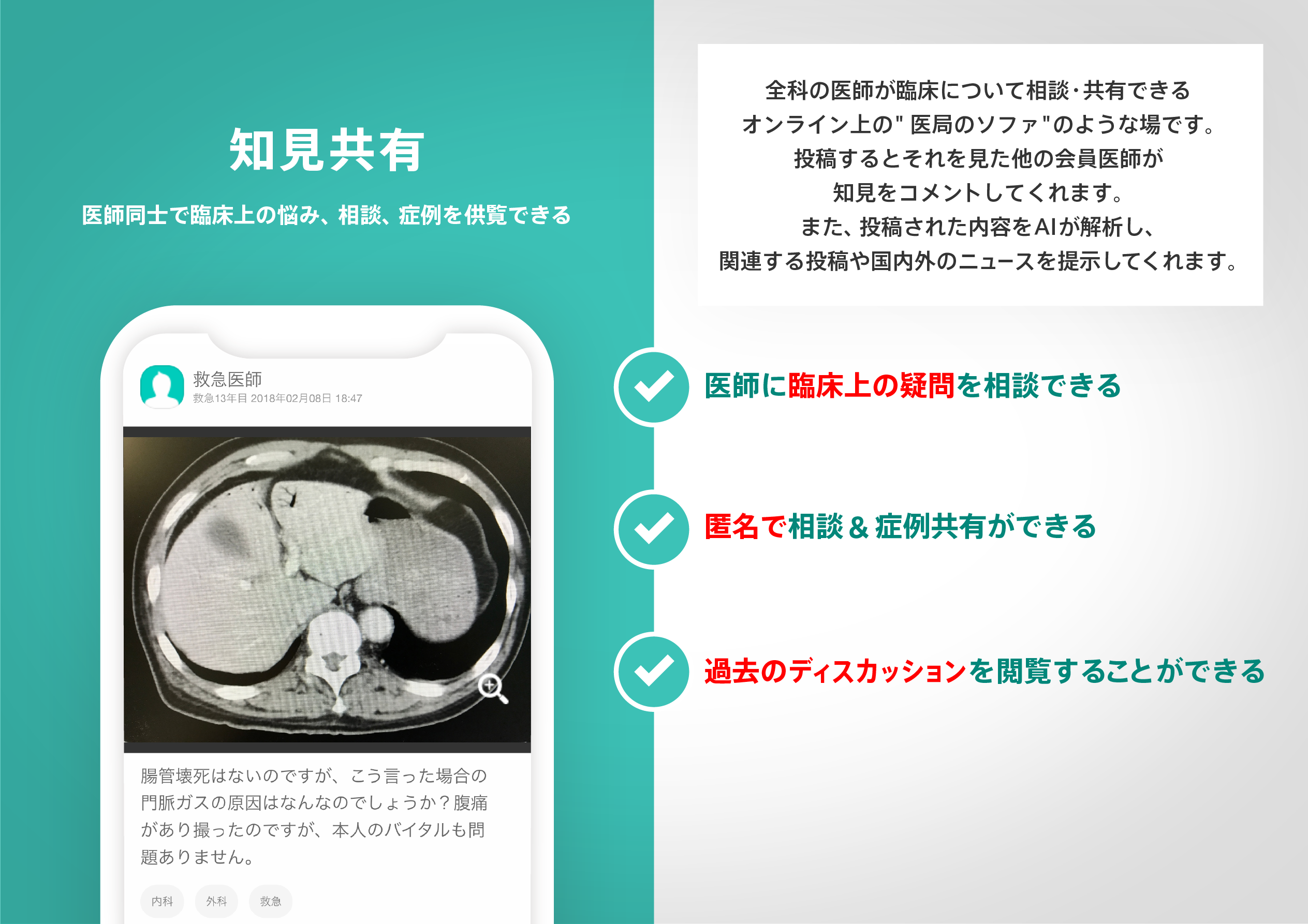
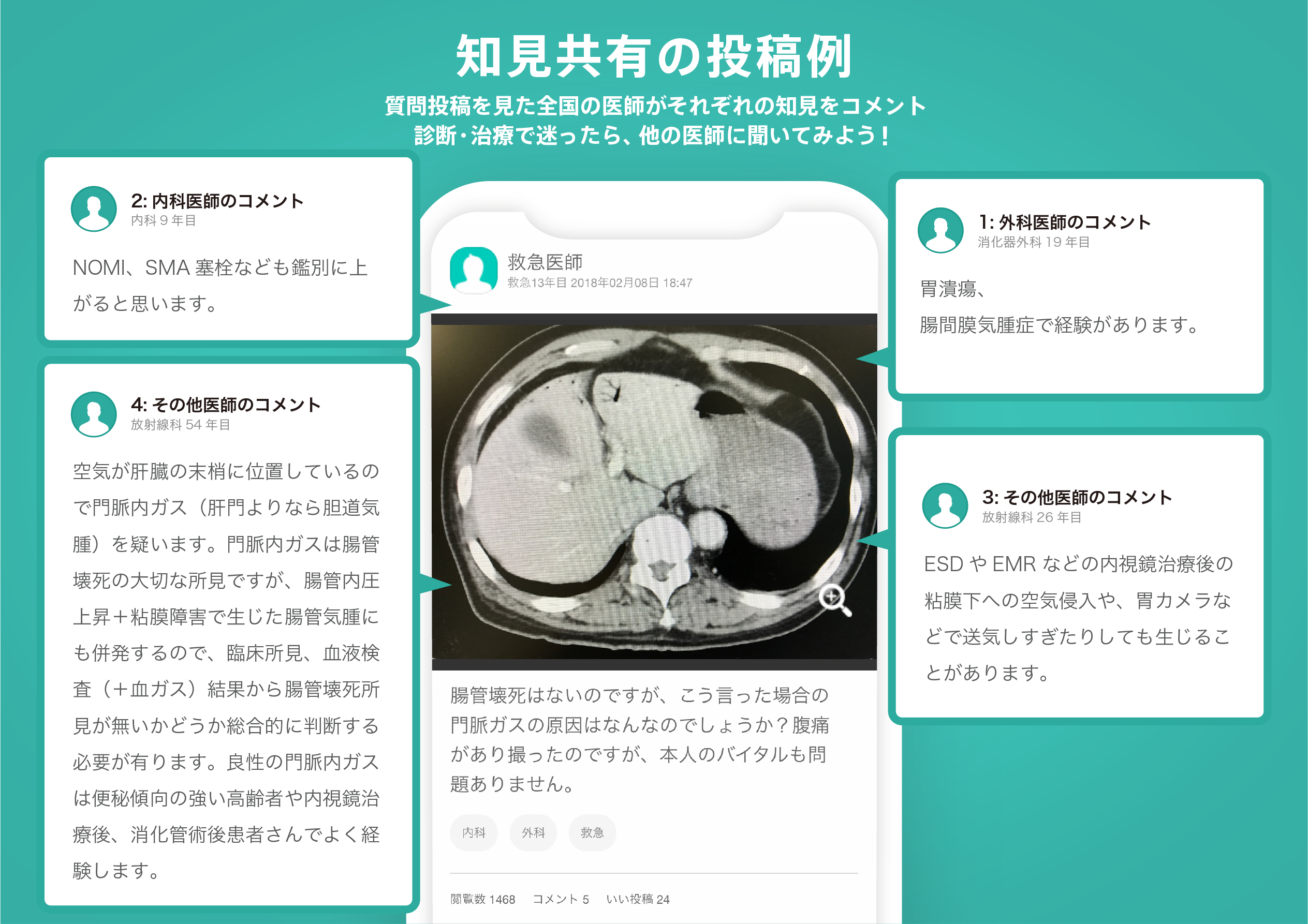
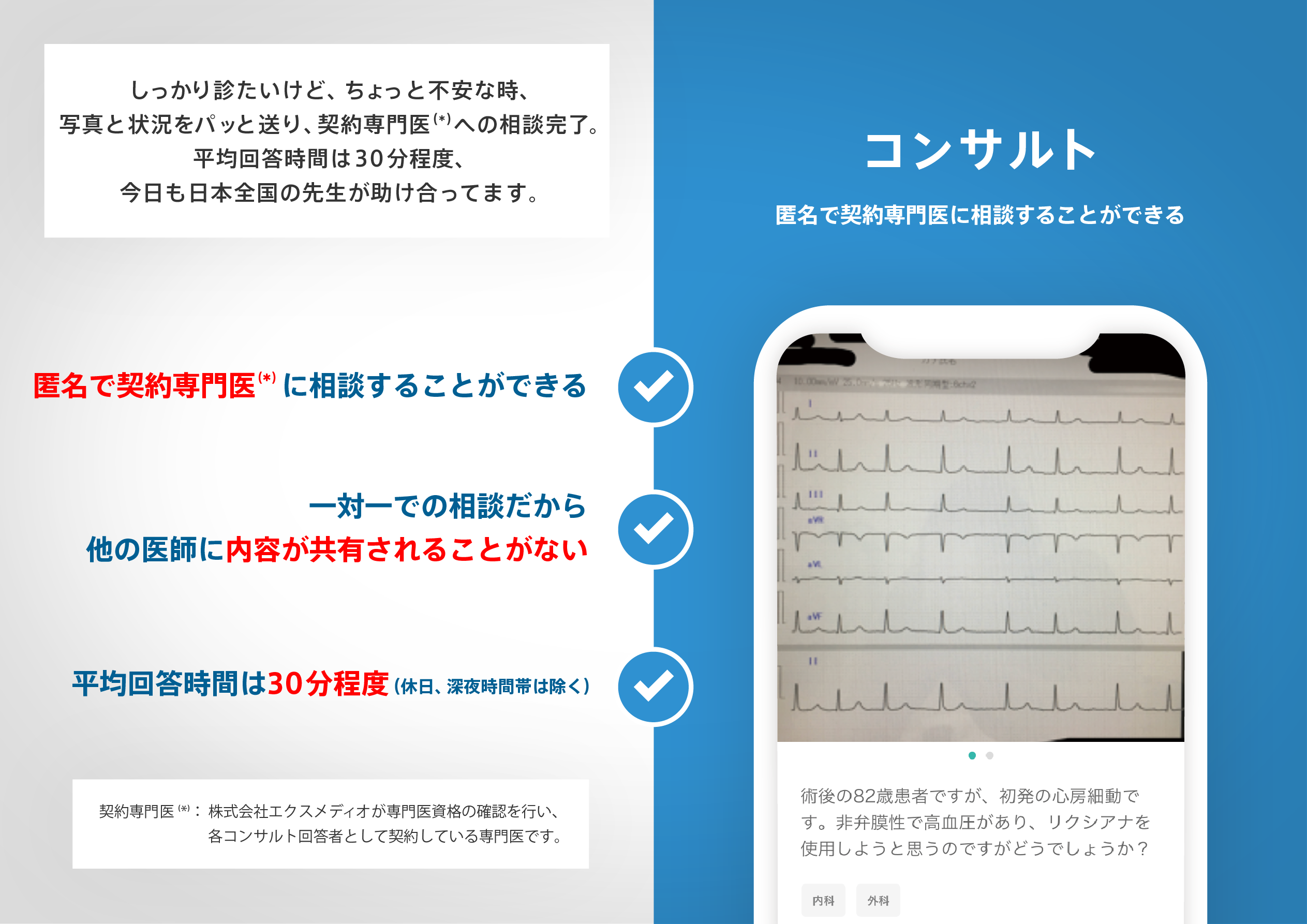
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。