著名医師による解説が無料で読めます
すると翻訳の精度が向上します
動機:シーケンス技術により、事前の培養なしに環境から直接微生物群集をシーケンスすることができます。ビニングと呼ばれるプロセスである微生物群集の分類分析は、メタゲノムの読み取りデータを分析する際に最も困難なタスクの1つです。主な問題は、既存の参照データベースに分類学的に関連するゲノムの欠如、種の不均一な存在率、および短い読み取り長とシーケンスエラーによる制限です。 結果:Metaprobは、監視されていないメタゲノムビニングのための新しい組み立て支援ツールです。Metaprobの斬新さは、いくつかの重要な問題を解決することに由来しています。読み取りを独立した読み取りのグループに分割する方法であるため、K-MER周波数は過大評価されません。K-MERカウントを確率的配列シグネチャに変換する方法は、K-MERの可変分布を修正し、基礎となるゲノム統計のより良い推定値を生成するために、読み取りの不均衡なグループを修正します。データセット内の種の数を推定する方法。メタプロブは、さまざまな存在比のために、短い読み取りデータセット(Fメジャー0.87)と長い読み取りデータセット(Fメジャー0.97)の両方をビニングする他の最先端のツールよりも正確で効率的であることを示しています。また、種の数の推定は、メタクラスターよりも正確です。実際の人間のスツールデータセットメタプロブは、以前の人間の腸の研究に沿って、最も主要な種を識別します。 可用性と実装:https://bitbucket.org/samu661/metaprob 連絡先:cinzia.pizzi@dei.unipd.itまたはcomin@dei.unipd.it 補足情報:補足データは、バイオインフォマティクスオンラインで入手できます。
動機:シーケンス技術により、事前の培養なしに環境から直接微生物群集をシーケンスすることができます。ビニングと呼ばれるプロセスである微生物群集の分類分析は、メタゲノムの読み取りデータを分析する際に最も困難なタスクの1つです。主な問題は、既存の参照データベースに分類学的に関連するゲノムの欠如、種の不均一な存在率、および短い読み取り長とシーケンスエラーによる制限です。 結果:Metaprobは、監視されていないメタゲノムビニングのための新しい組み立て支援ツールです。Metaprobの斬新さは、いくつかの重要な問題を解決することに由来しています。読み取りを独立した読み取りのグループに分割する方法であるため、K-MER周波数は過大評価されません。K-MERカウントを確率的配列シグネチャに変換する方法は、K-MERの可変分布を修正し、基礎となるゲノム統計のより良い推定値を生成するために、読み取りの不均衡なグループを修正します。データセット内の種の数を推定する方法。メタプロブは、さまざまな存在比のために、短い読み取りデータセット(Fメジャー0.87)と長い読み取りデータセット(Fメジャー0.97)の両方をビニングする他の最先端のツールよりも正確で効率的であることを示しています。また、種の数の推定は、メタクラスターよりも正確です。実際の人間のスツールデータセットメタプロブは、以前の人間の腸の研究に沿って、最も主要な種を識別します。 可用性と実装:https://bitbucket.org/samu661/metaprob 連絡先:cinzia.pizzi@dei.unipd.itまたはcomin@dei.unipd.it 補足情報:補足データは、バイオインフォマティクスオンラインで入手できます。
MOTIVATION: Sequencing technologies allow the sequencing of microbial communities directly from the environment without prior culturing. Taxonomic analysis of microbial communities, a process referred to as binning, is one of the most challenging tasks when analyzing metagenomic reads data. The major problems are the lack of taxonomically related genomes in existing reference databases, the uneven abundance ratio of species and the limitations due to short read lengths and sequencing errors. RESULTS: MetaProb is a novel assembly-assisted tool for unsupervised metagenomic binning. The novelty of MetaProb derives from solving a few important problems: how to divide reads into groups of independent reads, so that k-mer frequencies are not overestimated; how to convert k-mer counts into probabilistic sequence signatures, that will correct for variable distribution of k-mers, and for unbalanced groups of reads, in order to produce better estimates of the underlying genome statistic; how to estimate the number of species in a dataset. We show that MetaProb is more accurate and efficient than other state-of-the-art tools in binning both short reads datasets (F-measure 0.87) and long reads datasets (F-measure 0.97) for various abundance ratios. Also, the estimation of the number of species is more accurate than MetaCluster. On a real human stool dataset MetaProb identifies the most predominant species, in line with previous human gut studies. AVAILABILITY AND IMPLEMENTATION: https://bitbucket.org/samu661/metaprob CONTACTS: cinzia.pizzi@dei.unipd.it or comin@dei.unipd.it SUPPLEMENTARY INFORMATION: Supplementary data are available at Bioinformatics online.
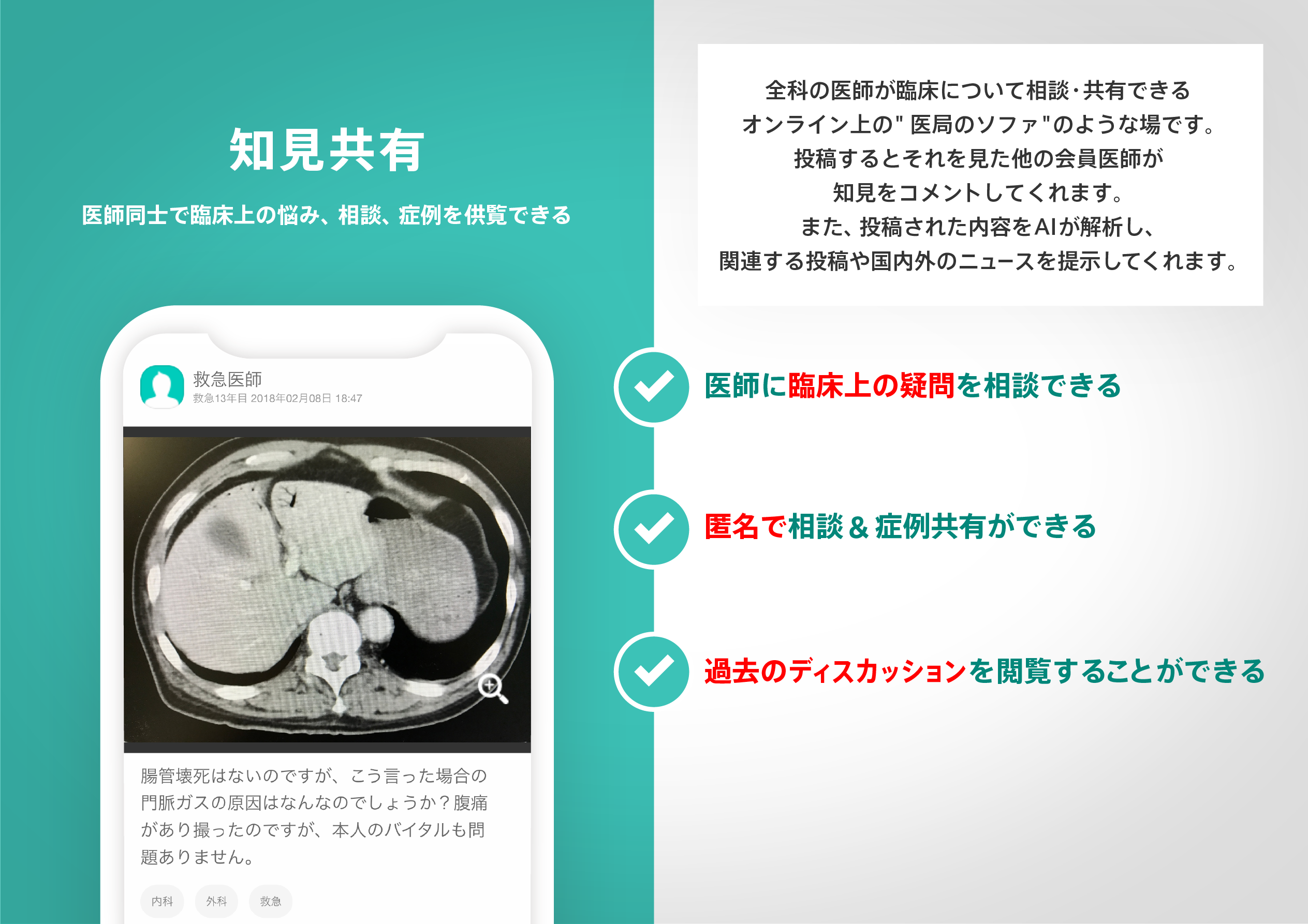
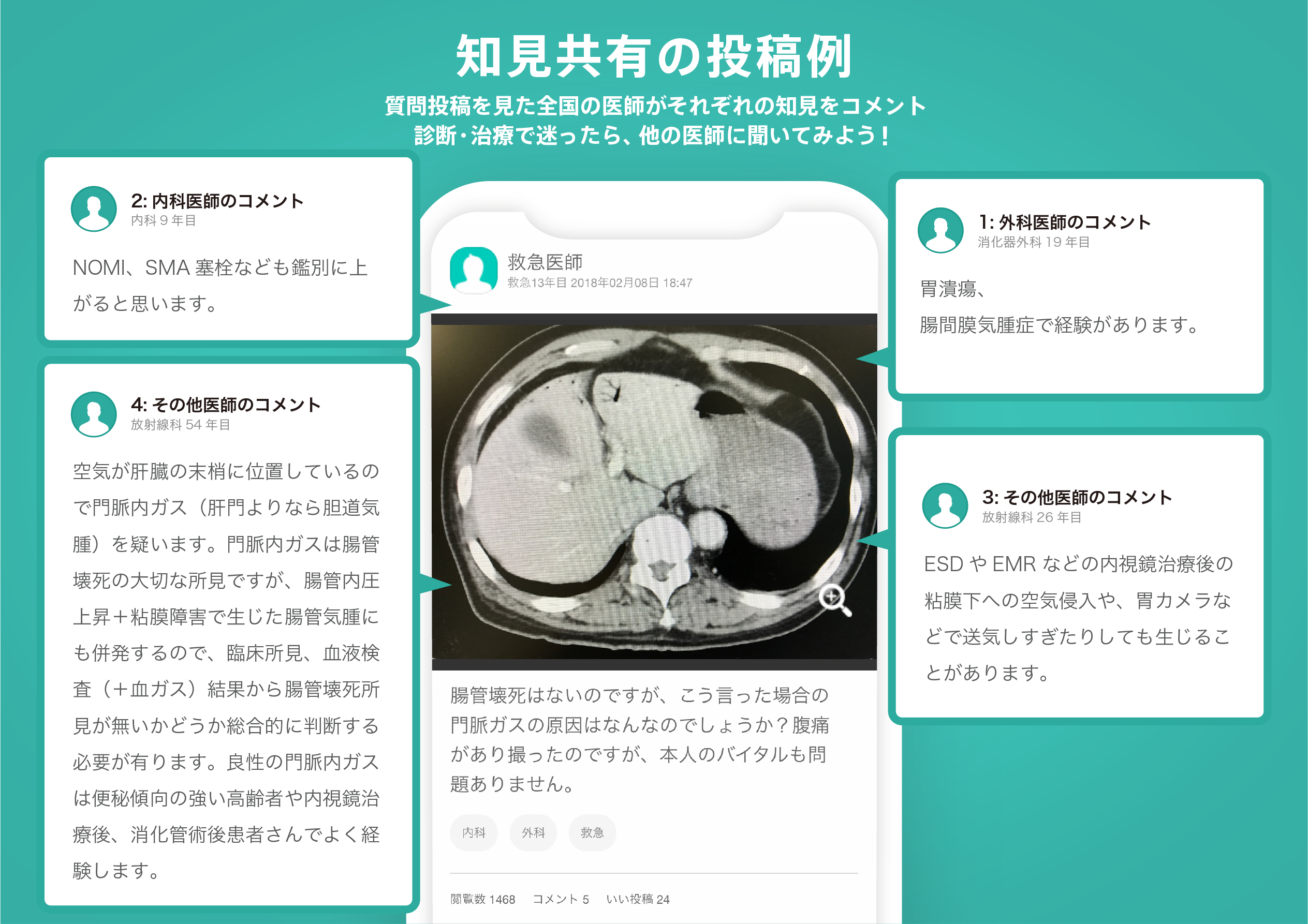
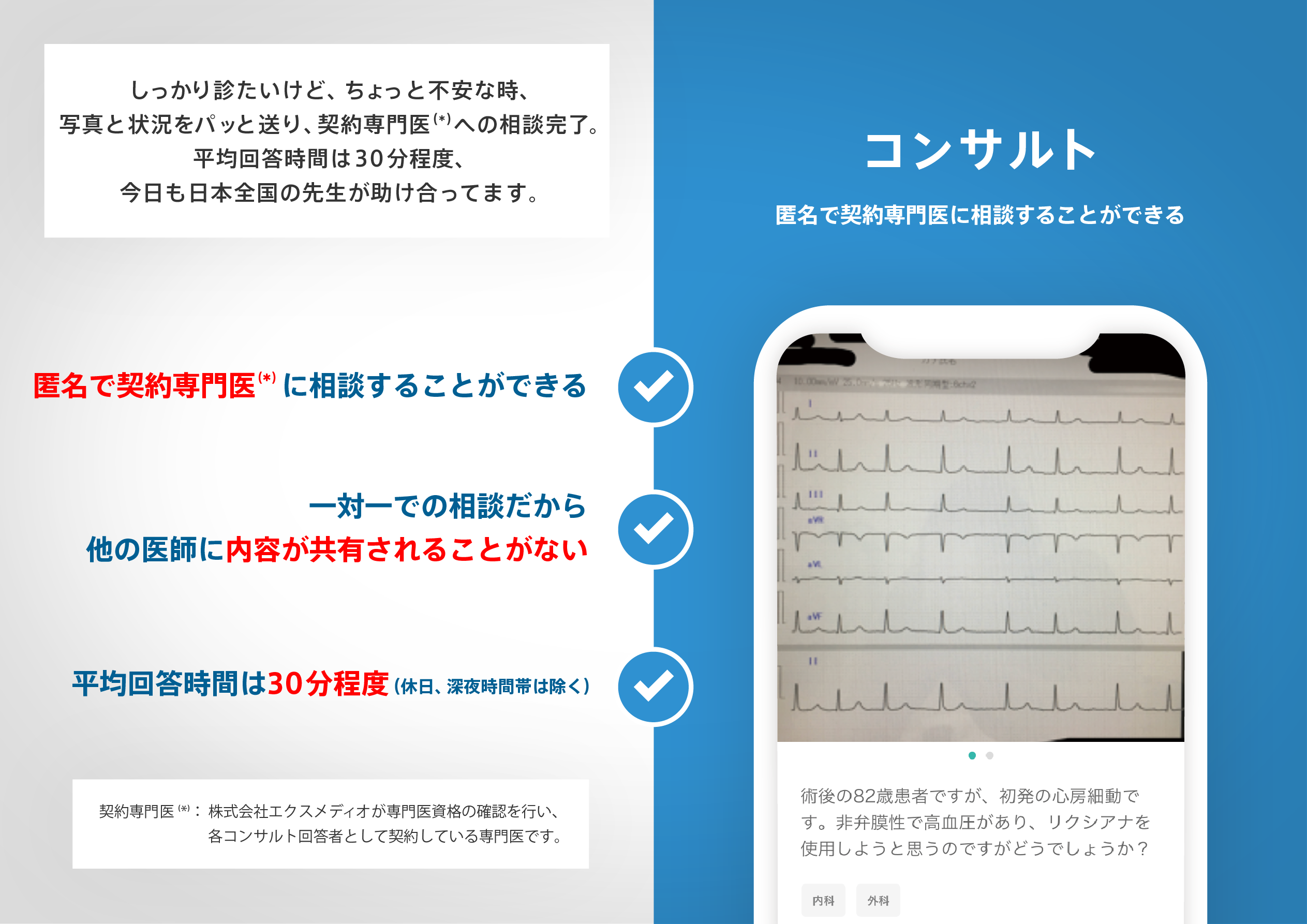
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。