著名医師による解説が無料で読めます
すると翻訳の精度が向上します
パラログ遺伝子は、進化中の遺伝子重複イベントから生じます。これは、一般的な経路やタンパク質複合体で協力する同様のタンパク質につながることがよくあります。その結果、パラログは遺伝子発現の相関関係を示し、それにより共同規制のメカニズムが不明のままです。真核生物では、遺伝子は、遺伝子プロモーターとの相互作用をループすることにより、遠位エンハンサー要素によって部分的に調節されます。これらのループ相互作用は、ゲノム全体のクロマチン立体構造捕捉(HI-C)実験によって測定でき、トポロジカルな関連ドメイン(TAD)と呼ばれる自己相互作用領域を明らかにしました。Paralogは、TADSに従って調整された表現を可能にするために共通の規制メカニズムを共有していると仮定します。この仮説をテストするために、多様な組織、ゲノム全体のエンハンサープロモーター関連、およびヒト、マウス、ドッグゲノムのHI-C実験におけるヒト遺伝子発現データとパラロジーアノテーションを統合しました。パラログ遺伝子ペアは、同じTADでの共局在のために濃縮され、予想よりも一般的なエンハンサー要素を共有し、大きなゲノム距離で接触頻度を増加させていることを示しています。合わせて、我々の結果は、パラログが共通の調節メカニズムとクラスターを線形ゲノムだけでなく、3次元クロマチンアーキテクチャでも共有していることを示しています。これにより、多様な細胞型に対するパラログの協調的な表現が可能になり、機能的ゲノム組織における進化的制約を示します。
パラログ遺伝子は、進化中の遺伝子重複イベントから生じます。これは、一般的な経路やタンパク質複合体で協力する同様のタンパク質につながることがよくあります。その結果、パラログは遺伝子発現の相関関係を示し、それにより共同規制のメカニズムが不明のままです。真核生物では、遺伝子は、遺伝子プロモーターとの相互作用をループすることにより、遠位エンハンサー要素によって部分的に調節されます。これらのループ相互作用は、ゲノム全体のクロマチン立体構造捕捉(HI-C)実験によって測定でき、トポロジカルな関連ドメイン(TAD)と呼ばれる自己相互作用領域を明らかにしました。Paralogは、TADSに従って調整された表現を可能にするために共通の規制メカニズムを共有していると仮定します。この仮説をテストするために、多様な組織、ゲノム全体のエンハンサープロモーター関連、およびヒト、マウス、ドッグゲノムのHI-C実験におけるヒト遺伝子発現データとパラロジーアノテーションを統合しました。パラログ遺伝子ペアは、同じTADでの共局在のために濃縮され、予想よりも一般的なエンハンサー要素を共有し、大きなゲノム距離で接触頻度を増加させていることを示しています。合わせて、我々の結果は、パラログが共通の調節メカニズムとクラスターを線形ゲノムだけでなく、3次元クロマチンアーキテクチャでも共有していることを示しています。これにより、多様な細胞型に対するパラログの協調的な表現が可能になり、機能的ゲノム組織における進化的制約を示します。
Paralog genes arise from gene duplication events during evolution, which often lead to similar proteins that cooperate in common pathways and in protein complexes. Consequently, paralogs show correlation in gene expression whereby the mechanisms of co-regulation remain unclear. In eukaryotes, genes are regulated in part by distal enhancer elements through looping interactions with gene promoters. These looping interactions can be measured by genome-wide chromatin conformation capture (Hi-C) experiments, which revealed self-interacting regions called topologically associating domains (TADs). We hypothesize that paralogs share common regulatory mechanisms to enable coordinated expression according to TADs. To test this hypothesis, we integrated paralogy annotations with human gene expression data in diverse tissues, genome-wide enhancer-promoter associations and Hi-C experiments in human, mouse and dog genomes. We show that paralog gene pairs are enriched for co-localization in the same TAD, share more often common enhancer elements than expected and have increased contact frequencies over large genomic distances. Combined, our results indicate that paralogs share common regulatory mechanisms and cluster not only in the linear genome but also in the three-dimensional chromatin architecture. This enables concerted expression of paralogs over diverse cell-types and indicate evolutionary constraints in functional genome organization.
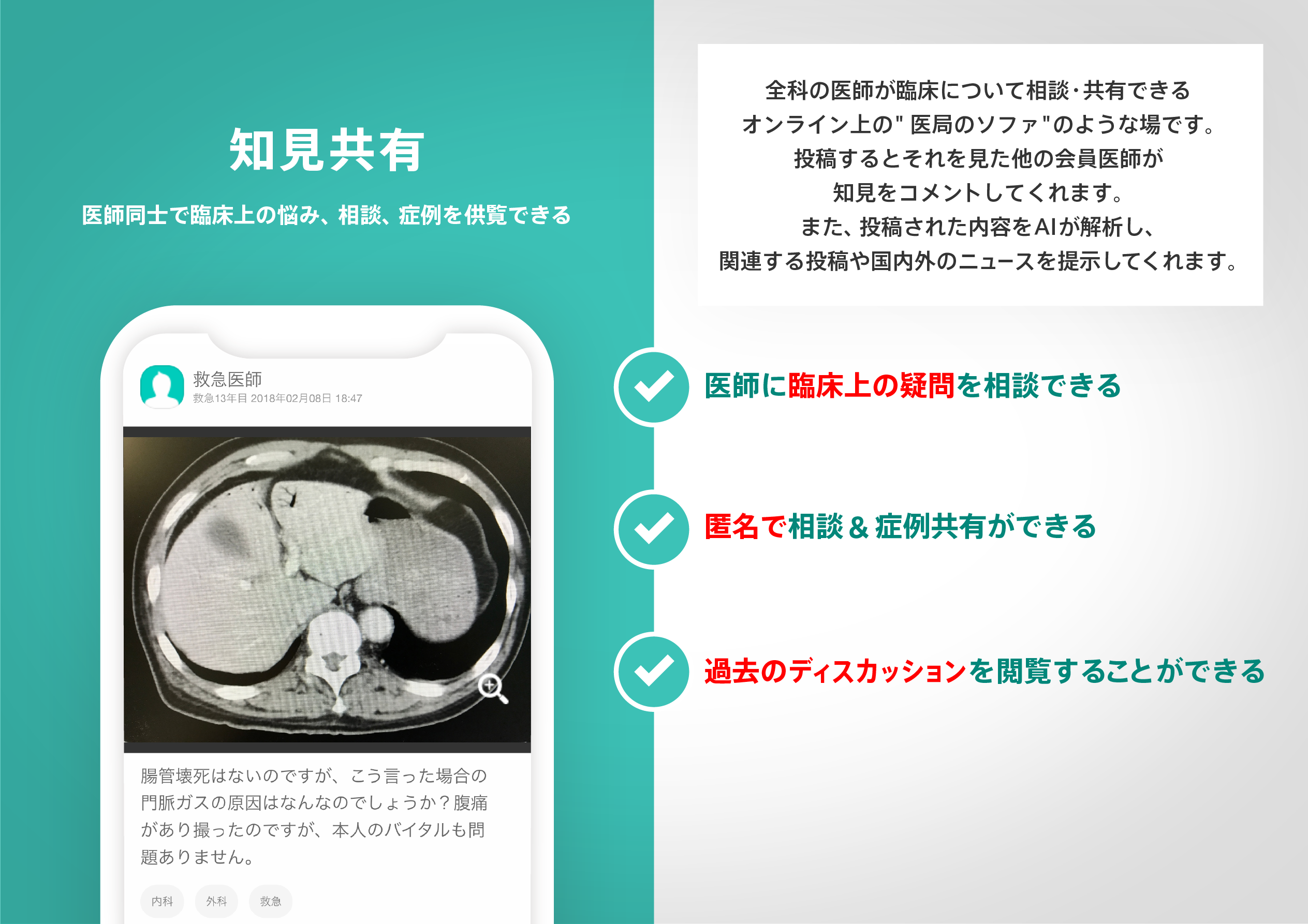
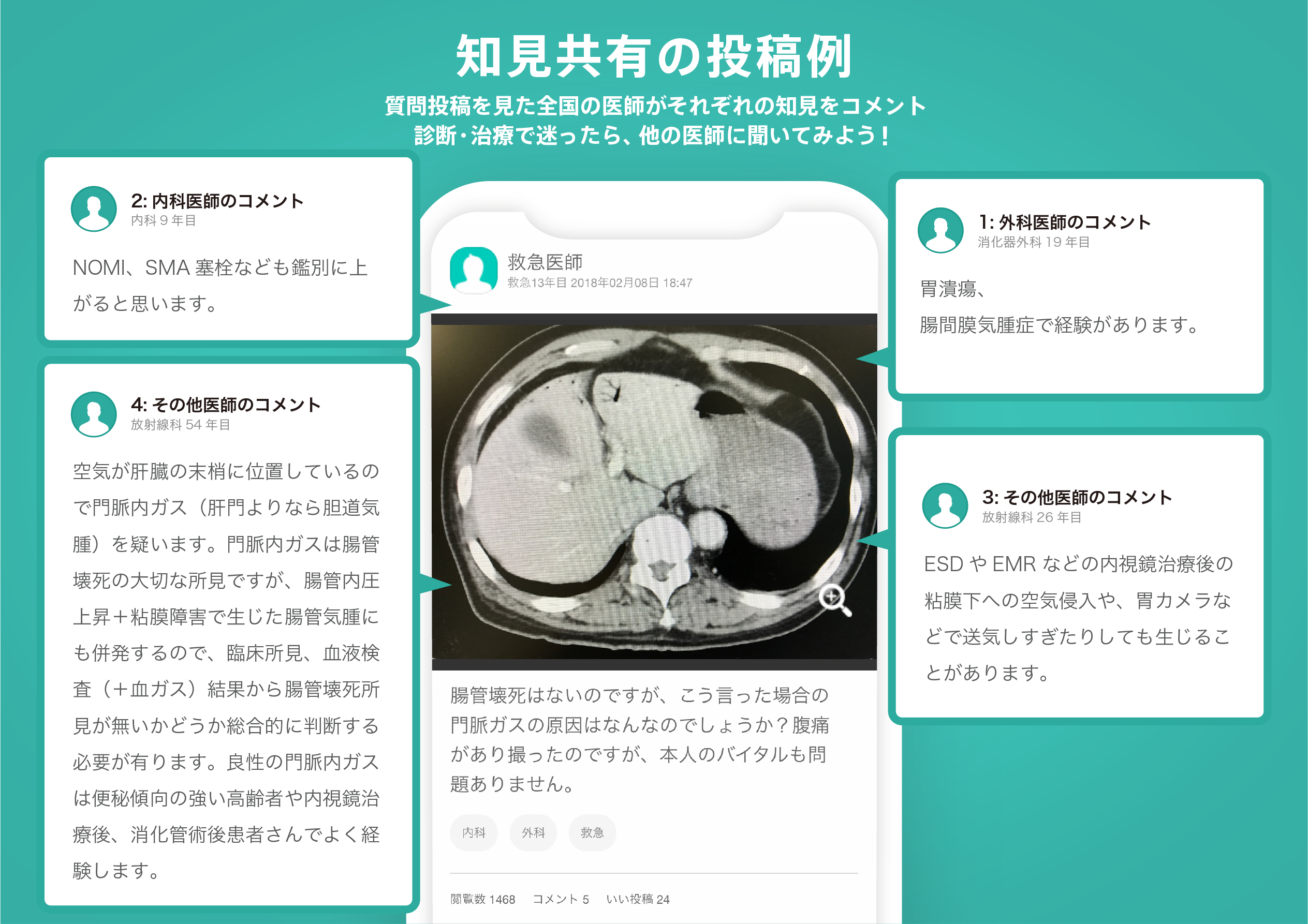
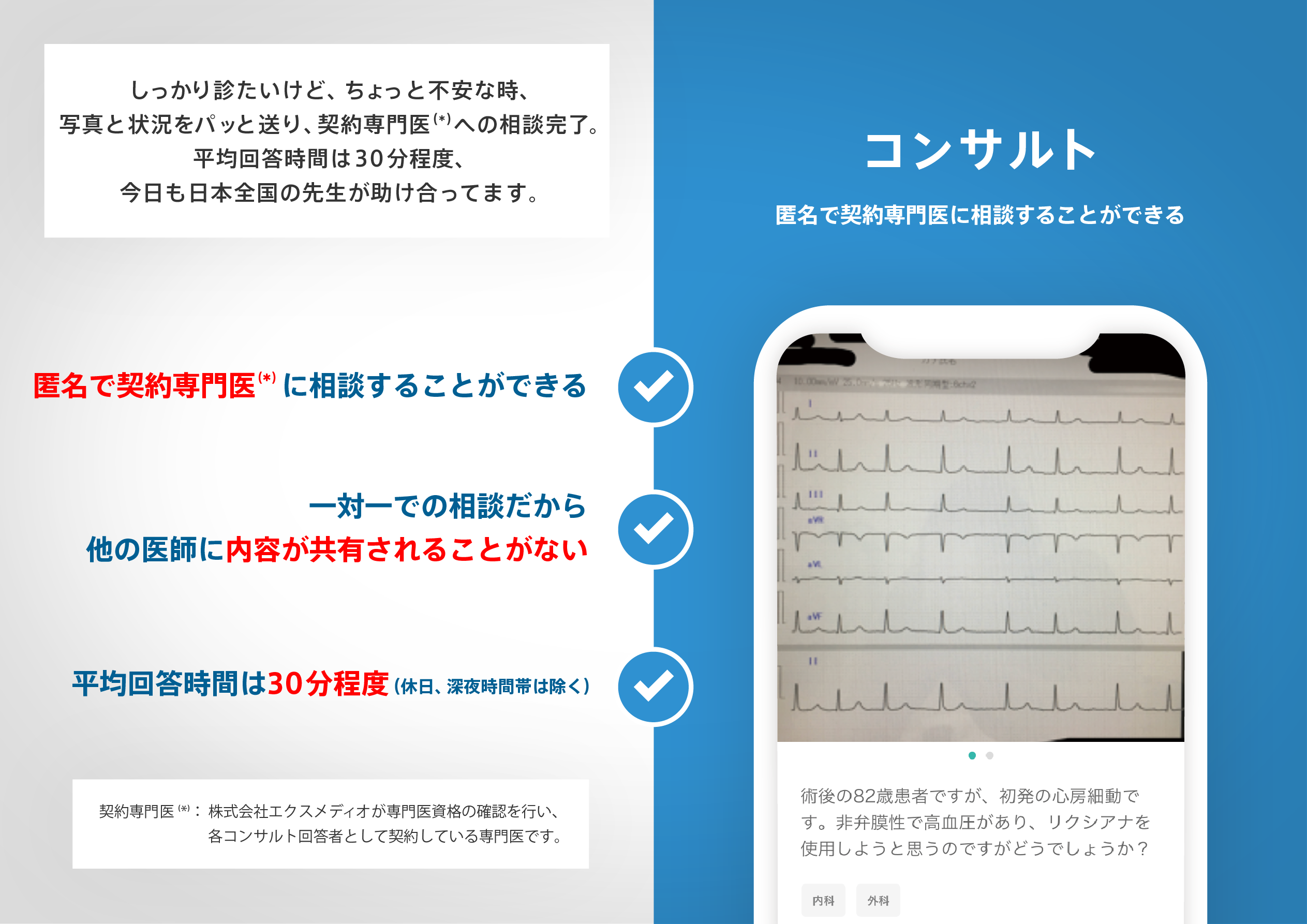
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。