著名医師による解説が無料で読めます
すると翻訳の精度が向上します
背景: ヒトキノームの系統樹の注釈は、化合物プロファイリングデータ、キナーゼの構造的特徴、またはこの重要なタンパク質クラス内の機能的関係を視覚化する直感的な方法です。キナーゼ関連データの量と複雑さの増加は、キナーゼ疾患の関与およびキナーゼ阻害剤の潜在的な治療用途に関する複雑なクエリを可能にするツールの必要性を強調しています。 結果: ここでは、生化学的、構造的、および疾患関連データをヒトキノームツリーにリンクすることにより、キナーゼ知識による対話型ナビゲーションを容易にするユーザーフレンドリーなオンラインツールである KinMap を紹介します。この目的を達成するために、ChEMBL、Protein Data Bank、Center for Therapeutic Target Validation プラットフォームなど、自由に入手できるソースからの前処理されたデータが KinMap に統合され、独自のデータで簡単に補完できます。KinMap の価値は、既知のキナーゼ阻害剤の新たな治療適応を明らかにし、医薬品開発の取り組みにおいてキナーゼの優先順位を付けるために、例示的に実証されるでしょう。 結論: KinMap は、人間の kinome のインタラクティブな探索を容易にする新世代の kinome ツリー ビューアです。KinMap を使用すると、人間のキノム ツリーの高品質の注釈付き画像の生成と、科学コミュニケーションにおけるキノム関連データの交換が可能になります。さらに、KinMap は複数の入力および出力形式をサポートし、代替キナーゼ名を認識して統一された命名スキームにリンクするため、さまざまな分野やアプリケーションにわたって便利なツールになります。KinMap の Web サービスは、 http://www.kinhub.org/kinmap/ から無料で利用できます。
背景: ヒトキノームの系統樹の注釈は、化合物プロファイリングデータ、キナーゼの構造的特徴、またはこの重要なタンパク質クラス内の機能的関係を視覚化する直感的な方法です。キナーゼ関連データの量と複雑さの増加は、キナーゼ疾患の関与およびキナーゼ阻害剤の潜在的な治療用途に関する複雑なクエリを可能にするツールの必要性を強調しています。 結果: ここでは、生化学的、構造的、および疾患関連データをヒトキノームツリーにリンクすることにより、キナーゼ知識による対話型ナビゲーションを容易にするユーザーフレンドリーなオンラインツールである KinMap を紹介します。この目的を達成するために、ChEMBL、Protein Data Bank、Center for Therapeutic Target Validation プラットフォームなど、自由に入手できるソースからの前処理されたデータが KinMap に統合され、独自のデータで簡単に補完できます。KinMap の価値は、既知のキナーゼ阻害剤の新たな治療適応を明らかにし、医薬品開発の取り組みにおいてキナーゼの優先順位を付けるために、例示的に実証されるでしょう。 結論: KinMap は、人間の kinome のインタラクティブな探索を容易にする新世代の kinome ツリー ビューアです。KinMap を使用すると、人間のキノム ツリーの高品質の注釈付き画像の生成と、科学コミュニケーションにおけるキノム関連データの交換が可能になります。さらに、KinMap は複数の入力および出力形式をサポートし、代替キナーゼ名を認識して統一された命名スキームにリンクするため、さまざまな分野やアプリケーションにわたって便利なツールになります。KinMap の Web サービスは、 http://www.kinhub.org/kinmap/ から無料で利用できます。
BACKGROUND: Annotations of the phylogenetic tree of the human kinome is an intuitive way to visualize compound profiling data, structural features of kinases or functional relationships within this important class of proteins. The increasing volume and complexity of kinase-related data underlines the need for a tool that enables complex queries pertaining to kinase disease involvement and potential therapeutic uses of kinase inhibitors. RESULTS: Here, we present KinMap, a user-friendly online tool that facilitates the interactive navigation through kinase knowledge by linking biochemical, structural, and disease association data to the human kinome tree. To this end, preprocessed data from freely-available sources, such as ChEMBL, the Protein Data Bank, and the Center for Therapeutic Target Validation platform are integrated into KinMap and can easily be complemented by proprietary data. The value of KinMap will be exemplarily demonstrated for uncovering new therapeutic indications of known kinase inhibitors and for prioritizing kinases for drug development efforts. CONCLUSION: KinMap represents a new generation of kinome tree viewers which facilitates interactive exploration of the human kinome. KinMap enables generation of high-quality annotated images of the human kinome tree as well as exchange of kinome-related data in scientific communications. Furthermore, KinMap supports multiple input and output formats and recognizes alternative kinase names and links them to a unified naming scheme, which makes it a useful tool across different disciplines and applications. A web-service of KinMap is freely available at http://www.kinhub.org/kinmap/ .
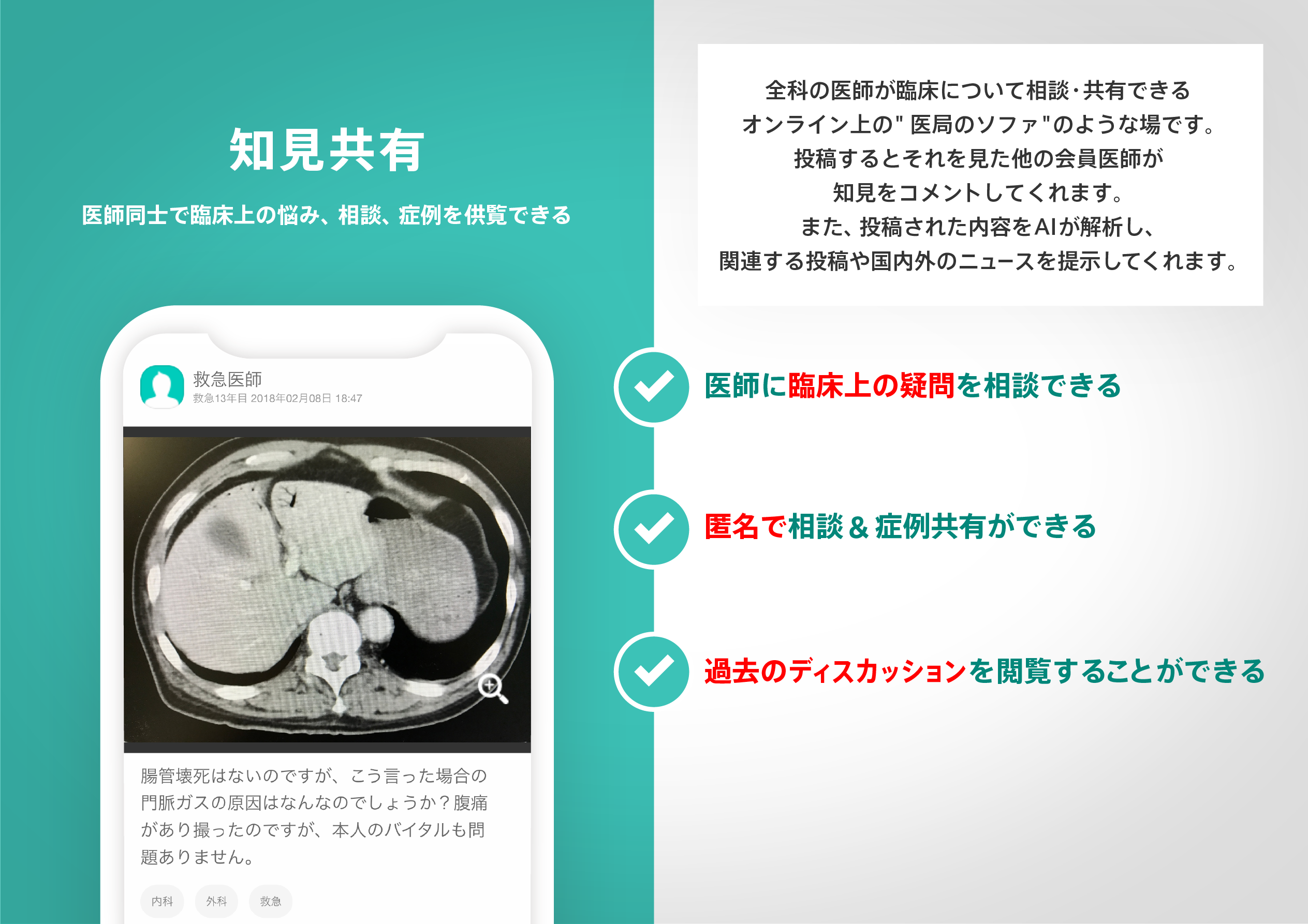
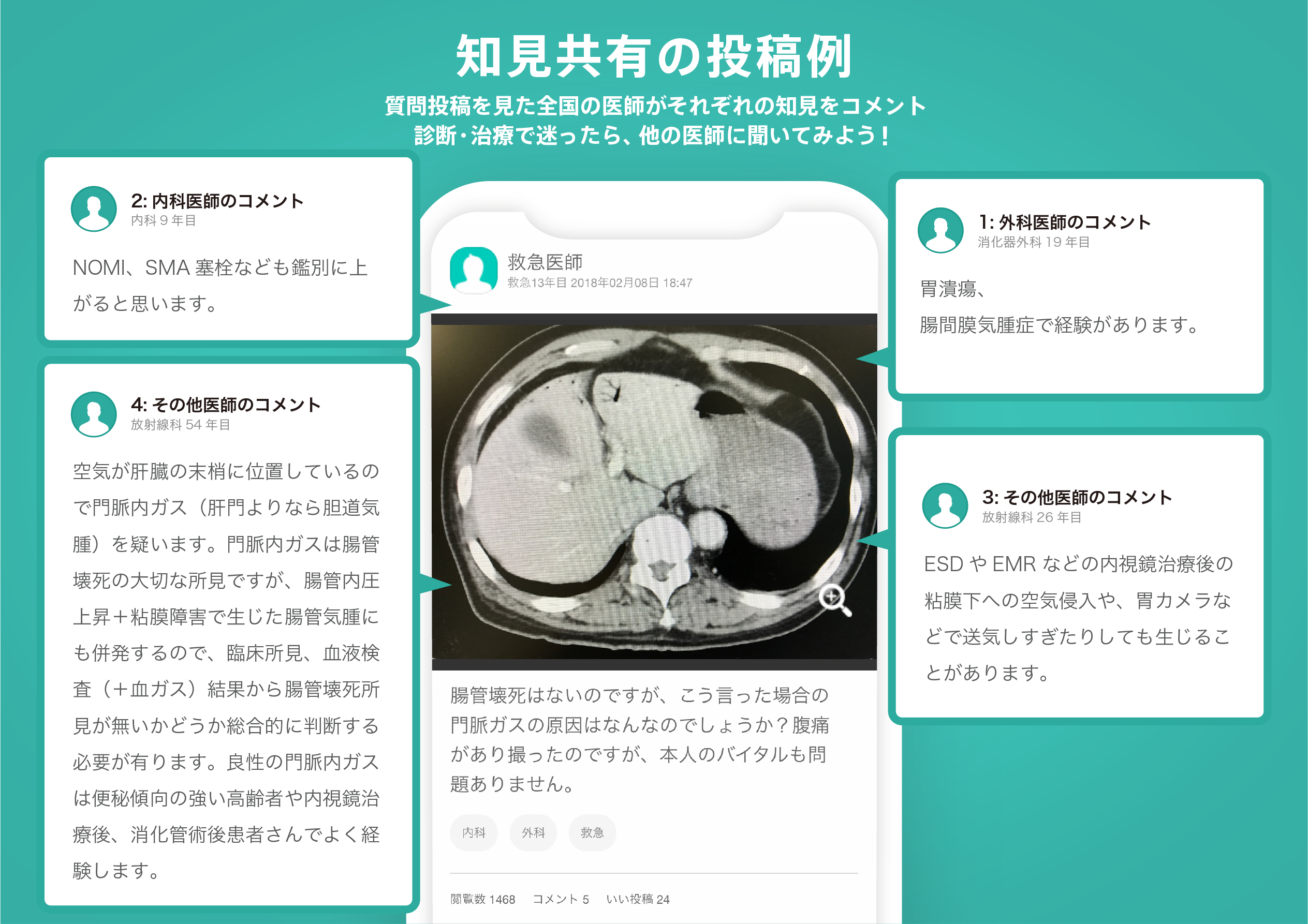
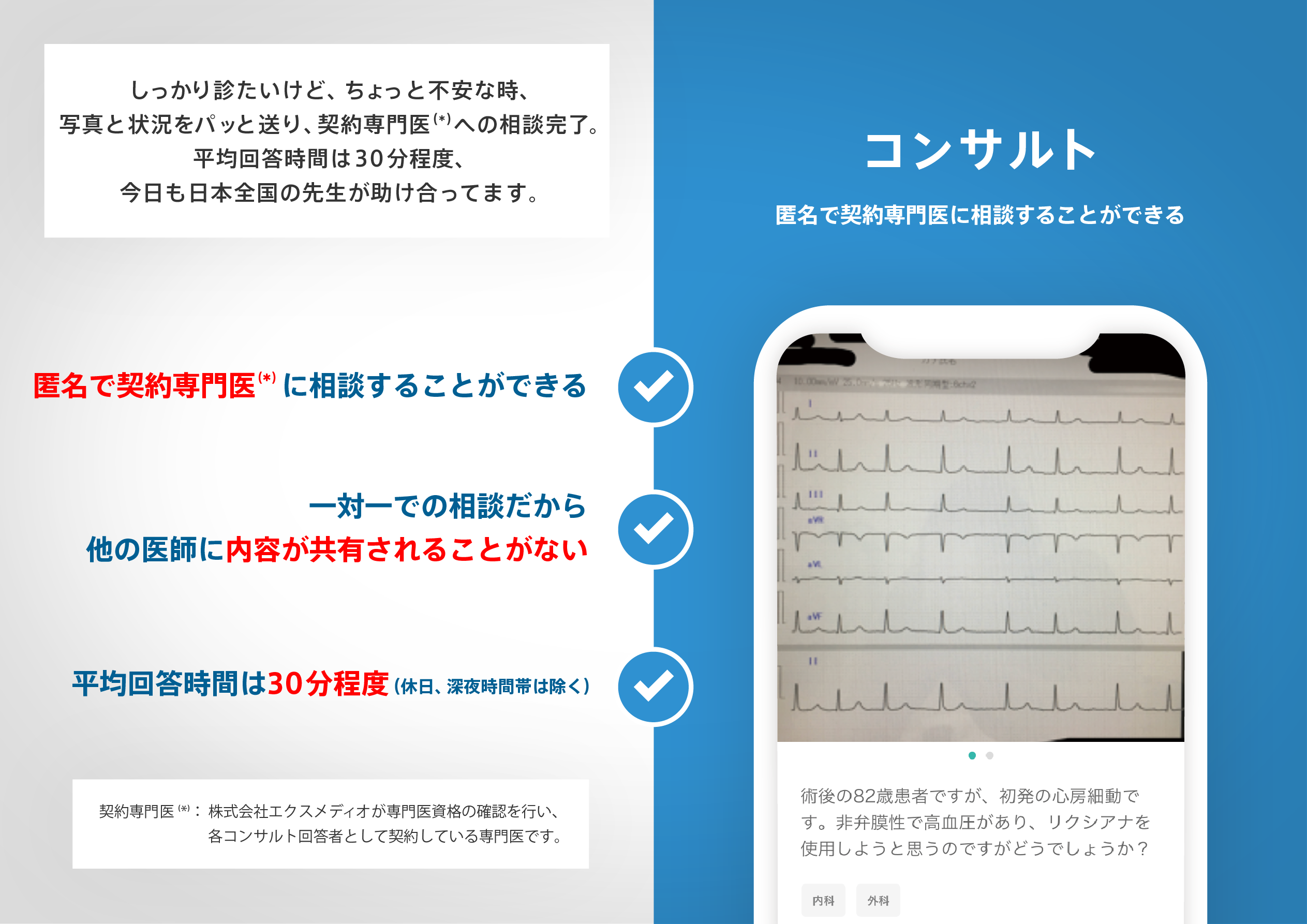
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。