著名医師による解説が無料で読めます
すると翻訳の精度が向上します
さまざまな長さとシーケンスのパリンドロムをバクテリオファージPhi X174ゲノムの非必須領域に挿入することにより、パリンドロームのサイズとシーケンスの遺伝的安定性の効果を調査しました。ECORIリンカーCCGAATTCGG(E)、BAMHIリンカーCCGGATCCGG(B)または両方の混合物(E、B)のサイズが増加するマルチマーは、以前に構築されたバクテリオファージ株PHI X174 J-F INS6のPVUII部位に挿入されました。遺伝的安定性を有意に喪失することなくゲノムで維持できる最大のインサートは、それぞれ2b、4e、および4(e、b)でした。このサイズを超えるポリマーは挿入できますが、ファージゲノムからの迅速かつ正確な欠失をもたらしました。これにより、NBはNEよりも不安定であり、NEはNよりも不安定でした(E、B)。結果として得られた欠失変異体の分析は、2つの異なるタイプの削除の証拠を提供しました。より頻繁な欠失は、いずれかのタイプのパリンドロームから発生し、10塩基対のブロック(1つのリンカーユニット)のブロック内でヌクレオチドを除去しましたが、パリンドローム配列からのみ、常に18塩基ペアの長いパリンドローム(1つのリンカーと8つの隣接する8つの底部が残っています。ベースペア)背後。あまり頻繁に発生する削除は、NBタイプのパリンドロムからのみ発生し、完全なパリンドローム配列と隣接するヌクレオチドを除去します。少なくとも最初のタイプの削除は、RECA活動がない場合に発生しました。我々の結果は、サイズとパリンドロムの遺伝的安定性、つまり十字形の安定性を低下させる可能性のあるシーケンスとの相関関係を示しています。これは、パリンドロームを十字形または十字形のような構造に押し出ることでパリンドロームの欠失が発生するという理論を支持します。
さまざまな長さとシーケンスのパリンドロムをバクテリオファージPhi X174ゲノムの非必須領域に挿入することにより、パリンドロームのサイズとシーケンスの遺伝的安定性の効果を調査しました。ECORIリンカーCCGAATTCGG(E)、BAMHIリンカーCCGGATCCGG(B)または両方の混合物(E、B)のサイズが増加するマルチマーは、以前に構築されたバクテリオファージ株PHI X174 J-F INS6のPVUII部位に挿入されました。遺伝的安定性を有意に喪失することなくゲノムで維持できる最大のインサートは、それぞれ2b、4e、および4(e、b)でした。このサイズを超えるポリマーは挿入できますが、ファージゲノムからの迅速かつ正確な欠失をもたらしました。これにより、NBはNEよりも不安定であり、NEはNよりも不安定でした(E、B)。結果として得られた欠失変異体の分析は、2つの異なるタイプの削除の証拠を提供しました。より頻繁な欠失は、いずれかのタイプのパリンドロームから発生し、10塩基対のブロック(1つのリンカーユニット)のブロック内でヌクレオチドを除去しましたが、パリンドローム配列からのみ、常に18塩基ペアの長いパリンドローム(1つのリンカーと8つの隣接する8つの底部が残っています。ベースペア)背後。あまり頻繁に発生する削除は、NBタイプのパリンドロムからのみ発生し、完全なパリンドローム配列と隣接するヌクレオチドを除去します。少なくとも最初のタイプの削除は、RECA活動がない場合に発生しました。我々の結果は、サイズとパリンドロムの遺伝的安定性、つまり十字形の安定性を低下させる可能性のあるシーケンスとの相関関係を示しています。これは、パリンドロームを十字形または十字形のような構造に押し出ることでパリンドロームの欠失が発生するという理論を支持します。
By inserting palindromes of varying length and sequence into a non-essential region of the bacteriophage phi X174 genome we have investigated the effect of palindrome size and sequence on their genetic stability. Multimers of increasing size of the EcoRI linker CCGAATTCGG (E), the BamHI linker CCGGATCCGG (B) or mixtures of both (E, B) were inserted into the PvuII site of a previously constructed bacteriophage strain phi X174 J-F ins6. The largest inserts that could be maintained in the genome without significant loss of genetic stability were 2B, 4E, and 4(E, B), respectively. Polymers exceeding this size could be inserted but resulted in rapid and precise deletion from the phage genome, whereby nB was more unstable than nE, and nE was more unstable than n(E, B). Analysis of the resulting deletion mutants provided evidence for two different types of deletions. The more frequent deletion arose from either type palindrome and removed nucleotides in blocks of ten base-pairs (one linker unit), but only from the palindromic sequence, and always left at least an 18 base-pair long palindrome (one linker plus 8 neighboring base-pairs) behind. The less frequently occurring deletions arose only from nB type palindromes, removing the complete palindromic sequence plus adjacent nucleotides. At least the first type of deletion occurred in the absence of recA activity. Our results show a correlation between the sequence, as well as size, and the genetic stability of palindromes, i.e. sequences that could decrease the stability of a cruciform increased their genetic stability. This supports the theory that palindrome deletion occurs via extrusion of the palindrome into a cruciform or cruciform-like structure.
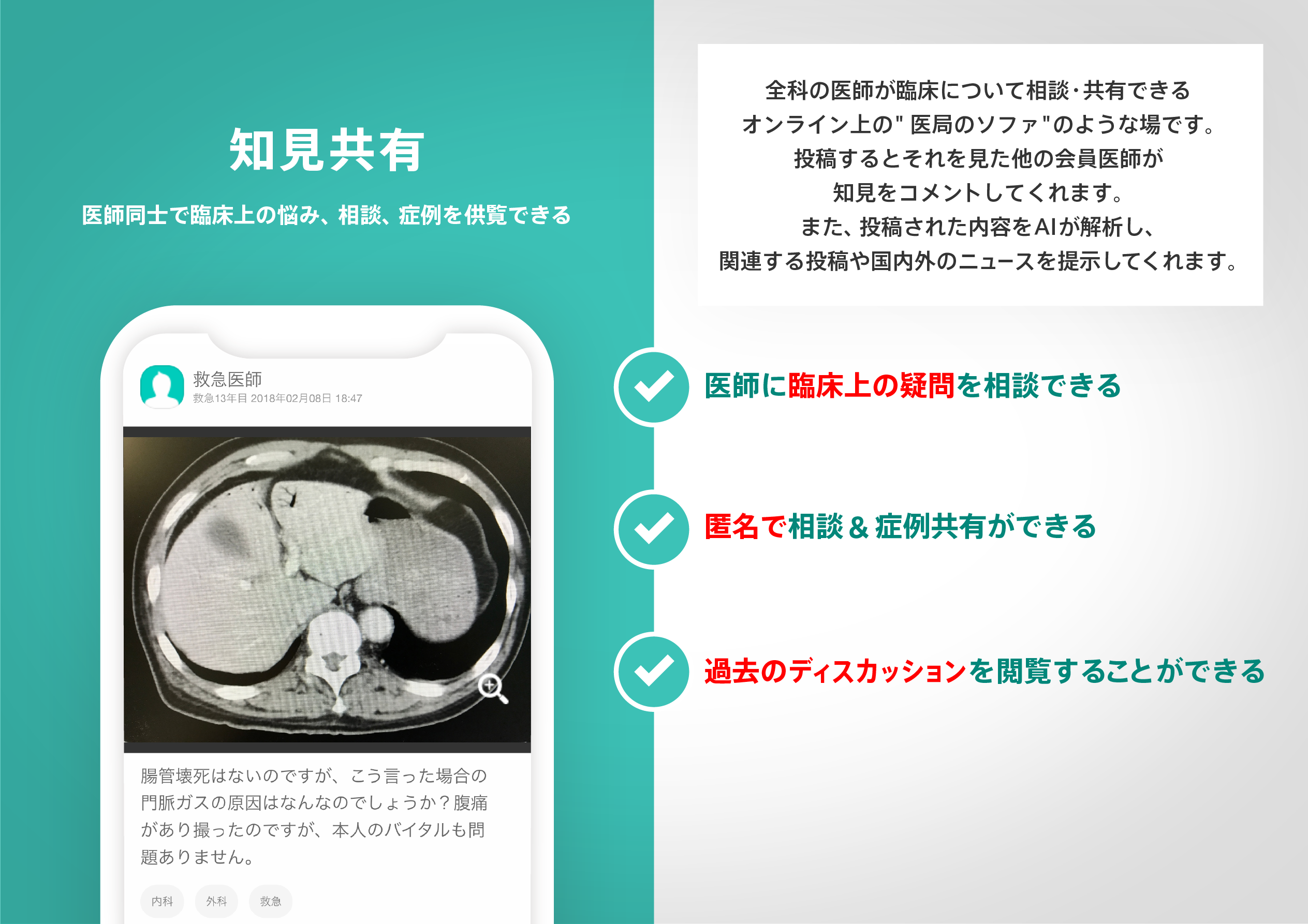
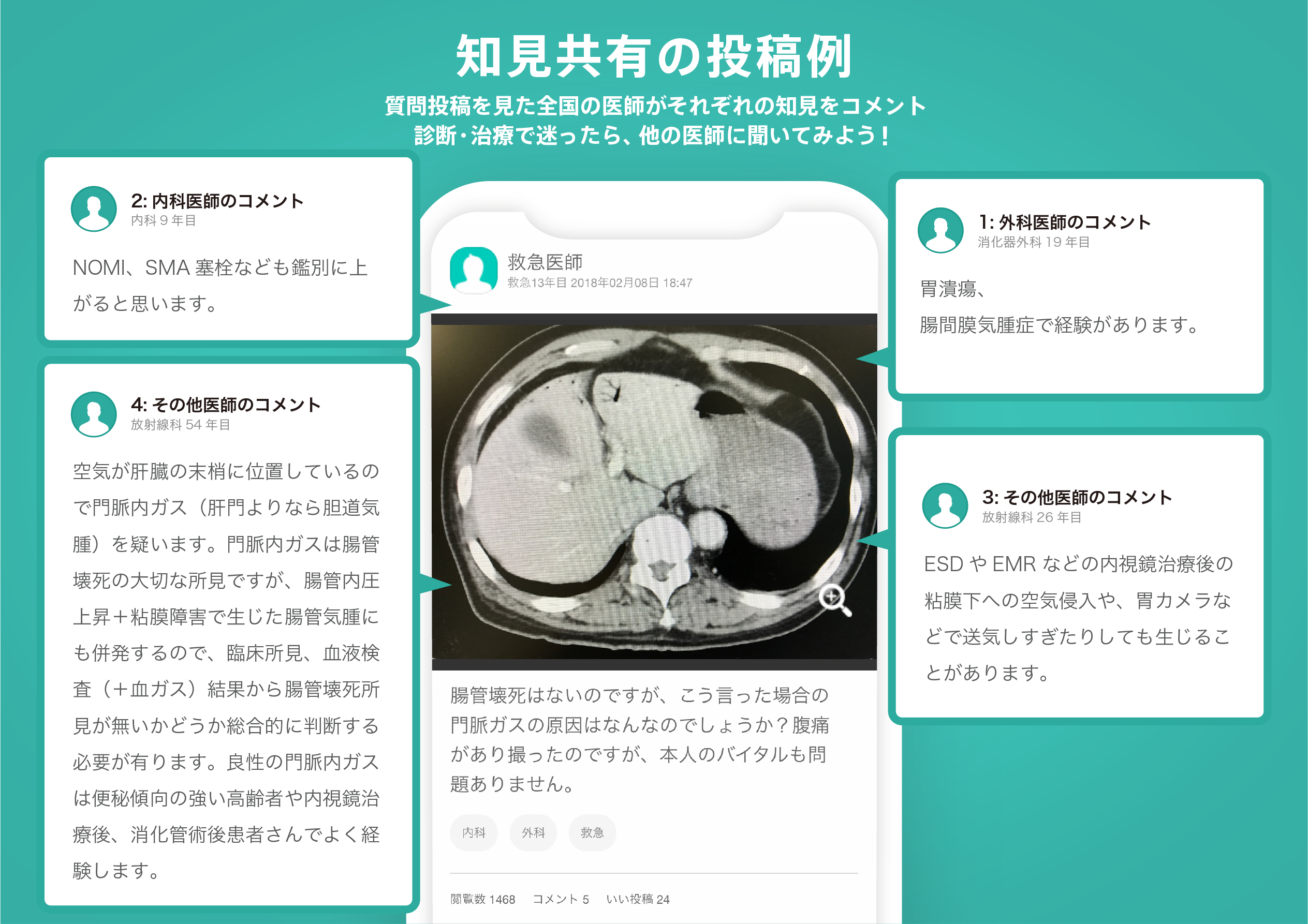
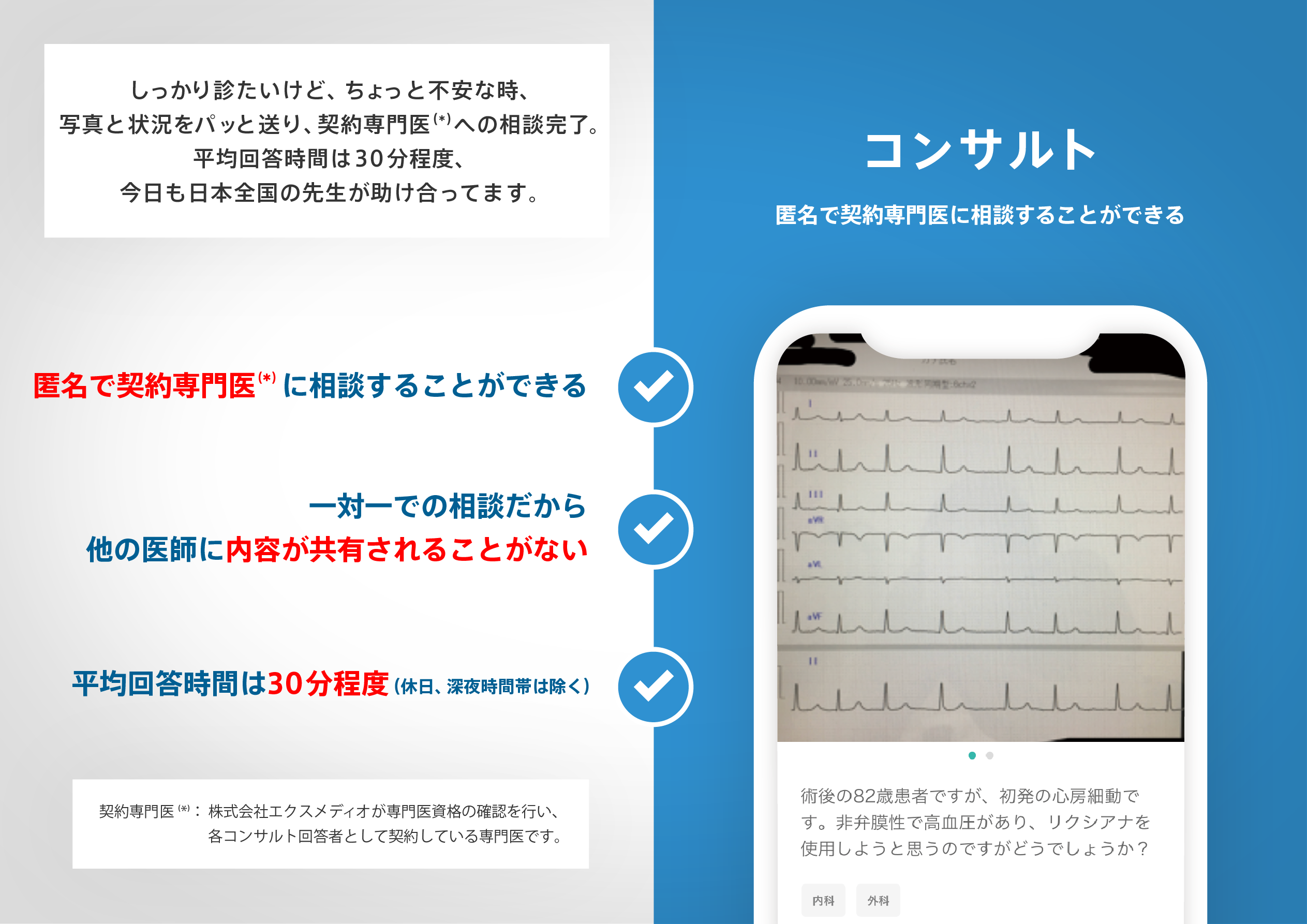
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。