著名医師による解説が無料で読めます
すると翻訳の精度が向上します
ポリミキシン耐性菌の増加する有病率は、ポリミキシンリポペプチドの改善の検索を刺激しました。ここでは、Paenibacillus polymyxa ATCC 10401のポリミキシンD非リボソームペプチドシンテターゼの配列と生成物プロファイルを説明します。PMXB、およびPMXE)。ポリミキシンBやEとは異なり、ポリミキシンDには、L-α、γ-ジアミノ酪酸とは対照的に、ポジション3にD-SERが含まれており、L-LEUではなく位置7にL-THRがあります。PMXEのモジュール3には、L-SERのd-formへの変換を触媒する補助エピマー化ドメインがありました。構造モデリングは、PMXEのモジュール3のアデニル化ドメインとPMXAのモジュール6および7のアデニル化ドメインが、好ましい基質よりも大きなサイドチェーンでアミノ酸を結合できることを示唆しました。個々のアミノ酸を培地に供給して、ポリミキシンD1およびD2の産生に影響を与えるだけでなく、ポリミキシンDの位置3、6、および7に異なるアミノ酸が組み込まれました。グラム陰性臨床分離株のパネルに対して、天然のポリミキシンD1とD2は優れたin vitro抗菌活性を示し、マウスの血液感染モデルで肺炎球とアシネトバクターbaumanniiに対して効果的でした。結果は、これらの異常なD-SER3ポリムキシンの優れた抗菌活性を示し、ポリミキシン非リボソーム生合成機構の操作を介してポリミキシンDの位置3、6、および7に代替アミノ酸を組み込む可能性を強調しています。
ポリミキシン耐性菌の増加する有病率は、ポリミキシンリポペプチドの改善の検索を刺激しました。ここでは、Paenibacillus polymyxa ATCC 10401のポリミキシンD非リボソームペプチドシンテターゼの配列と生成物プロファイルを説明します。PMXB、およびPMXE)。ポリミキシンBやEとは異なり、ポリミキシンDには、L-α、γ-ジアミノ酪酸とは対照的に、ポジション3にD-SERが含まれており、L-LEUではなく位置7にL-THRがあります。PMXEのモジュール3には、L-SERのd-formへの変換を触媒する補助エピマー化ドメインがありました。構造モデリングは、PMXEのモジュール3のアデニル化ドメインとPMXAのモジュール6および7のアデニル化ドメインが、好ましい基質よりも大きなサイドチェーンでアミノ酸を結合できることを示唆しました。個々のアミノ酸を培地に供給して、ポリミキシンD1およびD2の産生に影響を与えるだけでなく、ポリミキシンDの位置3、6、および7に異なるアミノ酸が組み込まれました。グラム陰性臨床分離株のパネルに対して、天然のポリミキシンD1とD2は優れたin vitro抗菌活性を示し、マウスの血液感染モデルで肺炎球とアシネトバクターbaumanniiに対して効果的でした。結果は、これらの異常なD-SER3ポリムキシンの優れた抗菌活性を示し、ポリミキシン非リボソーム生合成機構の操作を介してポリミキシンDの位置3、6、および7に代替アミノ酸を組み込む可能性を強調しています。
The increasing prevalence of polymyxin-resistant bacteria has stimulated the search for improved polymyxin lipopeptides. Here we describe the sequence and product profile for polymyxin D nonribosomal peptide synthetase from Paenibacillus polymyxa ATCC 10401. The polymyxin D synthase gene cluster comprised five genes that encoded ABC transporters (pmxC and pmxD) and enzymes responsible for the biosynthesis of polymyxin D (pmxA, pmxB, and pmxE). Unlike polymyxins B and E, polymyxin D contains d-Ser at position 3 as opposed to l-α,γ-diaminobutyric acid and has an l-Thr at position 7 rather than l-Leu. Module 3 of pmxE harbored an auxiliary epimerization domain that catalyzes the conversion of l-Ser to the d-form. Structural modeling suggested that the adenylation domains of module 3 in PmxE and modules 6 and 7 in PmxA could bind amino acids with larger side chains than their preferred substrate. Feeding individual amino acids into the culture media not only affected production of polymyxins D1 and D2 but also led to the incorporation of different amino acids at positions 3, 6, and 7 of polymyxin D. Interestingly, the unnatural polymyxin analogues did not show antibiotic activity against a panel of Gram-negative clinical isolates, while the natural polymyxins D1 and D2 exhibited excellent in vitro antibacterial activity and were efficacious against Klebsiella pneumoniae and Acinetobacter baumannii in a mouse blood infection model. The results demonstrate the excellent antibacterial activity of these unusual d-Ser3 polymxyins and underscore the possibility of incorporating alternate amino acids at positions 3, 6, and 7 of polymyxin D via manipulation of the polymyxin nonribosomal biosynthetic machinery.
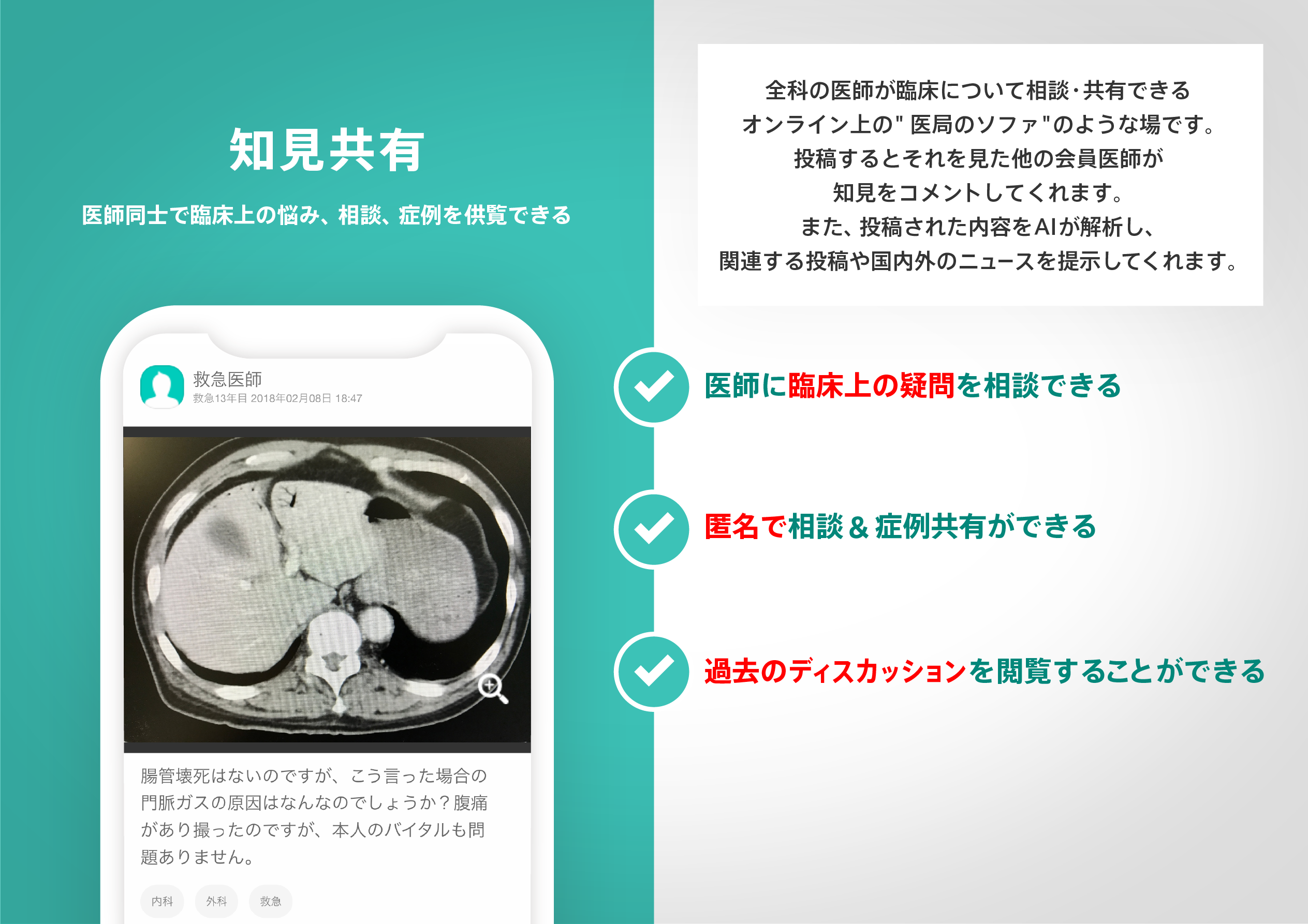
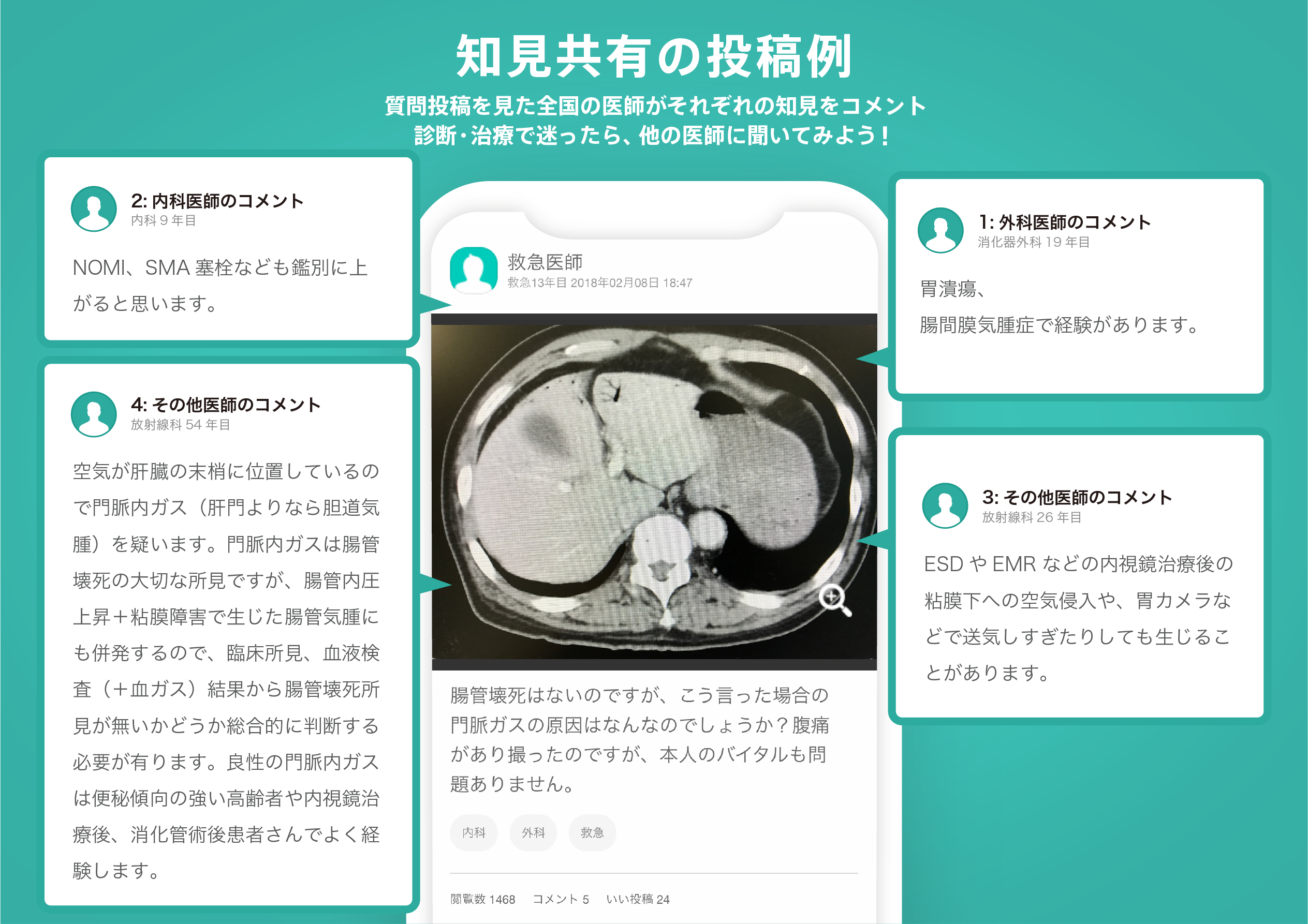
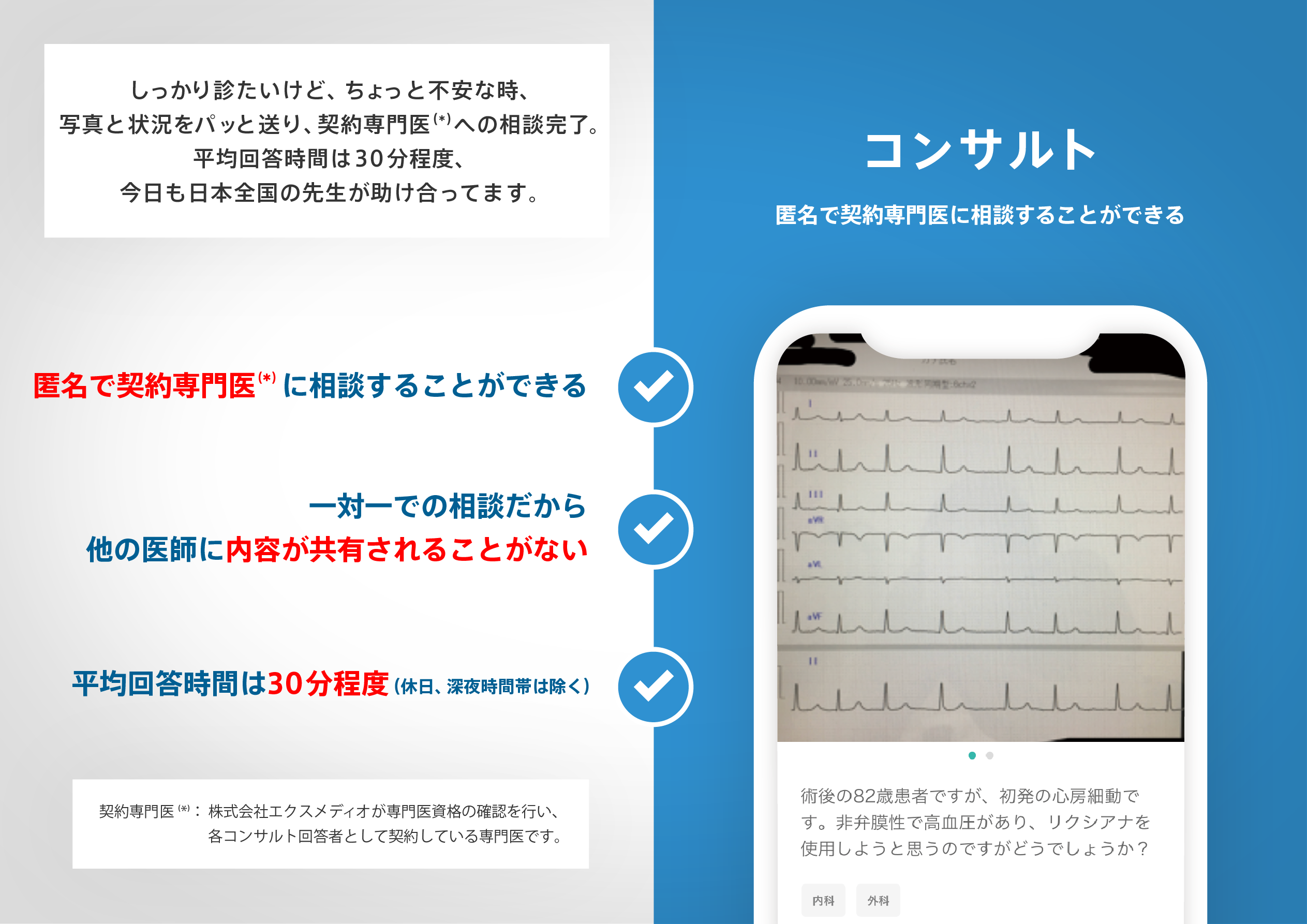
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。