著名医師による解説が無料で読めます
すると翻訳の精度が向上します
複雑なプロテオームの多重化された定量分析により、深い生物学的洞察が可能になります。多重化分析用に多数のワークフローが開発されていますが、最も定量的に正確な方法(SPS-MS3)は、長い取得義務サイクルに苦しんでいます。SPS-MS3メソッドの長いデューティサイクルと戦うために、新しいリアルタイムデータベース検索(RTS)プラットフォーム、Orbiterを構築しました。Orbiterを使用したRTは、特定のスペクトルに一致しない場合、SPS-MS3スキャンを排除します。RTSと誤検出率分析を含むOrbiterのオンラインプロテオーム分析パイプラインでは、10ミリ秒未満で単一のスペクトルデータベース検索を処理することができました。結果は、彗星を使用してペプチドスペクトルマッチを識別し、これらの一致をフィルタリングし、目的のタンパク質をより効率的に定量化するための高速で機能的な手段です。重要なことに、ペプチドスペクトルマッチングに彗星を使用することで、翻訳後の修飾の分析を含む、よく知られており、広範囲に検証されたスコアリングを含む、完全に機能する検索が可能になりました。これらのデータを使用して、適応的かつ柔軟な方法で後続のスキャンをトリガーできます。この作業では、この適応データ収集プラットフォームのユーティリティをテストして、多重化された定量的実験の効率と精度を改善しました。RTSにより、質量分析データ収集の効率が2倍増加することがわかりました。OrbiterのRTは、SPS-MS3分析の半分の時間で10個のプロテオームにわたって8000を超えるタンパク質を定量化しました(RTSで18時間、SPS-MS3で36時間)。
複雑なプロテオームの多重化された定量分析により、深い生物学的洞察が可能になります。多重化分析用に多数のワークフローが開発されていますが、最も定量的に正確な方法(SPS-MS3)は、長い取得義務サイクルに苦しんでいます。SPS-MS3メソッドの長いデューティサイクルと戦うために、新しいリアルタイムデータベース検索(RTS)プラットフォーム、Orbiterを構築しました。Orbiterを使用したRTは、特定のスペクトルに一致しない場合、SPS-MS3スキャンを排除します。RTSと誤検出率分析を含むOrbiterのオンラインプロテオーム分析パイプラインでは、10ミリ秒未満で単一のスペクトルデータベース検索を処理することができました。結果は、彗星を使用してペプチドスペクトルマッチを識別し、これらの一致をフィルタリングし、目的のタンパク質をより効率的に定量化するための高速で機能的な手段です。重要なことに、ペプチドスペクトルマッチングに彗星を使用することで、翻訳後の修飾の分析を含む、よく知られており、広範囲に検証されたスコアリングを含む、完全に機能する検索が可能になりました。これらのデータを使用して、適応的かつ柔軟な方法で後続のスキャンをトリガーできます。この作業では、この適応データ収集プラットフォームのユーティリティをテストして、多重化された定量的実験の効率と精度を改善しました。RTSにより、質量分析データ収集の効率が2倍増加することがわかりました。OrbiterのRTは、SPS-MS3分析の半分の時間で10個のプロテオームにわたって8000を超えるタンパク質を定量化しました(RTSで18時間、SPS-MS3で36時間)。
Multiplexed quantitative analyses of complex proteomes enable deep biological insight. While a multitude of workflows have been developed for multiplexed analyses, the most quantitatively accurate method (SPS-MS3) suffers from long acquisition duty cycles. We built a new, real-time database search (RTS) platform, Orbiter, to combat the SPS-MS3 method's longer duty cycles. RTS with Orbiter eliminates SPS-MS3 scans if no peptide matches to a given spectrum. With Orbiter's online proteomic analytical pipeline, which includes RTS and false discovery rate analysis, it was possible to process a single spectrum database search in less than 10 ms. The result is a fast, functional means to identify peptide spectral matches using Comet, filter these matches, and more efficiently quantify proteins of interest. Importantly, the use of Comet for peptide spectral matching allowed for a fully featured search, including analysis of post-translational modifications, with well-known and extensively validated scoring. These data could then be used to trigger subsequent scans in an adaptive and flexible manner. In this work we tested the utility of this adaptive data acquisition platform to improve the efficiency and accuracy of multiplexed quantitative experiments. We found that RTS enabled a 2-fold increase in mass spectrometric data acquisition efficiency. Orbiter's RTS quantified more than 8000 proteins across 10 proteomes in half the time of an SPS-MS3 analysis (18 h for RTS, 36 h for SPS-MS3).
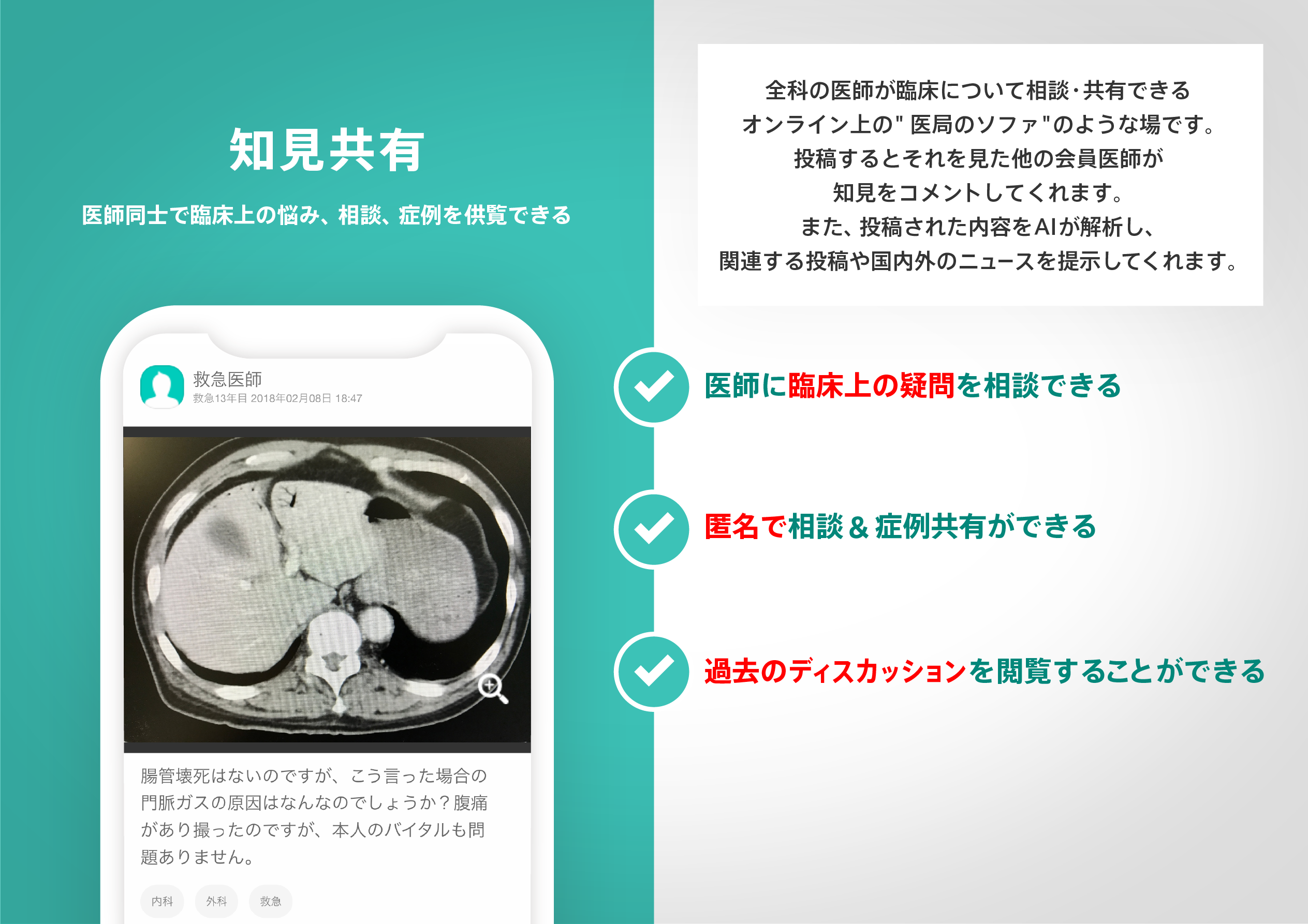
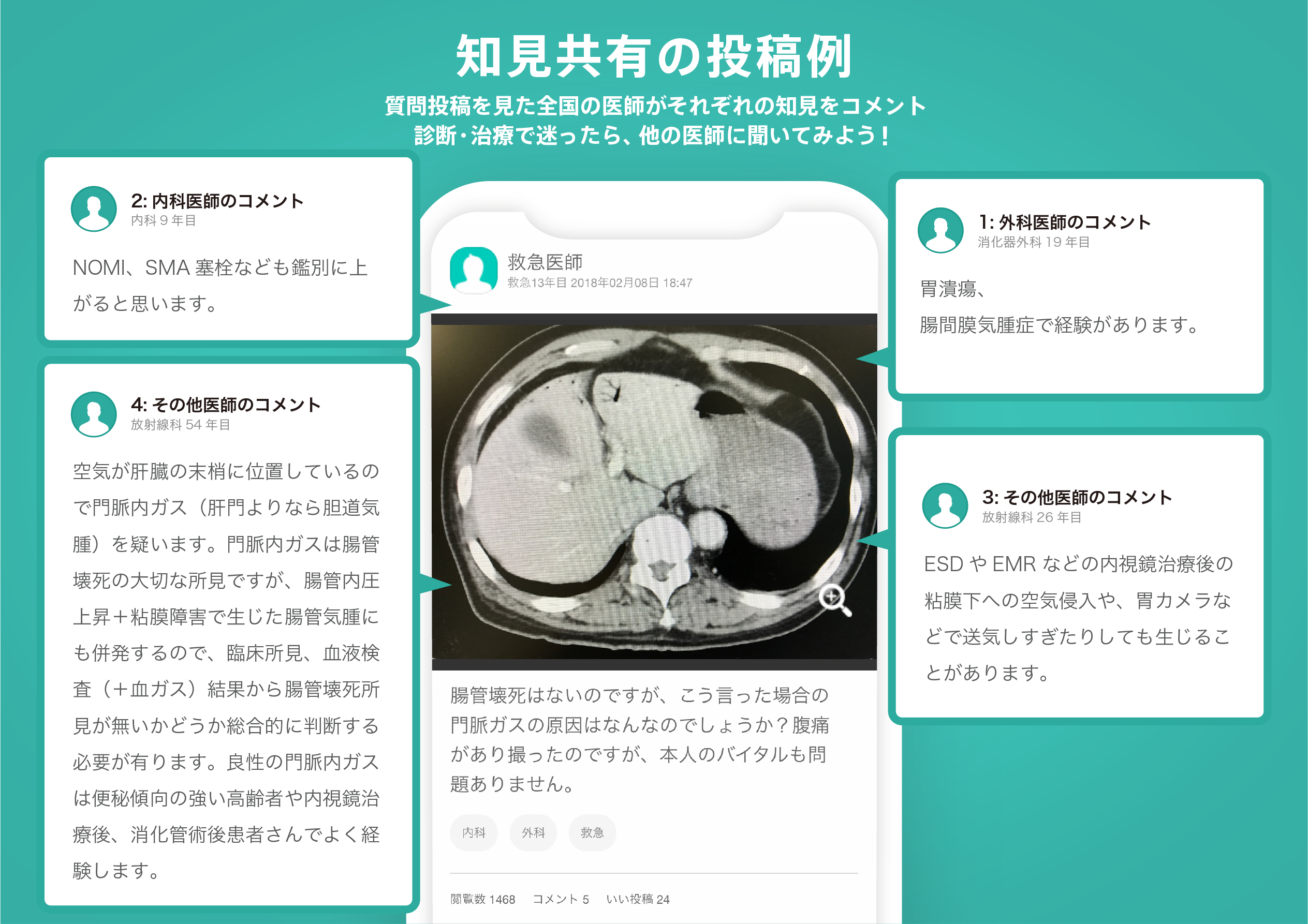
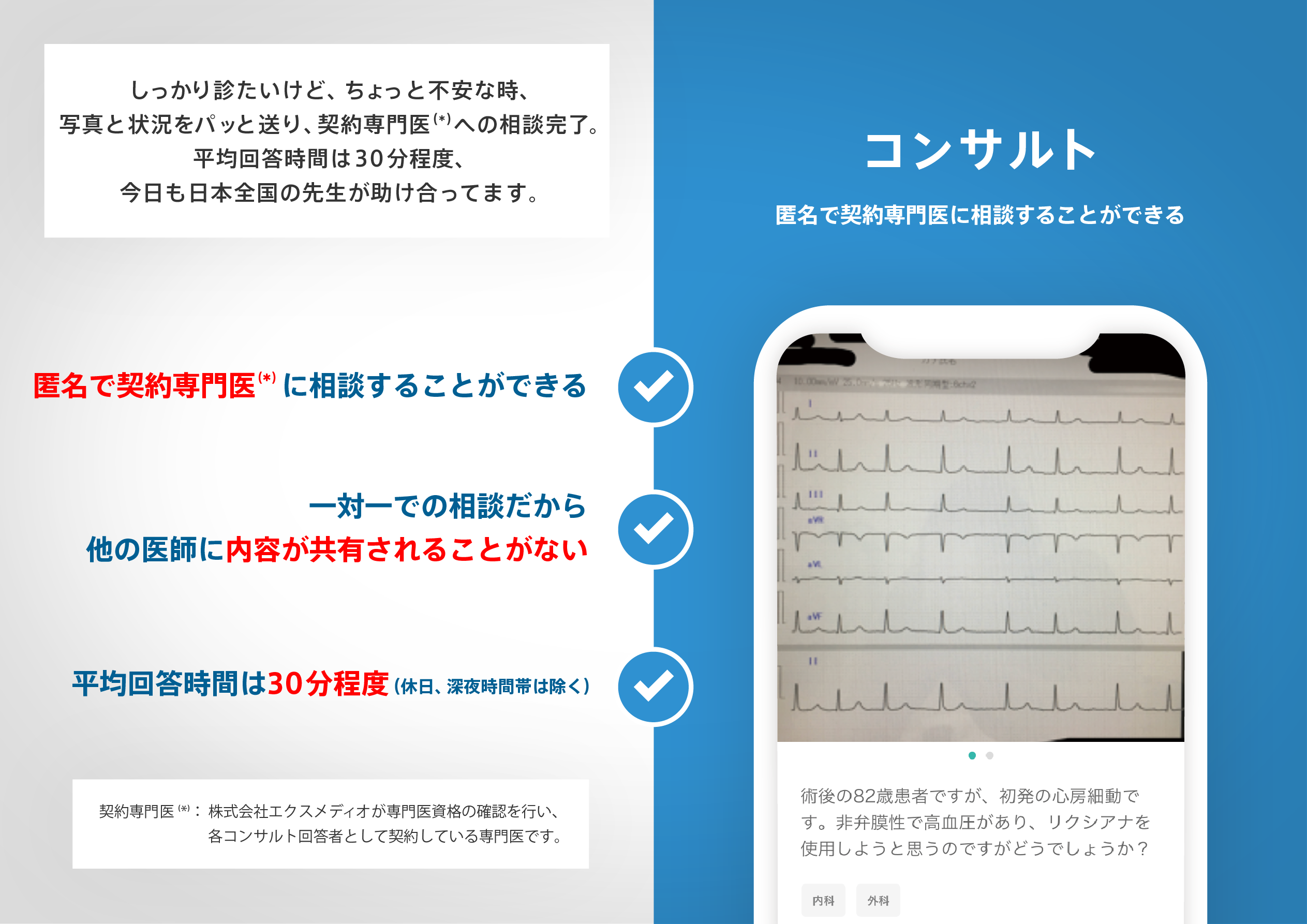
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。