著名医師による解説が無料で読めます
すると翻訳の精度が向上します
CRISPR/Cas9ヌクレアーゼは、さまざまな生物におけるゲノム編集に広く適用されています。ガイドRNA(Cas9-GRNA)で複合したCas9ヌクレアーゼは、GRNAを相補的に配列のゲノムDNAをスキャンして尋問することにより、標的を見つけます。DNAターゲット配列の認識には、このシーケンスの外側にある短いプロトススペーサー隣接モチーフ(PAM)が必要です。ターゲット位置の効率は、ターゲット認識を促進する相互作用の強度に依存する可能性があることを考えると、ここでは、同族のPAMシーケンスのさまざまなCas9ヌクレアーゼの親和性を比較しようとしました。この目的のために、ガイドRNA(GRNA)(SPCAS9-gRNA、SACAS9-GRNA、およびFNCAS9-gRNA)と3つのエンジニアリングSPCAS9-GRNAのGuide RNAS(GRNA)(SPCAS9-gRNA、FNCAS9-GRNAの複合化されたFrancisell novicidaから、Pyogenesストレプトコッカス、およびFrancisella novicidaからのCas9ヌクレアーゼの親和性を測定しました。PAMを含む短いDNAプローブのPAM特異性が変化したバリエーション。「Cas9ビーコン」と呼ばれる蛍光標識標的DNA誘導体へのCas9-grna結合速度に競争力のある速度に影響を与える能力を決定することにより、DNAプローブの相対的親和性を測定する「ビーコン」アッセイを使用しました。研究されたCAS9酵素間の同族PAM配列の親和性に有意差が観察されました。Spcas9-grnaおよびその標準的および準最適でないPAMのその設計されたバリアントの相対的な親和性は、ゲノム編集におけるこれらのPAMシーケンスの効率に関する以前の発見と相関していました。これらの発見は、その同族PAMに対するCas9ヌクレアーゼの高い親和性が、より高いゲノム編集効率を促進することを示唆しています。
CRISPR/Cas9ヌクレアーゼは、さまざまな生物におけるゲノム編集に広く適用されています。ガイドRNA(Cas9-GRNA)で複合したCas9ヌクレアーゼは、GRNAを相補的に配列のゲノムDNAをスキャンして尋問することにより、標的を見つけます。DNAターゲット配列の認識には、このシーケンスの外側にある短いプロトススペーサー隣接モチーフ(PAM)が必要です。ターゲット位置の効率は、ターゲット認識を促進する相互作用の強度に依存する可能性があることを考えると、ここでは、同族のPAMシーケンスのさまざまなCas9ヌクレアーゼの親和性を比較しようとしました。この目的のために、ガイドRNA(GRNA)(SPCAS9-gRNA、SACAS9-GRNA、およびFNCAS9-gRNA)と3つのエンジニアリングSPCAS9-GRNAのGuide RNAS(GRNA)(SPCAS9-gRNA、FNCAS9-GRNAの複合化されたFrancisell novicidaから、Pyogenesストレプトコッカス、およびFrancisella novicidaからのCas9ヌクレアーゼの親和性を測定しました。PAMを含む短いDNAプローブのPAM特異性が変化したバリエーション。「Cas9ビーコン」と呼ばれる蛍光標識標的DNA誘導体へのCas9-grna結合速度に競争力のある速度に影響を与える能力を決定することにより、DNAプローブの相対的親和性を測定する「ビーコン」アッセイを使用しました。研究されたCAS9酵素間の同族PAM配列の親和性に有意差が観察されました。Spcas9-grnaおよびその標準的および準最適でないPAMのその設計されたバリアントの相対的な親和性は、ゲノム編集におけるこれらのPAMシーケンスの効率に関する以前の発見と相関していました。これらの発見は、その同族PAMに対するCas9ヌクレアーゼの高い親和性が、より高いゲノム編集効率を促進することを示唆しています。
The CRISPR/Cas9 nucleases have been widely applied for genome editing in various organisms. Cas9 nucleases complexed with a guide RNA (Cas9-gRNA) find their targets by scanning and interrogating the genomic DNA for sequences complementary to the gRNA. Recognition of the DNA target sequence requires a short protospacer adjacent motif (PAM) located outside this sequence. Given that the efficiency of target location may depend on the strength of interactions that promote target recognition, here we sought to compare affinities of different Cas9 nucleases for their cognate PAM sequences. To this end, we measured affinities of Cas9 nucleases from Streptococcus pyogenes, Staphylococcus aureus, and Francisella novicida complexed with guide RNAs (gRNAs) (SpCas9-gRNA, SaCas9-gRNA, and FnCas9-gRNA, respectively) and of three engineered SpCas9-gRNA variants with altered PAM specificities for short, PAM-containing DNA probes. We used a "beacon" assay that measures the relative affinities of DNA probes by determining their ability to competitively affect the rate of Cas9-gRNA binding to fluorescently labeled target DNA derivatives called "Cas9 beacons." We observed significant differences in the affinities for cognate PAM sequences among the studied Cas9 enzymes. The relative affinities of SpCas9-gRNA and its engineered variants for canonical and suboptimal PAMs correlated with previous findings on the efficiency of these PAM sequences in genome editing. These findings suggest that high affinity of a Cas9 nuclease for its cognate PAM promotes higher genome-editing efficiency.
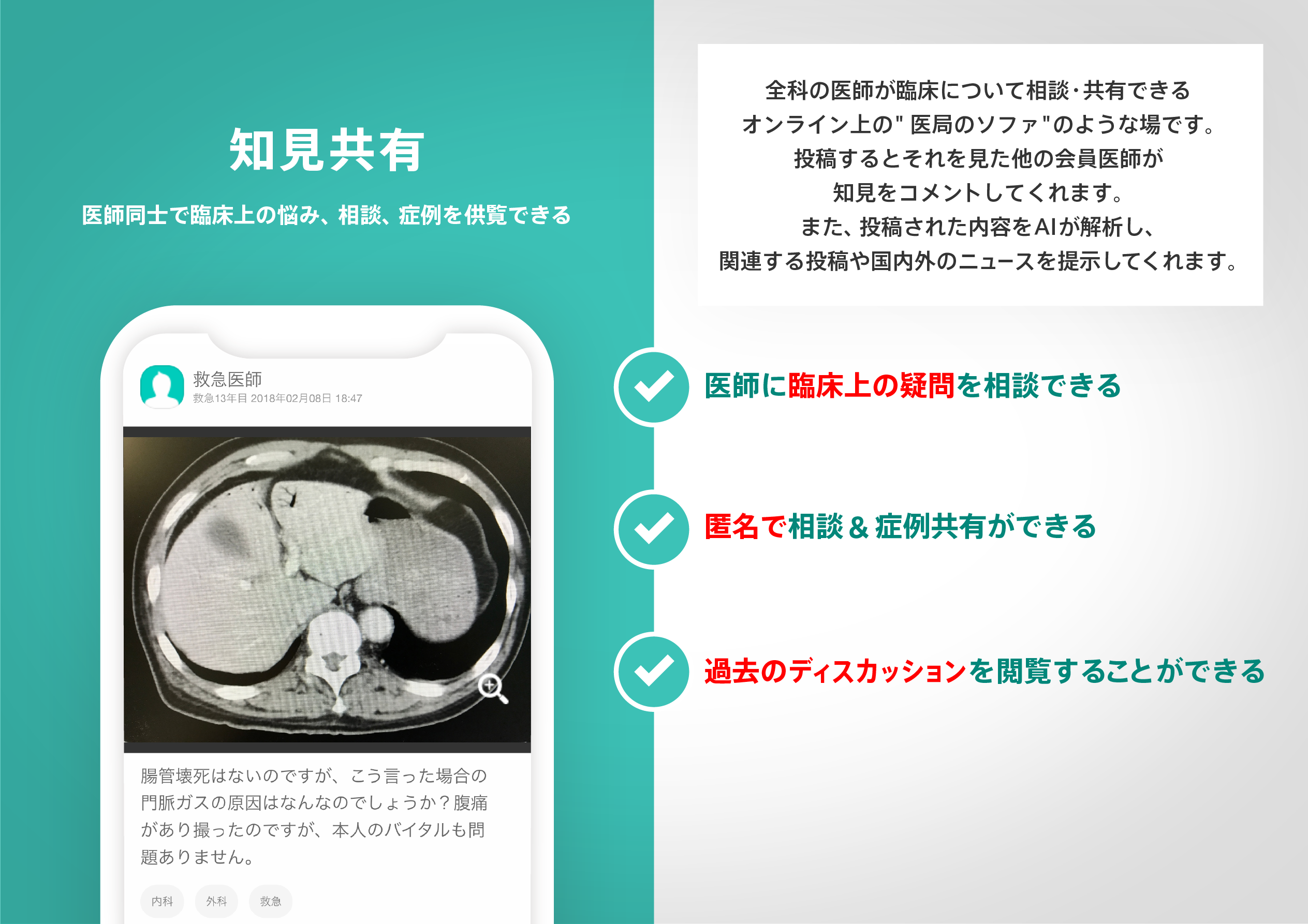
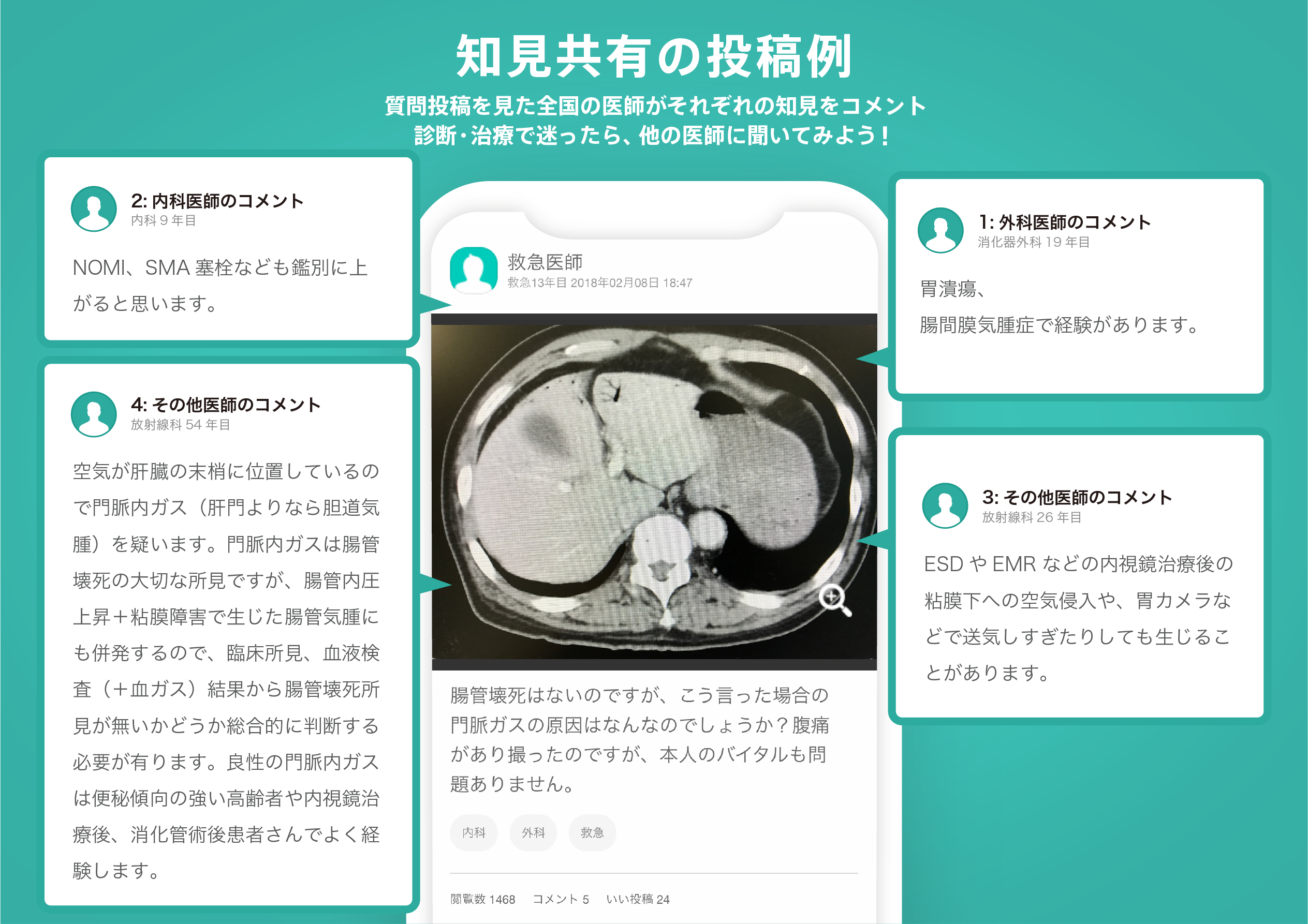
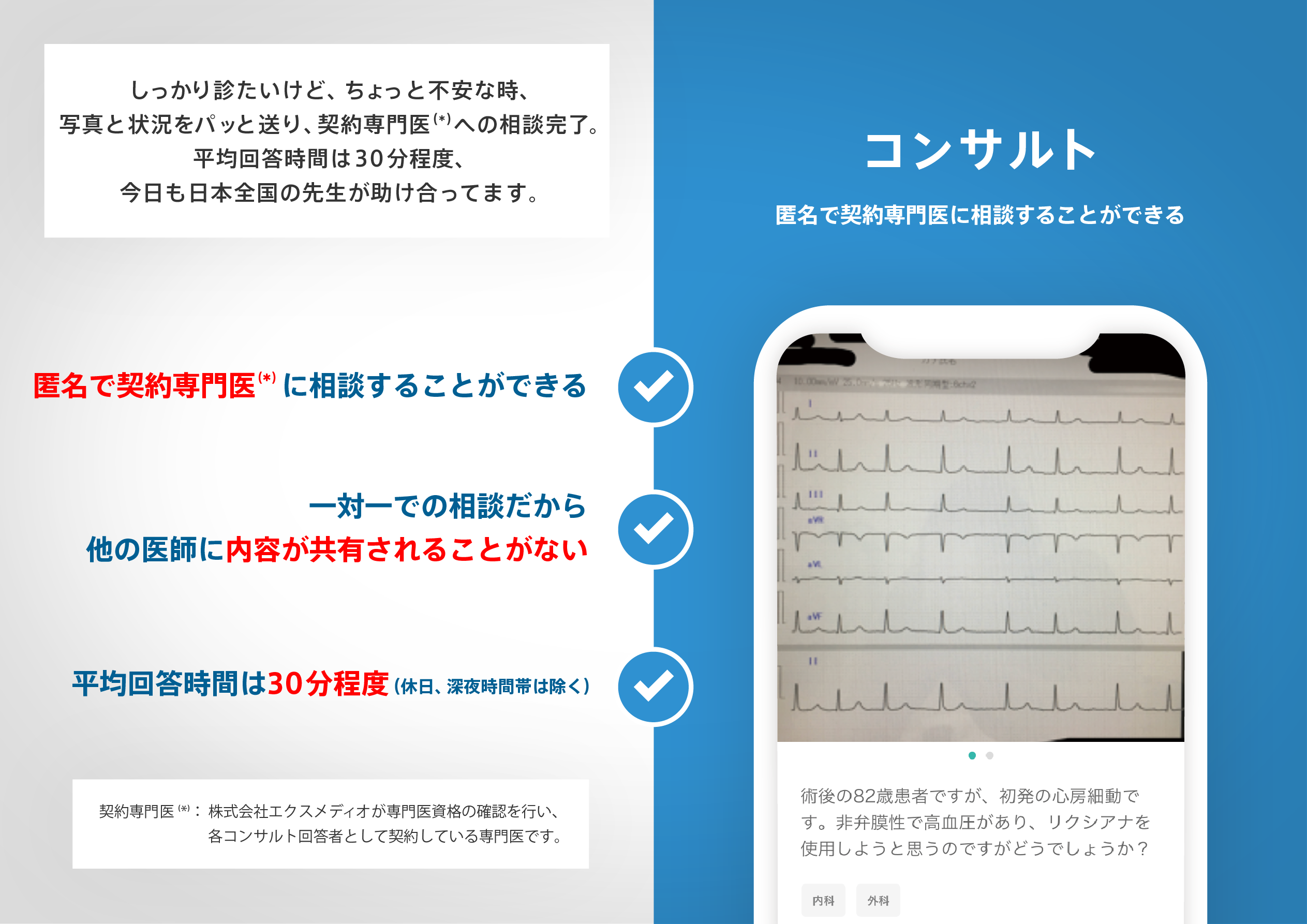
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。