著名医師による解説が無料で読めます
すると翻訳の精度が向上します
タンパク質の役割を評価するために、最も一般的には変異誘発RNAiまたはCRISPRノックアウトを介して、タンパク質損失の表現型研究を使用できます。このような研究は、タンパク質機能の理解と、多くのヒト疾患状態の推定治療標的の同定に重要でした。しかし、これらの方法論的アプローチは、それらが容易に可逆的ではないため、課題を提示します。そして、必須遺伝子が標的にされている場合、関連する細胞生存率の損失はさらなる研究を妨げる可能性があります。ここでは、多数のタンパク質に適用できる可逆的で条件付きライブセルノックアウト戦略を提示します。このモジュール式タンパク質タグ付けアプローチは、VHL E3リガーゼ成分の動員を介してハロタグ融合タンパク質を特異的に分解するHaloprotac3の使用を通じて、ゲノムではなくタンパク質のターゲット損失を調節します。内因性タンパク質のハロタグ媒介分解を有効にするために、CRISPR/CAS9を介してタンパク質NまたはC末端でハロタグゲノム挿入のプロトコルを提供し、ハロタグ蛍光リガンドを使用して、蛍光活性化細胞選別(FACS)を介して編集された細胞を濃縮します。これらのアプローチを使用して、さまざまな細胞内位置に存在する内因性ハロタグ融合タンパク質は、Haloprotac3によって分解される可能性があります。内因性ターゲットの分解を検出することは困難であるため、11アミノ酸ペプチドタグHIBITがハロタグ融合に追加され、抗体を使用せずにハロタグ融合レベルの敏感な発光検出が可能になります。最後に、Haloprotac3の分解と別の融合タグProtac、DTAG-13の分解と比較することにより、Haloprotac3はより速い分解速度と類似の分解程度を持っていることを実証します。©2020著者。基本プロトコル1:CRISPR/CAS9 HalotagまたはHibit-Halotag Basic Protocol 2:Haloprotac3内因性ハロータグ融合の分解。
タンパク質の役割を評価するために、最も一般的には変異誘発RNAiまたはCRISPRノックアウトを介して、タンパク質損失の表現型研究を使用できます。このような研究は、タンパク質機能の理解と、多くのヒト疾患状態の推定治療標的の同定に重要でした。しかし、これらの方法論的アプローチは、それらが容易に可逆的ではないため、課題を提示します。そして、必須遺伝子が標的にされている場合、関連する細胞生存率の損失はさらなる研究を妨げる可能性があります。ここでは、多数のタンパク質に適用できる可逆的で条件付きライブセルノックアウト戦略を提示します。このモジュール式タンパク質タグ付けアプローチは、VHL E3リガーゼ成分の動員を介してハロタグ融合タンパク質を特異的に分解するHaloprotac3の使用を通じて、ゲノムではなくタンパク質のターゲット損失を調節します。内因性タンパク質のハロタグ媒介分解を有効にするために、CRISPR/CAS9を介してタンパク質NまたはC末端でハロタグゲノム挿入のプロトコルを提供し、ハロタグ蛍光リガンドを使用して、蛍光活性化細胞選別(FACS)を介して編集された細胞を濃縮します。これらのアプローチを使用して、さまざまな細胞内位置に存在する内因性ハロタグ融合タンパク質は、Haloprotac3によって分解される可能性があります。内因性ターゲットの分解を検出することは困難であるため、11アミノ酸ペプチドタグHIBITがハロタグ融合に追加され、抗体を使用せずにハロタグ融合レベルの敏感な発光検出が可能になります。最後に、Haloprotac3の分解と別の融合タグProtac、DTAG-13の分解と比較することにより、Haloprotac3はより速い分解速度と類似の分解程度を持っていることを実証します。©2020著者。基本プロトコル1:CRISPR/CAS9 HalotagまたはHibit-Halotag Basic Protocol 2:Haloprotac3内因性ハロータグ融合の分解。
To assess the role of a protein, protein loss phenotypic studies can be used, most commonly through mutagenesis RNAi or CRISPR knockout. Such studies have been critical for the understanding of protein function and the identification of putative therapeutic targets for numerous human disease states. However, these methodological approaches present challenges because they are not easily reversible, and if an essential gene is targeted, an associated loss of cell viability can potentially hinder further studies. Here we present a reversible and conditional live-cell knockout strategy that is applicable to numerous proteins. This modular protein-tagging approach regulates target loss at the protein, rather than the genomic, level through the use of HaloPROTAC3, which specifically degrades HaloTag fusion proteins via recruitment of the VHL E3 ligase component. To enable HaloTag-mediated degradation of endogenous proteins, we provide protocols for HaloTag genomic insertion at the protein N or C terminus via CRISPR/Cas9 and use of HaloTag fluorescent ligands to enrich edited cells via Fluorescence-Activated Cell Sorting (FACS). Using these approaches, endogenous HaloTag fusion proteins present in various subcellular locations can be degraded by HaloPROTAC3. As detecting the degradation of endogenous targets is challenging, the 11-amino-acid peptide tag HiBiT is added to the HaloTag fusion to allows the sensitive luminescence detection of HaloTag fusion levels without the use of antibodies. Lastly, we demonstrate, through comparison of HaloPROTAC3 degradation with that of another fusion tag PROTAC, dTAG-13, that HaloPROTAC3 has a faster degradation rate and similar extent of degradation. © 2020 The Authors. Basic Protocol 1: CRISPR/Cas9 insertion of HaloTag or HiBiT-HaloTag Basic Protocol 2: HaloPROTAC3 degradation of endogenous HaloTag fusions.
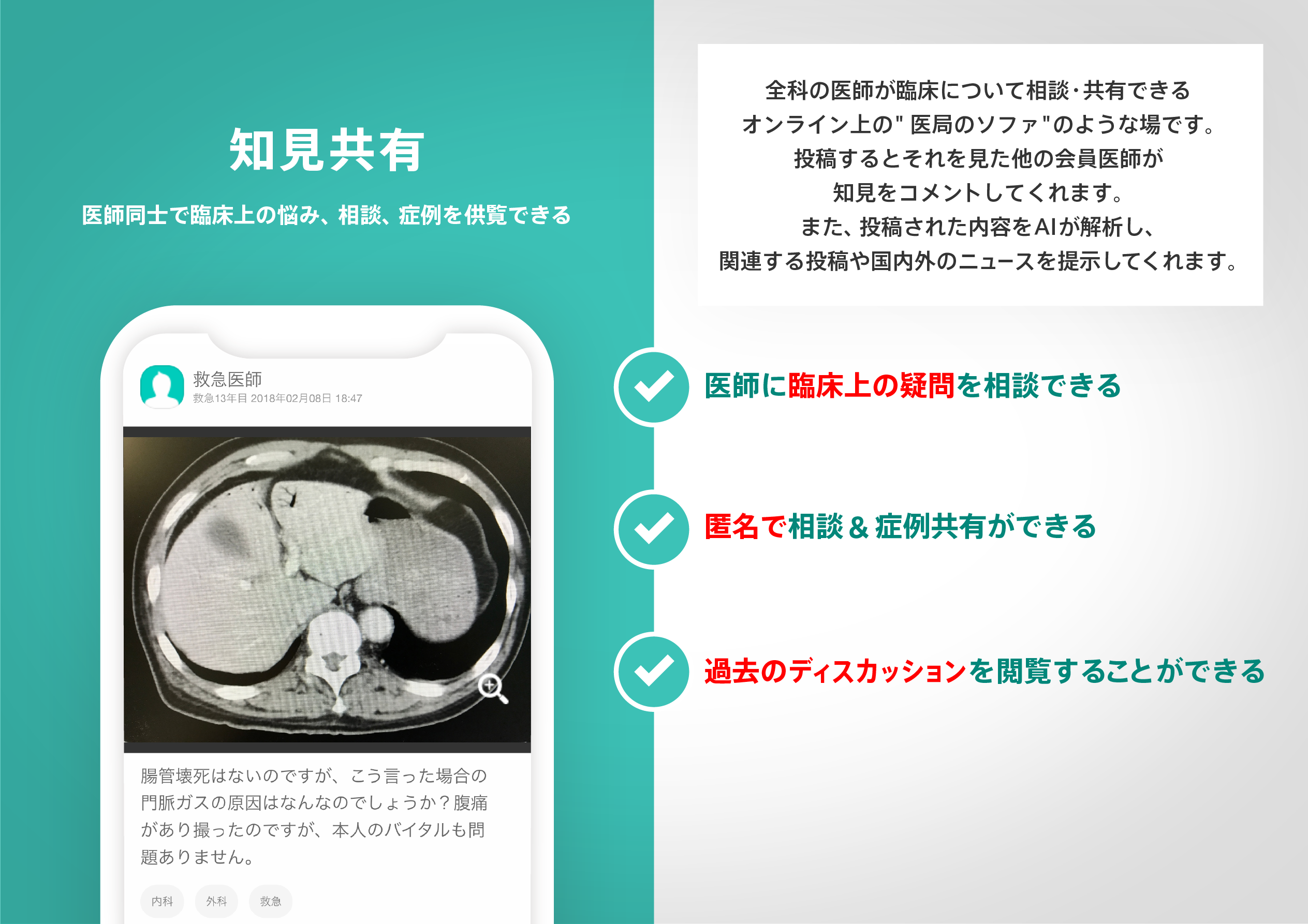
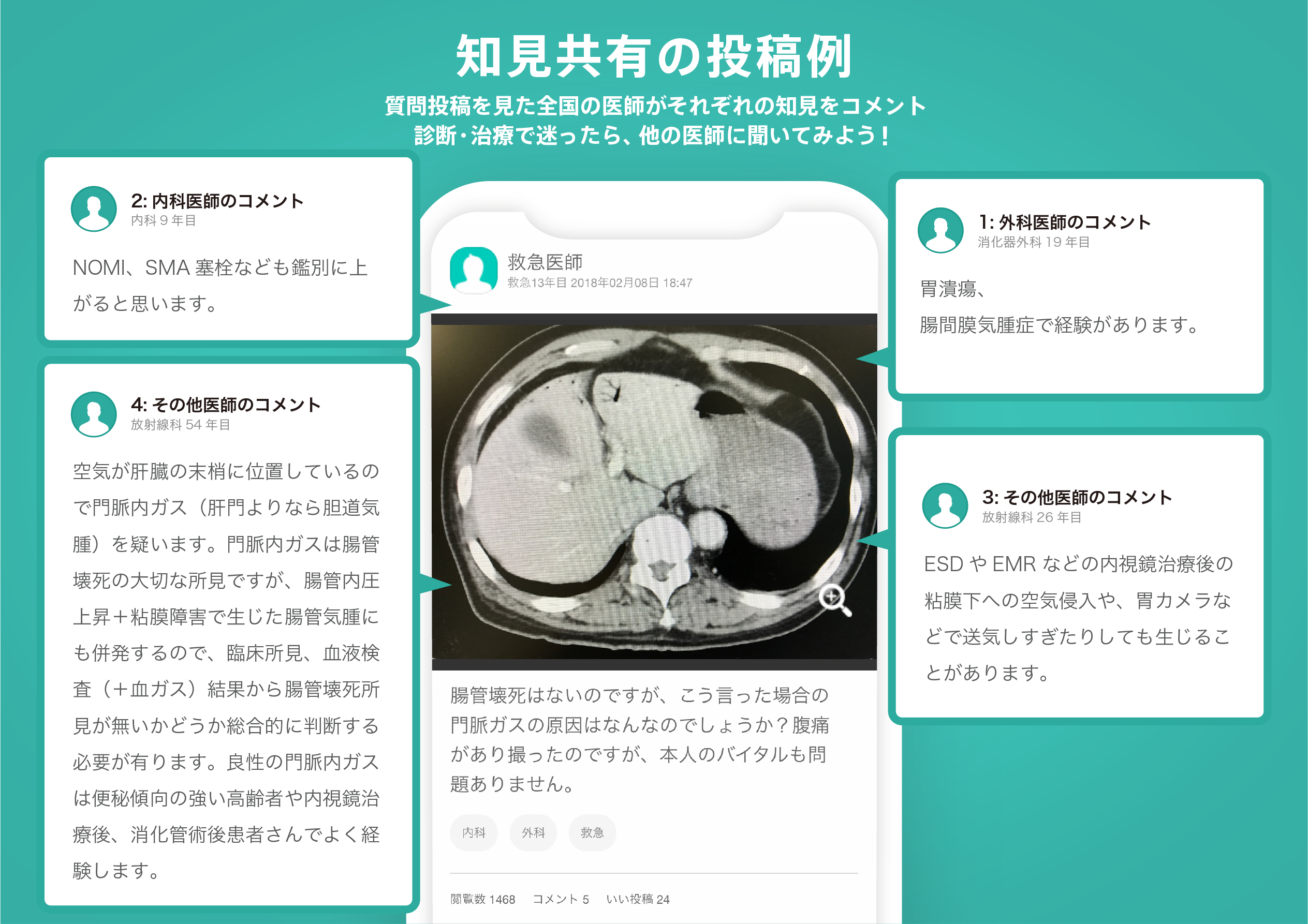
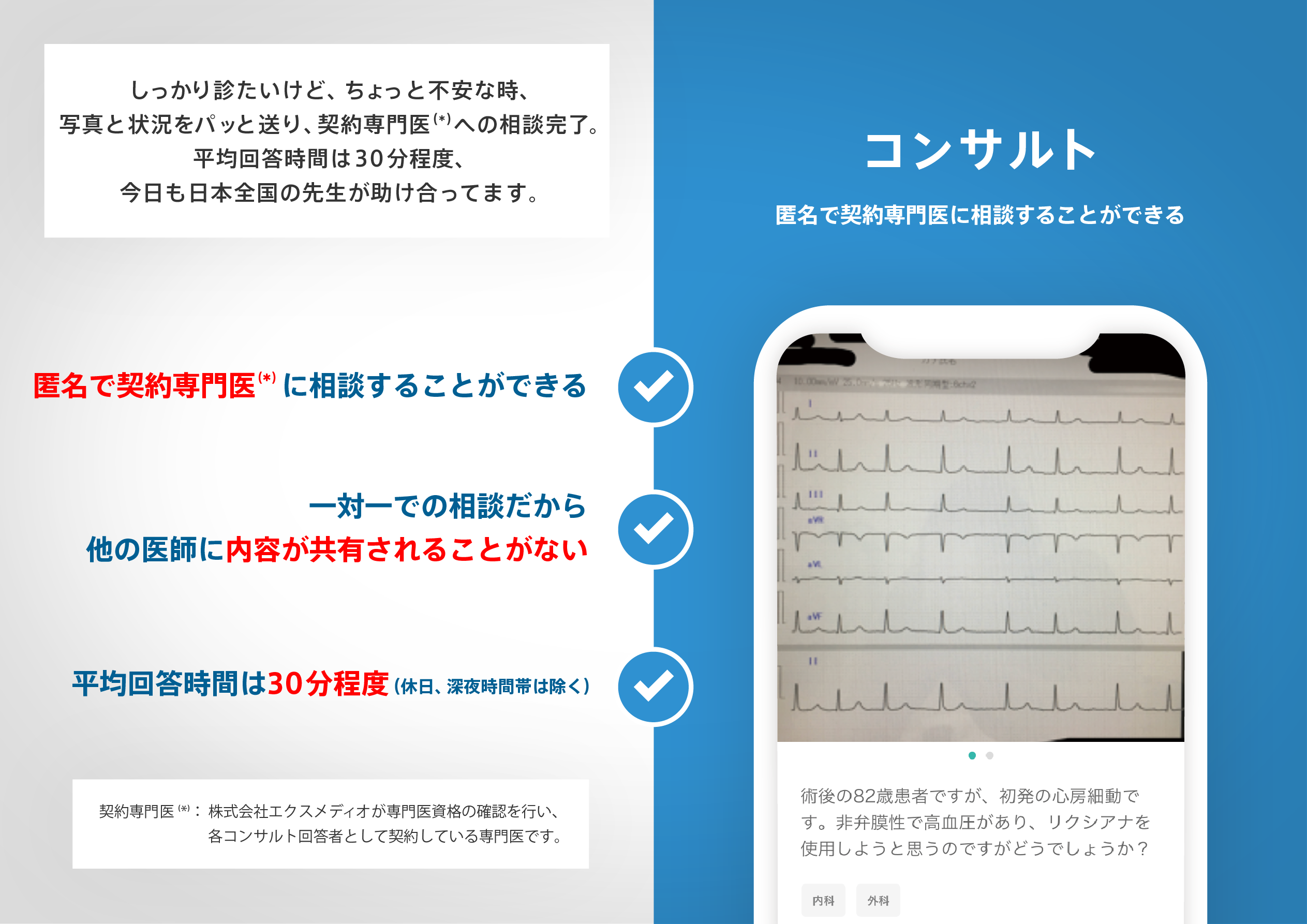
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。