著名医師による解説が無料で読めます
すると翻訳の精度が向上します
トランスクリプトームデータから生物学的意味を推測するために、同じレギュレーター、つまりレギュロンによって制御される遺伝子に焦点を当てることが有用です。残念ながら、現在の遺伝子セット濃縮分析(GSEA)ツールは、レギュレーターによって遺伝子が活性化されるか抑制されるかを考慮していません。レギュロンが特定の遺伝子の活性化因子として、また他の遺伝子の抑制因子として機能する可能性があるため、レギュロンを分析する場合、この区別は重要ですが、両方の遺伝子セットは同じレギュロンに属します。したがって、そのようなレギュロンの遺伝子の発現の違いを平均化するだけでは、レギュレータの活性を適切に反映しません。それをより複雑にしているのは、多くの遺伝子が異なる転写因子によって調節されているという事実であり、現在のトランスクリプトーム分析ツールは、どのレギュレータが遺伝子の観察された発現違いの原因であるかを示すことができないということです。これらの課題に対処するために、遺伝子セット濃縮分析プログラムGintoolを開発しました。Gintoolの追加機能は、トランスクリプトームデータの遺伝子セット分析の視覚化、分析の遺伝子セットとして機能カテゴリを含める可能性、およびオペロン内の発現違いを分析するオプションを促進するための新しいグラフィカルな表現です。また、プロテオームデータ。細胞内のすべての遺伝子の活性を想像することは、遺伝子の機能と調節を解明する一般的な方法です。ゲノムには何千もの遺伝子が含まれているため、これらのトランスクリプトーム分析は大量のデータを生成します。これらの大規模なデータセットの分析は困難です。したがって、Gintoolという新しいソフトウェアツールを開発し、同じレギュレーターであるいわゆるレギュロンによって制御された遺伝子セットの事前知識を使用して、トランスクリプトームデータの分析を促進できます。Gintoolの重要な斬新さは、これらの分析における遺伝子調節の方向性、つまり遺伝子が活性化されるか抑制されるかを考慮することができることです。これは、レギュロンまたは機能的カテゴリが影響を受けるかどうかを評価するために重要です。Gintoolには、トランスクリプトームデータセットの規制イベントの目視検査を促進するための新しいグラフィカルな方法も含まれています。Gintoolに含まれるこれらおよび追加の分析方法により、トランスクリプトームデータを分析するための強力なソフトウェアツールになります。
トランスクリプトームデータから生物学的意味を推測するために、同じレギュレーター、つまりレギュロンによって制御される遺伝子に焦点を当てることが有用です。残念ながら、現在の遺伝子セット濃縮分析(GSEA)ツールは、レギュレーターによって遺伝子が活性化されるか抑制されるかを考慮していません。レギュロンが特定の遺伝子の活性化因子として、また他の遺伝子の抑制因子として機能する可能性があるため、レギュロンを分析する場合、この区別は重要ですが、両方の遺伝子セットは同じレギュロンに属します。したがって、そのようなレギュロンの遺伝子の発現の違いを平均化するだけでは、レギュレータの活性を適切に反映しません。それをより複雑にしているのは、多くの遺伝子が異なる転写因子によって調節されているという事実であり、現在のトランスクリプトーム分析ツールは、どのレギュレータが遺伝子の観察された発現違いの原因であるかを示すことができないということです。これらの課題に対処するために、遺伝子セット濃縮分析プログラムGintoolを開発しました。Gintoolの追加機能は、トランスクリプトームデータの遺伝子セット分析の視覚化、分析の遺伝子セットとして機能カテゴリを含める可能性、およびオペロン内の発現違いを分析するオプションを促進するための新しいグラフィカルな表現です。また、プロテオームデータ。細胞内のすべての遺伝子の活性を想像することは、遺伝子の機能と調節を解明する一般的な方法です。ゲノムには何千もの遺伝子が含まれているため、これらのトランスクリプトーム分析は大量のデータを生成します。これらの大規模なデータセットの分析は困難です。したがって、Gintoolという新しいソフトウェアツールを開発し、同じレギュレーターであるいわゆるレギュロンによって制御された遺伝子セットの事前知識を使用して、トランスクリプトームデータの分析を促進できます。Gintoolの重要な斬新さは、これらの分析における遺伝子調節の方向性、つまり遺伝子が活性化されるか抑制されるかを考慮することができることです。これは、レギュロンまたは機能的カテゴリが影響を受けるかどうかを評価するために重要です。Gintoolには、トランスクリプトームデータセットの規制イベントの目視検査を促進するための新しいグラフィカルな方法も含まれています。Gintoolに含まれるこれらおよび追加の分析方法により、トランスクリプトームデータを分析するための強力なソフトウェアツールになります。
To infer the biological meaning from transcriptome data, it is useful to focus on genes that are regulated by the same regulator, i.e., regulons. Unfortunately, current gene set enrichment analysis (GSEA) tools do not consider whether a gene is activated or repressed by a regulator. This distinction is crucial when analyzing regulons since a regulator can work as an activator of certain genes and as a repressor of other genes, yet both sets of genes belong to the same regulon. Therefore, simply averaging expression differences of the genes of such a regulon will not properly reflect the activity of the regulator. What makes it more complicated is the fact that many genes are regulated by different transcription factors, and current transcriptome analysis tools are unable to indicate which regulator is most likely responsible for the observed expression difference of a gene. To address these challenges, we developed the gene set enrichment analysis program GINtool. Additional features of GINtool are novel graphical representations to facilitate the visualization of gene set analyses of transcriptome data, the possibility to include functional categories as gene sets for analysis, and the option to analyze expression differences within operons, which is useful when analyzing prokaryotic transcriptome and also proteome data.IMPORTANCEMeasuring the activity of all genes in cells is a common way to elucidate the function and regulation of genes. These transcriptome analyses produce large amounts of data since genomes contain thousands of genes. The analysis of these large data sets is challenging. Therefore, we developed a new software tool called GINtool that can facilitate the analysis of transcriptome data by using prior knowledge of gene sets controlled by the same regulator, the so-called regulons. An important novelty of GINtool is that it can take into account the directionality of gene regulation in these analyses, i.e., whether a gene is activated or repressed, which is crucial to assess whether a regulon or functional category is affected. GINtool also includes new graphical methods to facilitate the visual inspection of regulation events in transcriptome data sets. These and additional analysis methods included in GINtool make it a powerful software tool to analyze transcriptome data.
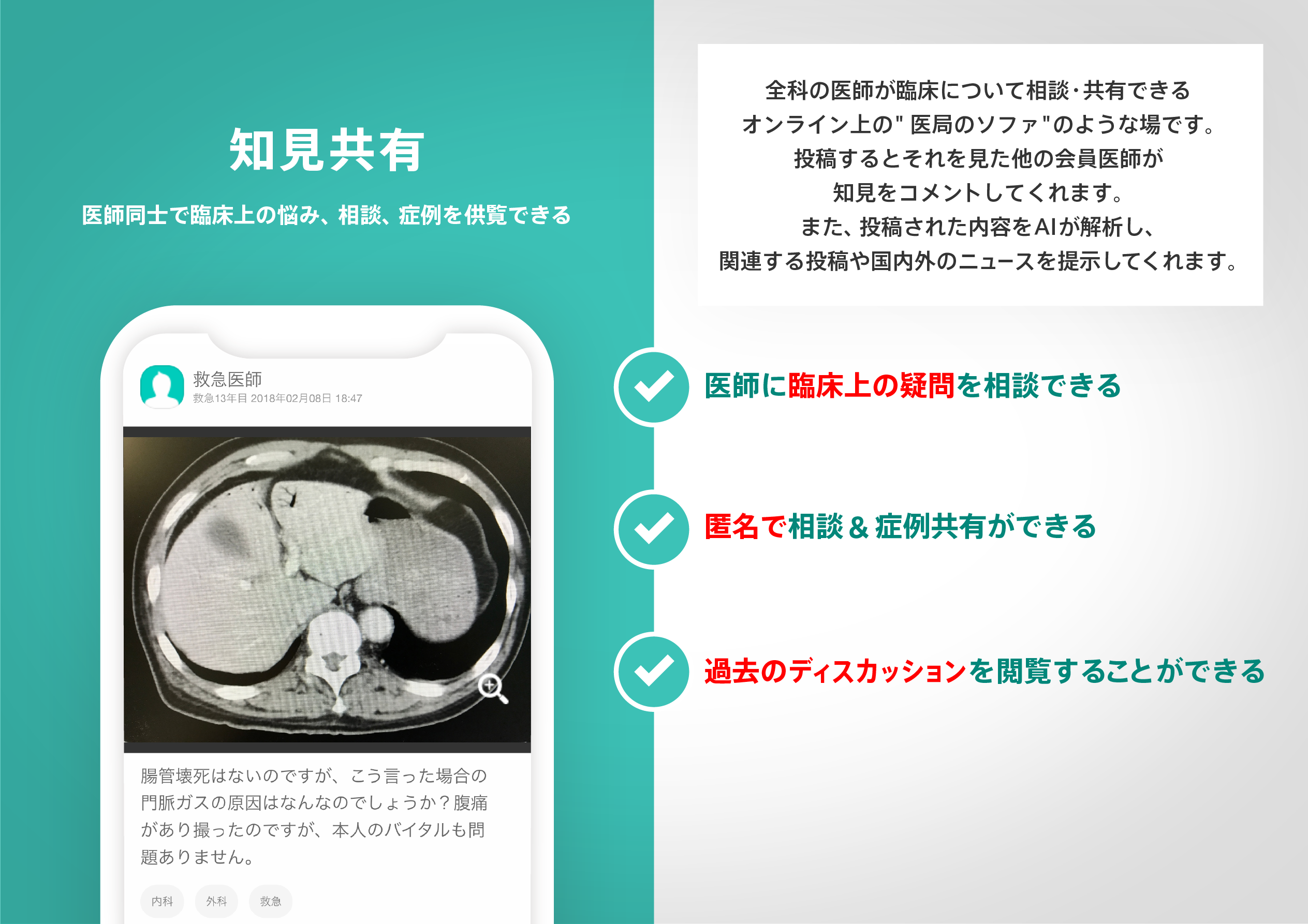
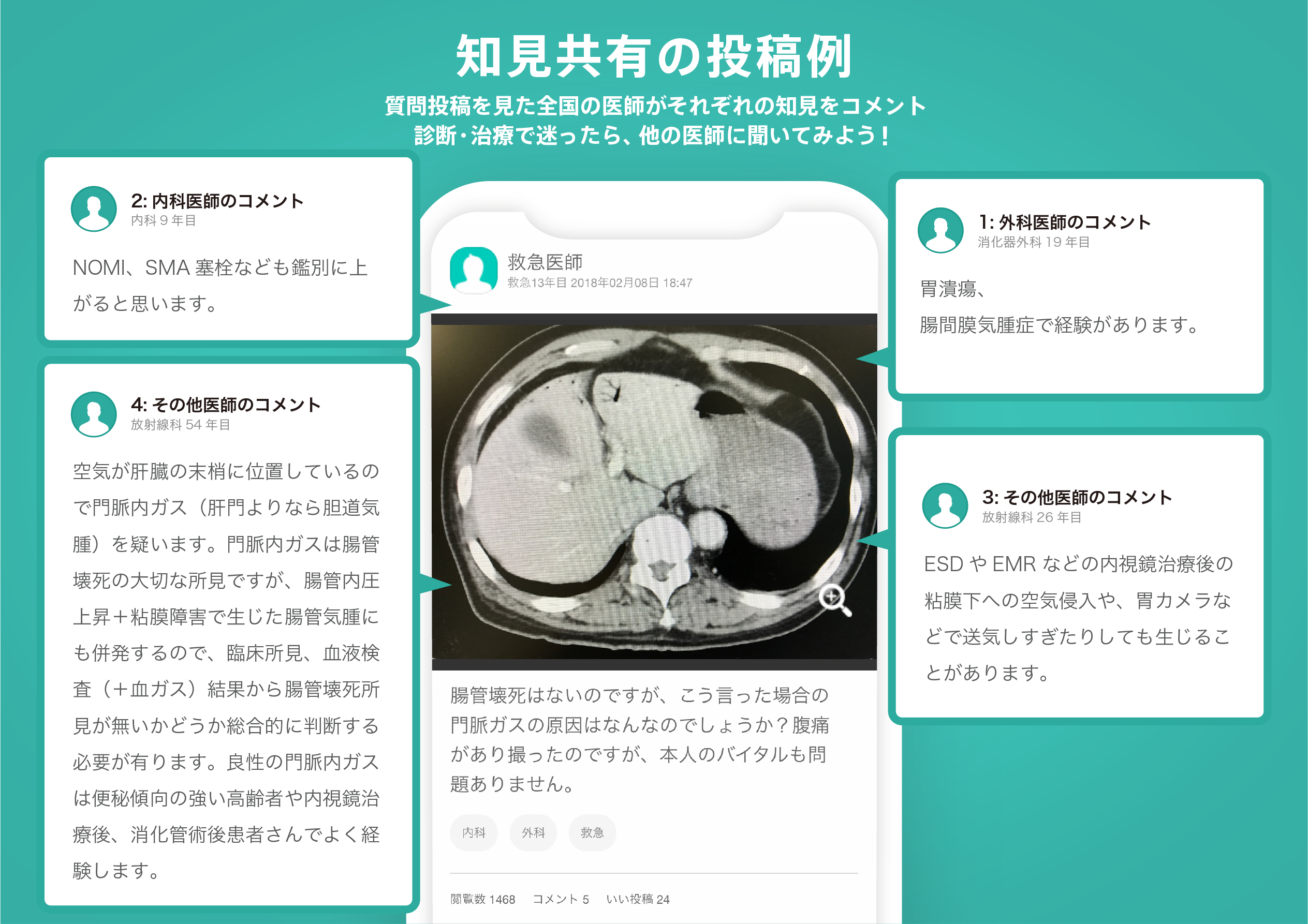
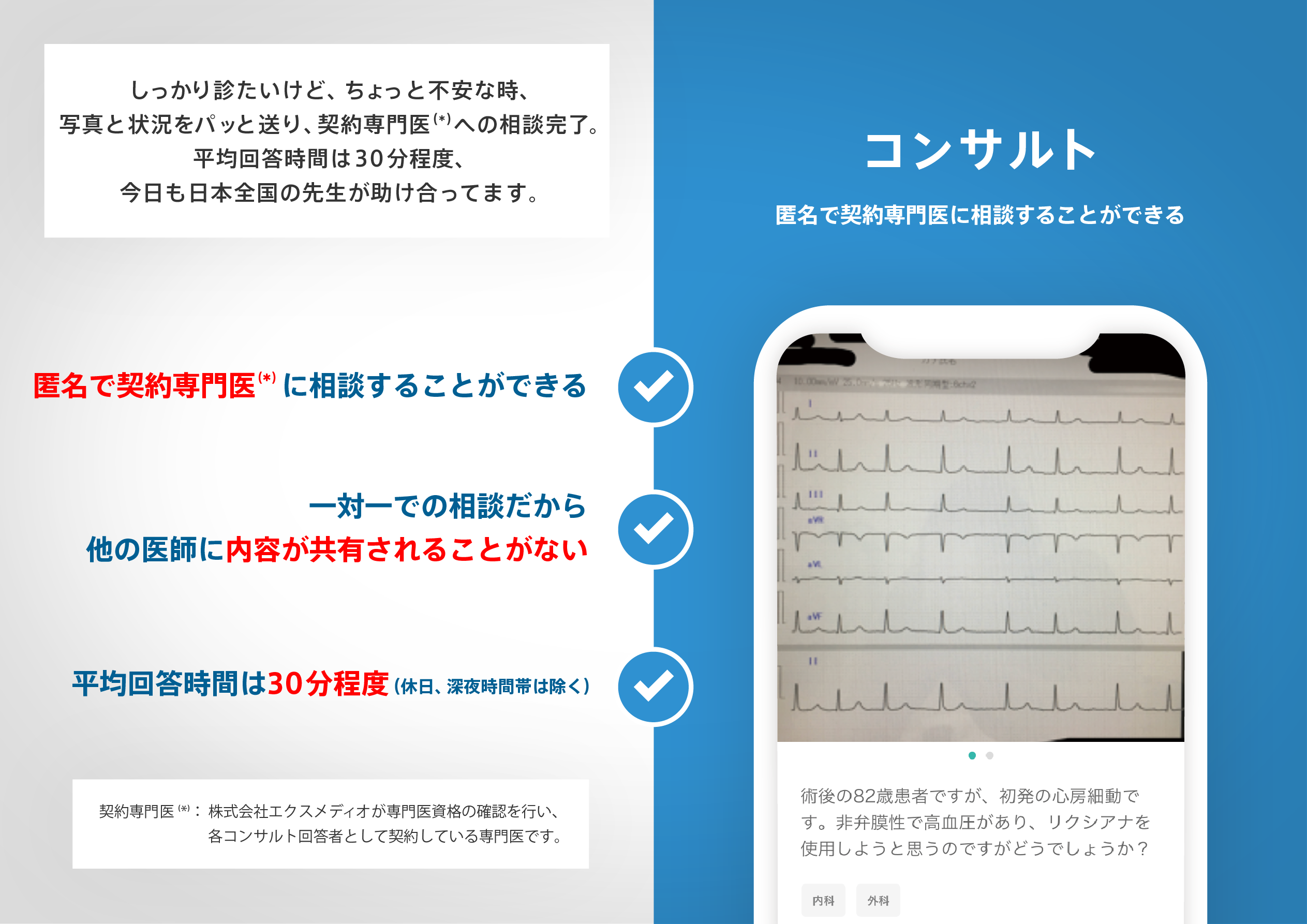
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。