著名医師による解説が無料で読めます
すると翻訳の精度が向上します
背景:多くのグラム陰性腸内菌は、毒性タンパク質(エフェクター)を腸上皮細胞に移動させ、III型分泌システム(T3SS)を使用して、さまざまな細胞機能の活性を覆します。多くのT3SSエフェクターは広範囲に特徴付けられていますが、機能的情報が完全に不明なエフェクタータンパク質がまだいくつかあります。 方法:この研究では、不明な機能の2つの予測エフェクターであるESPNとESPS(Escherichia coli分泌タンパク質NおよびS)が、転座、分布、および構造の予測の分析のために選択されました。 結果:TEM1(β-ラクタマーゼ)転座アッセイが実行され、ESPNとESPが細菌感染中にT3SS依存的に宿主細胞に移行することが示されました。系統樹の分析により、ESPNとESPのホモログは病原性細菌に広く分布していることが明らかになりました。複数のシーケンスアライメントにより、ESPNとそのホモログが保存されたC末端領域(673-1133 A.A.)を共有することが明らかになりました。さらに、ESPN(673-1133 A.A.)の構造も予測され、明確に定義されており、ループ領域で接続された3つのサブドメインがあることが示されました。ESPとそのホモログは、シーケンスに保存されたC末端(146-291 A.A.)を共有しています。ESPSの予測構造(146-291 A.A.)は、4つのβ鎖といくつかの短いヘリックスで構成されるβシートで構成されており、TMスコアが0.5014のVibrio cholerae RTXシステインプロテアーゼドメインの構造を備えています(PDBID:3eeb)。 結論:これらの結果は、ESPNとESPSが病原体の病原性に関連するT3SSエフェクターの2つの重要なクラスを表している可能性があることを示唆しており、我々の発見はESPNとESPの潜在的な機能を理解するための重要な手がかりを提供します。
背景:多くのグラム陰性腸内菌は、毒性タンパク質(エフェクター)を腸上皮細胞に移動させ、III型分泌システム(T3SS)を使用して、さまざまな細胞機能の活性を覆します。多くのT3SSエフェクターは広範囲に特徴付けられていますが、機能的情報が完全に不明なエフェクタータンパク質がまだいくつかあります。 方法:この研究では、不明な機能の2つの予測エフェクターであるESPNとESPS(Escherichia coli分泌タンパク質NおよびS)が、転座、分布、および構造の予測の分析のために選択されました。 結果:TEM1(β-ラクタマーゼ)転座アッセイが実行され、ESPNとESPが細菌感染中にT3SS依存的に宿主細胞に移行することが示されました。系統樹の分析により、ESPNとESPのホモログは病原性細菌に広く分布していることが明らかになりました。複数のシーケンスアライメントにより、ESPNとそのホモログが保存されたC末端領域(673-1133 A.A.)を共有することが明らかになりました。さらに、ESPN(673-1133 A.A.)の構造も予測され、明確に定義されており、ループ領域で接続された3つのサブドメインがあることが示されました。ESPとそのホモログは、シーケンスに保存されたC末端(146-291 A.A.)を共有しています。ESPSの予測構造(146-291 A.A.)は、4つのβ鎖といくつかの短いヘリックスで構成されるβシートで構成されており、TMスコアが0.5014のVibrio cholerae RTXシステインプロテアーゼドメインの構造を備えています(PDBID:3eeb)。 結論:これらの結果は、ESPNとESPSが病原体の病原性に関連するT3SSエフェクターの2つの重要なクラスを表している可能性があることを示唆しており、我々の発見はESPNとESPの潜在的な機能を理解するための重要な手がかりを提供します。
BACKGROUND: Many Gram-negative enterobacteria translocate virulence proteins (effectors) into intestinal epithelial cells using a type III secretion system (T3SS) to subvert the activity of various cell functions possess. Many T3SS effectors have been extensively characterized, but there are still some effector proteins whose functional information is completely unknown. METHODS: In this study, two predicted effectors of unknown function, EspN and EspS (Escherichia coli secreted protein N and S), were selected for analysis of translocation, distribution and structure prediction. RESULTS: The TEM1 (β-lactamase) translocation assay was performed, which showed that EspN and EspS are translocated into host cells in a T3SS-dependent manner during bacterial infection. A phylogenetic tree analysis revealed that homologs of EspN and EspS are widely distributed in pathogenic bacteria. Multiple sequence alignment revealed that EspN and its homologs share a conserved C-terminal region (673-1133 a.a.). Furthermore, the structure of EspN (673-1133 a.a.) was also predicted and well-defined, which showed that it has three subdomains connected by a loop region. EspS and its homologs share a sequence-conserved C-terminal (146-291 a.a.). The predicted structure of EspS (146-291 a.a.) is composed of a β-sheet consisting of four β-strands and several short helices, which has a TM score of 0.5014 with the structure of the Vibrio cholerae RTX cysteine protease domain (PDBID: 3eeb). CONCLUSIONS: These results suggest that EspN and EspS may represent two important classes of T3SS effectors associated with pathogen virulence, and our findings provide important clues to understanding the potential functions of EspN and EspS.
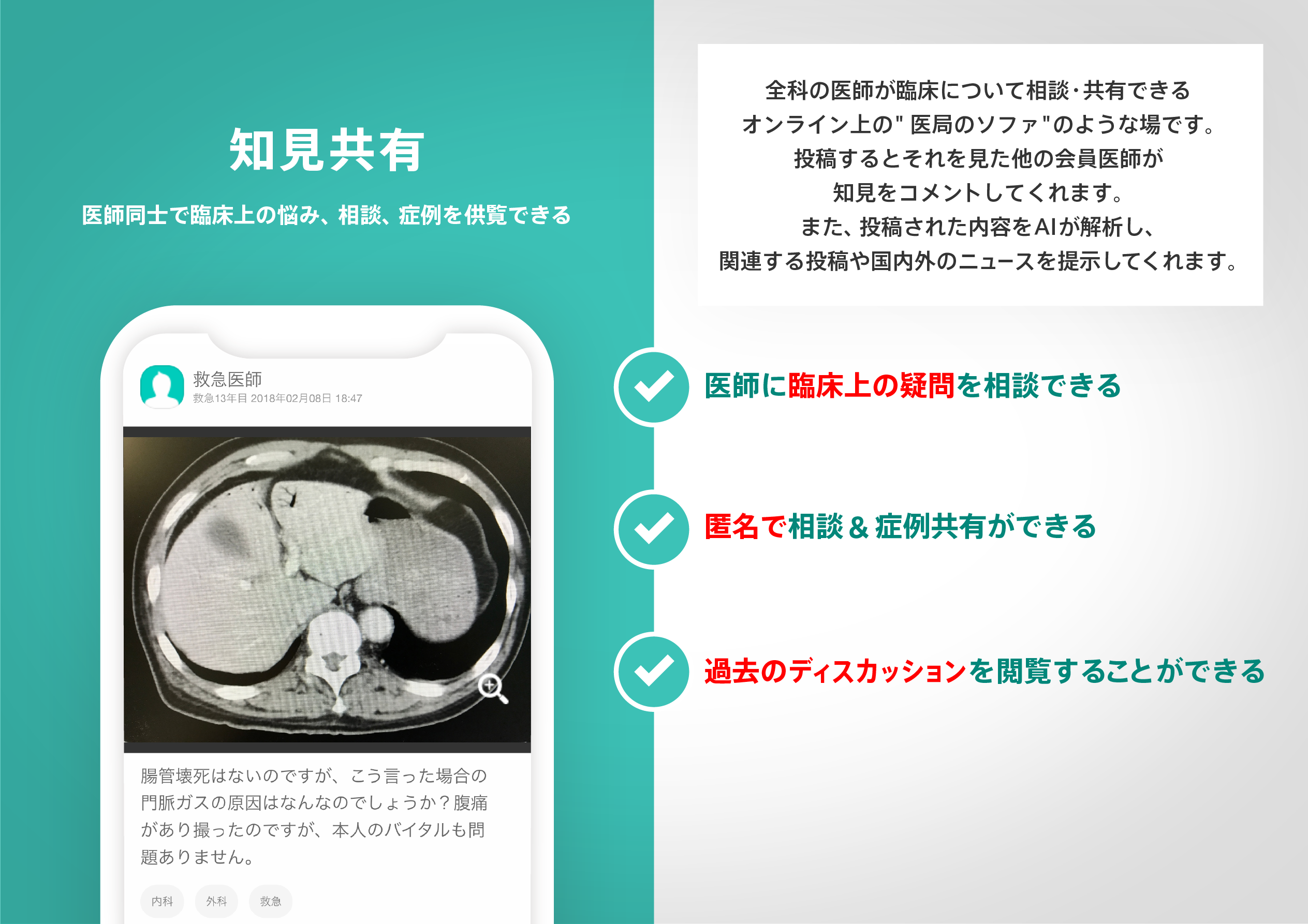
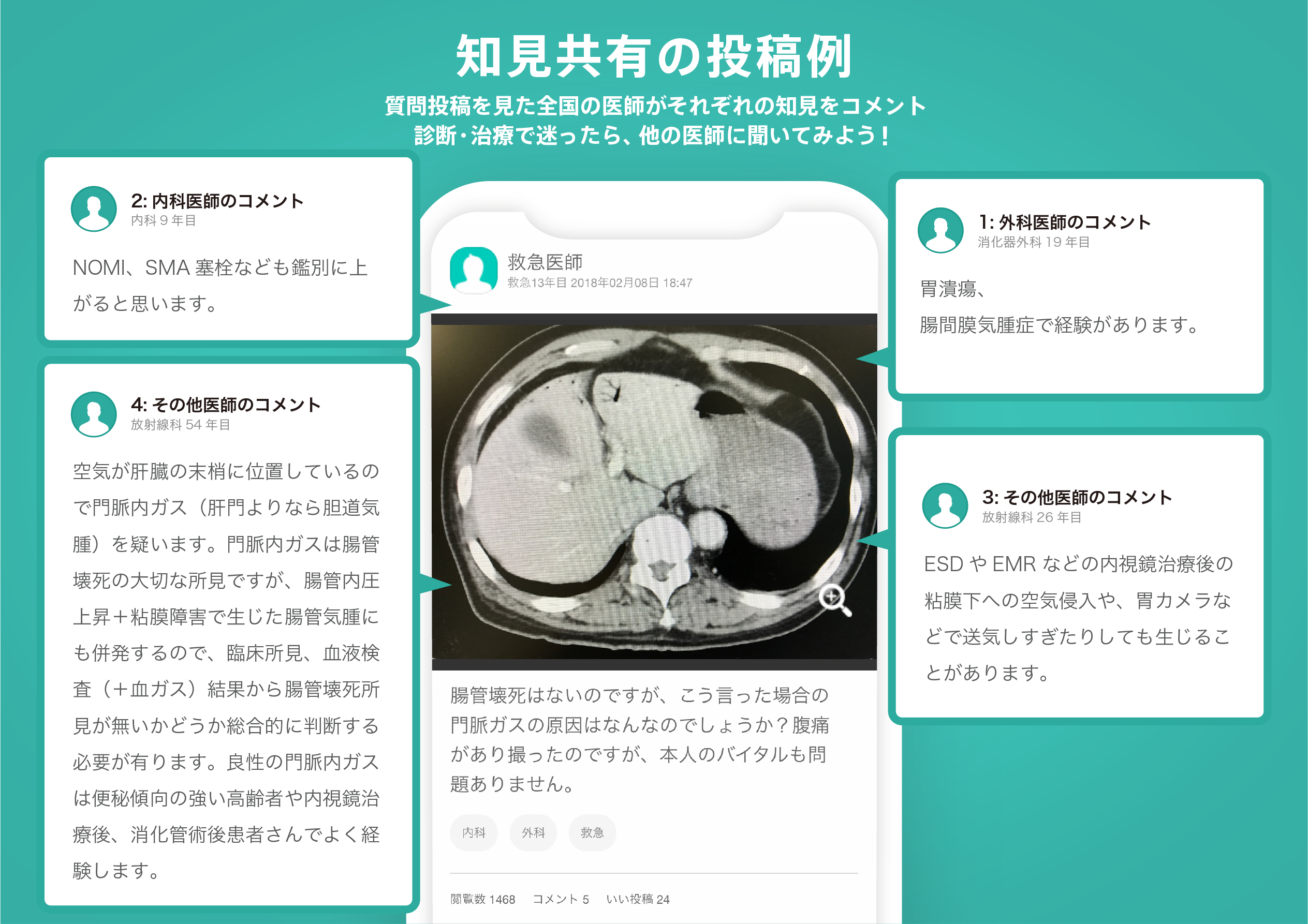
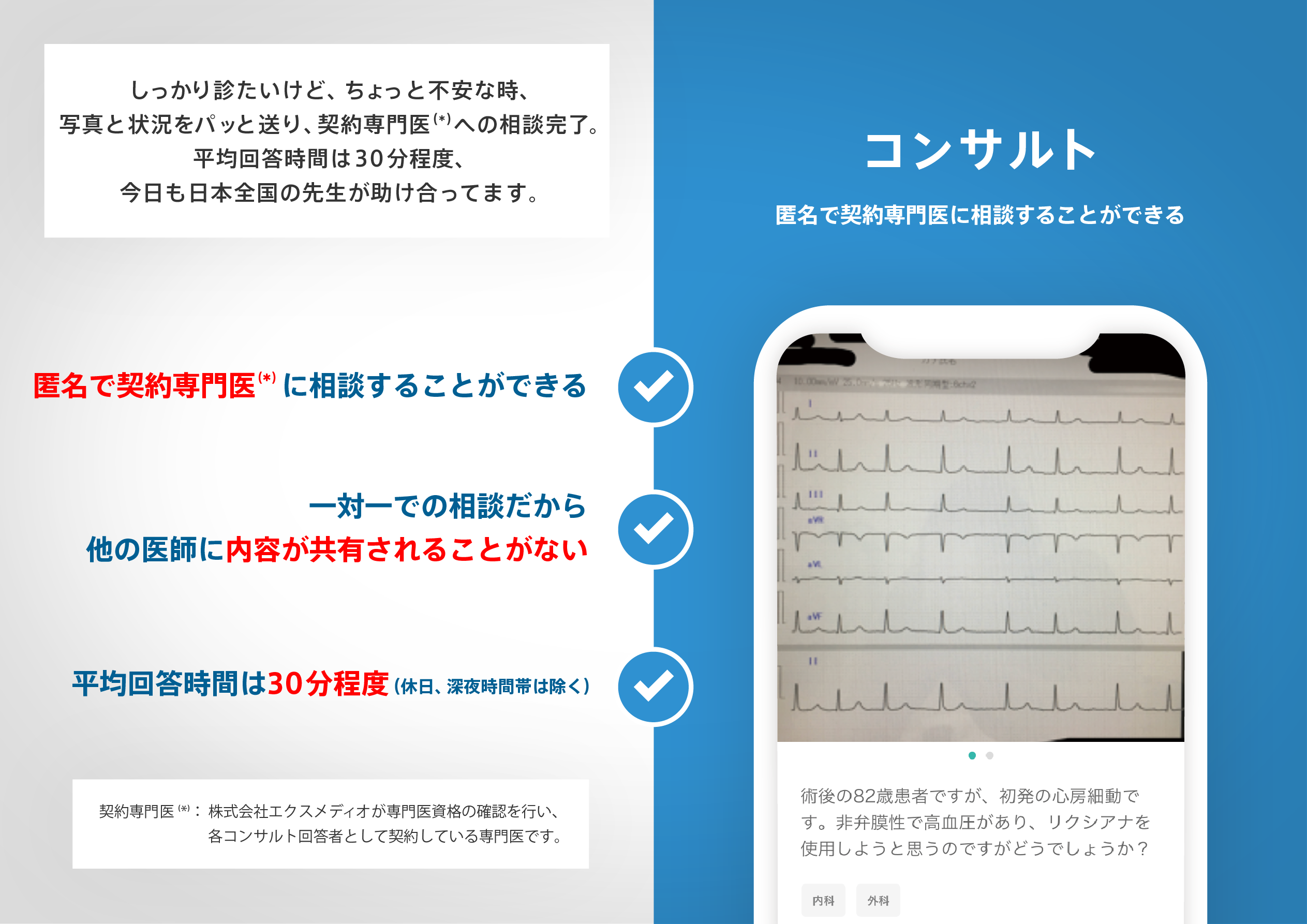
医師のための臨床サポートサービス
ヒポクラ x マイナビのご紹介
無料会員登録していただくと、さらに便利で効率的な検索が可能になります。